- 1. O TG-263 é a linguagem comum da radioterapia
- 2. O que é o TG-263
- 3. Problemas reais causados pela falta de padronização
- 4. Como aplicar o TG-263 na rotina clínica
- 5. Tabela completa de nomenclatura TG-263 717 estruturas
- 6. Integração com sistemas de planejamento e inteligência artificial
- 7. Fluxo de implementação em 10 passos
- 8. Relação com o delineamento de volumes-alvo
- 9. O futuro da padronização em radioterapia
- 10. Conclusão
O TG-263 é a linguagem comum da radioterapia
Um físico médico recebe um plano de tratamento exportado de outra instituição. Ao abrir o arquivo DICOM, encontra a parótida esquerda nomeada como Lt Parotid. No caso seguinte, vindo do mesmo serviço, o nome aparece como PAROTID_L. Em um terceiro paciente, parotid_left. E no template do próprio serviço receptor, a mesma estrutura consta como L_Parotid_Gland. Cinco nomes diferentes para o mesmo órgão de risco, dentro de um universo relativamente pequeno de casos.
Esse cenário não é hipotético. Ele reproduz dados reais coletados pela AAPM antes da publicação do TG-263. Em 20 instituições pesquisadas, a equipe encontrou entre 21 e 311 nomes definidos para estruturas anatômicas, com variações que iam desde abreviações pessoais até convenções inteiras criadas por um único profissional e nunca documentadas formalmente.
O problema parece pequeno quando se olha para um caso isolado. Mas se acumula rápido. Quando o serviço tenta automatizar revisão de DVH, treinar um modelo de auto-segmentação, consolidar dados para um estudo multicêntrico ou simplesmente comparar planos entre pacientes tratados em anos diferentes, a falta de padronização se transforma em retrabalho constante. Cada análise precisa de uma etapa prévia de “tradução” que consome tempo, introduz erros e impede automação real.
A AAPM reconheceu esse gargalo e, em 2012, montou o Task Group 263 com um mandato claro: criar um padrão de nomenclatura para estruturas anatômicas, volumes-alvo e métricas de DVH que pudesse ser adotado por qualquer serviço de radioterapia, independentemente de vendor, país ou porte operacional. O grupo reuniu 57 participantes — 33 físicos hospitalares, 15 médicos radioterapeutas, 8 representantes de fabricantes e 1 dosimetrista — e trabalhou por cinco anos até a publicação do relatório em janeiro de 2018.
O resultado não é apenas uma lista de nomes. O TG-263 define princípios de construção de nomenclatura, regras de lateralidade, convenções para volumes-alvo e seus níveis de dose, notação padronizada para métricas dosimétricas e um fluxo de implementação em 10 passos que permite a qualquer departamento adotar o padrão sem interromper a operação clínica.
Este guia cobre o conteúdo completo do relatório, inclui a tabela integral com as 717 estruturas não-alvo catalogadas, explica como os princípios se aplicam na prática diária e detalha a integração com sistemas de planejamento, ferramentas de inteligência artificial e workflows de pesquisa multicêntrica. O objetivo é funcionar como a referência em português para qualquer profissional que precise implementar, auditar ou expandir a nomenclatura TG-263 no seu serviço.
O que é o TG-263
O Task Group 263 da AAPM (American Association of Physicists in Medicine) nasceu da constatação de que a radioterapia precisava de um vocabulário técnico compartilhado para nomear estruturas anatômicas nos sistemas de planejamento de tratamento. Antes desse padrão, cada instituição desenvolvia suas próprias convenções — quando desenvolvia alguma. O resultado era uma fragmentação que dificultava qualquer atividade que dependesse de dados consistentes entre pacientes, equipamentos ou centros.
O grupo foi formalmente constituído em 2012 com membros indicados tanto pela AAPM quanto pela ASTRO (American Society for Radiation Oncology). A composição final incluiu 39 membros da AAPM e 41 da ASTRO, com sobreposição entre as duas sociedades, totalizando 57 participantes únicos. A diversidade do grupo não foi acidental: a presença de físicos, médicos, dosimetristas e representantes de fabricantes garantiu que o padrão fosse viável tanto do ponto de vista clínico quanto tecnológico.
O relatório foi publicado em janeiro de 2018 como AAPM Report No. 263, acompanhado por uma publicação peer-reviewed no Medical Physics (o artigo S0360 de 2018). O documento principal define os princípios; o material suplementar, disponível no site da AAPM, contém a planilha completa com todas as estruturas catalogadas.
A estrutura da planilha
O núcleo do TG-263 é uma planilha organizada em 9 colunas que classificam cada estrutura de forma sistemática. Essa organização não é arbitrária — cada coluna serve um propósito específico na cadeia de uso clínico e informático:
Target Type distingue se a estrutura é anatômica, um volume-alvo (GTV, CTV, PTV), um PRV ou uma estrutura derivada para planejamento. Major Category agrupa por sistema anatômico amplo — osso, nervo, órgão, vaso, linfonodo. Minor Category refina esse agrupamento com subcategorias mais específicas. Anatomic Group indica a região corporal: cabeça e pescoço, tórax, abdômen, pelve, corpo, membro.
N Characters registra o comprimento do nome padronizado, informação crítica porque o TG-263 recomenda um limite máximo de 16 caracteres para garantir compatibilidade com sistemas legados e campos de interface. TG263-Primary Name é o nome principal que deve ser usado no sistema de planejamento — por exemplo, Parotid_L para a parótida esquerda. TG-263-Reverse Order Name oferece uma versão invertida (L_Parotid) para facilitar busca e ordenação em listas extensas.
Description fornece o nome anatômico completo por extenso, sem abreviações. FMAID mapeia a estrutura para o Foundational Model of Anatomy, um ontologia anatômica mantida pela Universidade de Washington que permite interoperabilidade com SNOMED CT, DICOM e outros padrões informáticos em saúde.
Primary Name versus Reverse Order Name
A distinção entre esses dois campos é um dos conceitos mais importantes do TG-263 e frequentemente mal compreendida. O Primary Name segue a lógica Estrutura_Lateralidade — por exemplo, Kidney_L, Femur_R, CN_VII_L. Esse formato facilita a leitura humana e segue a convenção natural de nomear primeiro a estrutura e depois qualificá-la.
O Reverse Order Name inverte para Lateralidade_Estrutura — L_Kidney, R_Femur, L_CN_VII. Esse formato é útil quando a lista de estruturas precisa ser ordenada alfabeticamente por lateralidade, agrupando todas as estruturas esquerdas e todas as direitas juntas. Alguns sistemas de planejamento e ferramentas de análise se beneficiam dessa ordenação para revisão rápida.
O TG-263 recomenda que o Primary Name seja usado como nome preferencial no TPS. O Reverse Order Name existe como alternativa documentada, não como substituto. Serviços que adotam o padrão devem escolher uma das convenções e aplicá-la de forma consistente em toda a operação.
Escopo: 717 estruturas não-alvo
A planilha cataloga 717 estruturas não-alvo, organizadas em 7 grupos anatômicos: Cabeça e Pescoço (282), Tórax (180), Abdômen (60), Pelve (109), Corpo/Sistêmico (52), Membro singular (16) e Membros bilaterais (17). A planilha completa pode ser baixada diretamente do material suplementar do TG-263 no site da AAPM. Esse catálogo cobre praticamente toda estrutura anatômica que um serviço de radioterapia encontra na prática clínica, desde ossos e nervos cranianos até vasos, linfonodos, órgãos abdominais e estruturas pélvicas.
Além das estruturas anatômicas, o TG-263 define convenções separadas para volumes-alvo (GTV, CTV, ITV, PTV e suas variantes), estruturas de planejamento (PRV, estruturas auxiliares com prefixo z), e métricas dosimétricas (DVH). Esses três domínios seguem princípios próprios, detalhados nas seções seguintes deste guia.
Problemas reais causados pela falta de padronização
O TG-263 não surgiu de uma preocupação teórica. Antes de definir qualquer padrão, o grupo conduziu um levantamento em 20 instituições norte-americanas para documentar o estado real da nomenclatura em radioterapia. Os resultados foram reveladores.
Das 20 instituições pesquisadas, 16 declararam ter alguma forma de nomenclatura definida para pelo menos alguns sítios de doença. Mas “ter nomenclatura” não significava ter consistência. O número de estruturas definidas variava de 21 a 311 entre as instituições, e dentro de cada uma havia variações entre profissionais, entre salas e entre períodos. Nenhuma das 20 cobria todas as estruturas anatômicas necessárias para todas as modalidades de tratamento.
O exemplo mais citado no relatório é o do nervo óptico esquerdo. Ao coletar os nomes usados pelas instituições pesquisadas, o grupo encontrou 12 variantes para uma única estrutura: Lt Optic Nerve, L_Optic_Nerve, OpticNrv_L, Optic_Nerve_Left, entre outras. Cada variante era internamente lógica para quem a criou, mas incompatível com as demais quando os dados precisavam ser combinados.
Impacto na mineração de dados
Um serviço que acumula 10 anos de planos de tratamento possui um acervo valioso para pesquisa, benchmarking e melhoria de qualidade. Mas se esses planos usam nomes inconsistentes para as mesmas estruturas, qualquer consulta ao banco de dados se torna um exercício de mapeamento manual. Extrair “todas as doses médias na medula espinhal” exige primeiro identificar se a medula foi nomeada como SpinalCord, Spinal_Cord, SC, MedulaEspinhal, Cord ou qualquer outra variação local.
Esse custo de mapeamento não é trivial. Em estudos multicêntricos com milhares de pacientes, a etapa de harmonização de nomenclatura pode consumir semanas de trabalho e ainda assim conter erros. O TG-263 elimina esse problema na origem: se todos os centros usam SpinalCord, a consulta ao banco retorna resultados completos sem intervenção manual.
Impacto na auto-segmentação e IA
Modelos de deep learning para auto-segmentação precisam de dados de treinamento rotulados de forma consistente. Um modelo treinado com contornos rotulados como Parotid_L não consegue usar automaticamente dados rotulados como Lt_Parotid_Gland — o mapeamento precisa ser feito manualmente para cada variante, e qualquer erro nesse mapeamento contamina o treinamento.
Quando um serviço adota a nomenclatura TG-263, seus dados se tornam imediatamente compatíveis com modelos treinados em outros serviços que seguem o mesmo padrão. Isso acelera a adoção de auto-segmentação, melhora a qualidade do treinamento por permitir datasets maiores e viabiliza a validação cruzada entre instituições.
Impacto na automação de QA
Protocolos automatizados de garantia de qualidade dependem de nomes previsíveis. Um script que verifica se a dose máxima no cristalino não excede o limite institucional precisa saber exatamente como o cristalino está nomeado. Se o nome muda entre Lens_L, L_Lens, Left_Lens e Cristalino_E, o script precisa de uma tabela de sinônimos que cresce a cada nova variante encontrada — ou, pior, falha silenciosamente quando encontra um nome não catalogado.
O TG-263 permite que ferramentas de QA sejam escritas uma vez e funcionem em qualquer serviço aderente. A previsibilidade dos nomes é a base para automação confiável.
Impacto em estudos multicêntricos e ensaios clínicos
Ensaios clínicos de radioterapia que coletam dados dosimétricos de múltiplas instituições enfrentam o problema de nomenclatura em escala. O RTOG (agora NRG Oncology) publicou diretrizes de nomenclatura para estudos específicos, mas sem um padrão universal adotado pela comunidade, cada novo ensaio repetia o mesmo ciclo de definição, comunicação e verificação. O TG-263 oferece uma base permanente que reduz esse overhead para qualquer ensaio futuro. A padronização de nomenclatura também facilita a integração DICOM entre sistemas de diferentes fabricantes.
Como aplicar o TG-263 na rotina clínica
O TG-263 define dois conjuntos de princípios: 15 para estruturas não-alvo (órgãos de risco e estruturas anatômicas) e 10 para volumes-alvo. Além disso, padroniza a notação de métricas dosimétricas. Cada conjunto foi projetado para resolver problemas específicos da prática clínica.
Princípios para estruturas não-alvo
Limite de 16 caracteres. O nome padronizado não deve exceder 16 caracteres. Esse limite não é arbitrário — reflete restrições reais de campos de interface em sistemas de planejamento legados e contemporâneos. Nomes mais longos são truncados por alguns TPS, gerando ambiguidade. O limite força concisão e impede proliferação de nomes descritivos longos que ninguém digita de forma idêntica duas vezes.
Unicidade por case. Cada nome deve ser único independentemente de maiúsculas e minúsculas. Brainstem e brainstem não podem coexistir como estruturas distintas. Essa regra previne erros em sistemas que ignoram case na busca ou ordenação.
Sem espaços, underscore como separador. Espaços são proibidos em nomes TG-263. O separador padrão é o underscore (_). Assim, Optic_Nerve_L e não Optic Nerve L. Essa convenção evita problemas com parsers, scripts e interfaces que tratam espaços como delimitadores de campo.
Sufixos de lateralidade: _L, _R, _A, _P. Estruturas lateralizadas recebem o sufixo correspondente ao final do nome. O padrão usa letras únicas para esquerda (_L), direita (_R), anterior (_A) e posterior (_P). Estruturas bilaterais sem lateralidade definida usam o plural — por exemplo, Kidneys para ambos os rins, Kidney_L e Kidney_R para cada um individualmente.
Raízes de categoria. Estruturas de categorias específicas usam prefixos padronizados que facilitam agrupamento e busca:
A_ para artérias (A_Carotid_L), V_ para veias (V_Jugular_R), LN_ para linfonodos (LN_Ax_L1_L), CN_ para nervos cranianos (CN_VII_L), Bone_ para ossos (Bone_Mandible), Musc_ para músculos (Musc_Masseter_L). Esses prefixos garantem que todas as artérias fiquem agrupadas na lista, todos os linfonodos juntos, e assim por diante.
Estruturas PRV. Planning Risk Volumes (PRV) seguem a convenção Estrutura_PRV para margem genérica ou Estrutura_PRVxx onde xx indica a margem em milímetros. Exemplos: Brainstem_PRV para um PRV do tronco encefálico com margem não especificada, SpinalCord_PRV05 para um PRV da medula com expansão de 5 mm. Essa convenção permite que qualquer profissional identifique imediatamente a estrutura base e a margem aplicada sem consultar documentação externa.
Estruturas parciais: o til (~). Quando apenas parte de uma estrutura é delineada, o TG-263 usa o til como sufixo: Brain~ para cérebro parcial, Lung~_L para pulmão esquerdo parcial. Essa situação é comum em tratamentos onde o campo de aquisição ou de tratamento não cobre a estrutura inteira — o til sinaliza explicitamente que a cobertura é incompleta, evitando que métricas de DVH sejam interpretadas como representativas do órgão inteiro.
Estruturas de planejamento: prefixo z. Estruturas criadas exclusivamente para otimização de plano — anéis, estruturas de subtração, auxiliares de dose — recebem o prefixo z para ficarem no final da lista alfabética e não se misturarem com estruturas anatômicas reais. Exemplos: zPTVopt, zRing, zBolus. A convenção é simples e eficaz: quando um físico varre a lista de estruturas, tudo que começa com z é auxiliar de planejamento e pode ser filtrado ou ignorado conforme o contexto.
Princípios para volumes-alvo
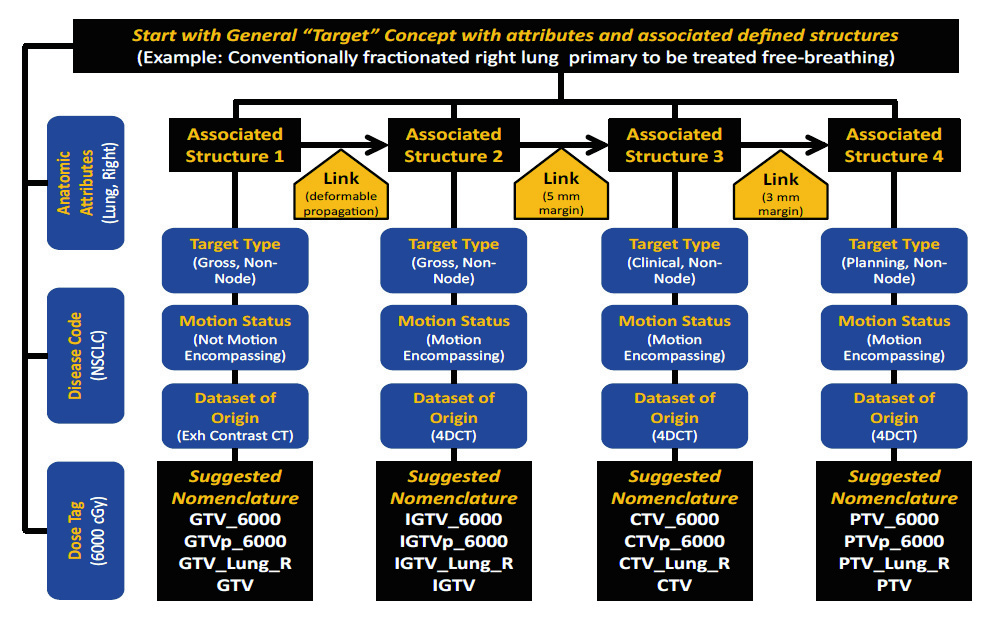
A nomenclatura de volumes-alvo segue 10 princípios construídos para refletir a hierarquia clínica entre volume bruto de doença, volume clínico, margens internas e volume de planejamento.
Tipos de volume. O TG-263 define os seguintes tipos: GTV (Gross Tumor Volume), CTV (Clinical Target Volume), ITV (Internal Target Volume), IGTV (Internal Gross Target Volume), ICTV (Internal Clinical Target Volume), PTV (Planning Target Volume) e PTV! (PTV de avaliação, desvinculado de restrições de otimização). Cada tipo ocupa uma posição precisa na cadeia de derivação clínica.
Classificadores. Volumes podem receber classificadores que indicam a natureza da doença: n para nodal (GTV_n), p para primário (CTV_p), sb para leito cirúrgico (CTV_sb), par para parenquimatoso. Esses classificadores se combinam com o tipo de volume e permitem identificar a origem clínica sem ambiguidade. Um plano com GTV_p, GTV_n, CTV_p e CTV_n comunica em quatro nomes toda a estratégia de cobertura do tumor primário e da doença nodal.
Níveis de dose. Quando o plano prescreve doses diferentes para volumes distintos, o TG-263 permite indicar o nível no nome: PTV_High, PTV_Low, PTV_Mid para níveis relativos, ou PTV_5040 para dose absoluta em cGy. Essa convenção é particularmente útil em planos SIB (Simultaneous Integrated Boost), onde três ou mais níveis de dose coexistem e a clareza sobre qual PTV recebe qual prescrição é crítica para a segurança do tratamento.
Composição de nomes-alvo. Os elementos se combinam em uma lógica previsível: Tipo_Classificador_NivelDose. Assim, PTV_n_High identifica inequivocamente o volume de planejamento nodal que recebe a dose mais alta. CTV_sb_Low é o volume clínico do leito cirúrgico no nível de dose baixa. A composição é modular e extensível sem violar as regras de construção.
Nomenclatura de métricas dosimétricas (DVH)

O TG-263 padroniza a forma de escrever métricas de DVH para eliminar ambiguidade. A notação segue o formato MetricaValorUnidade[UnidadeResultado]:
V20Gy[%] — volume que recebe pelo menos 20 Gy, expresso em porcentagem. V20Gy[cc] — o mesmo volume, expresso em centímetros cúbicos. D0.1cc[Gy] — dose que cobre pelo menos 0,1 cc do volume, em Gy. D95%[Gy] — dose no ponto que cobre 95% do volume. Mean[Gy] — dose média no volume. Max[Gy] — dose máxima pontual.
Essa notação resolve um problema crônico: a mesma métrica escrita de formas diferentes (V20, V_20Gy, V20_pct, Vol_20Gy_%) em relatórios, protocolos e scripts. Com o padrão TG-263, um script que calcula V20Gy[%] produz uma saída legível por qualquer outro script ou profissional que conheça a convenção.
Tabela completa de nomenclatura TG-263
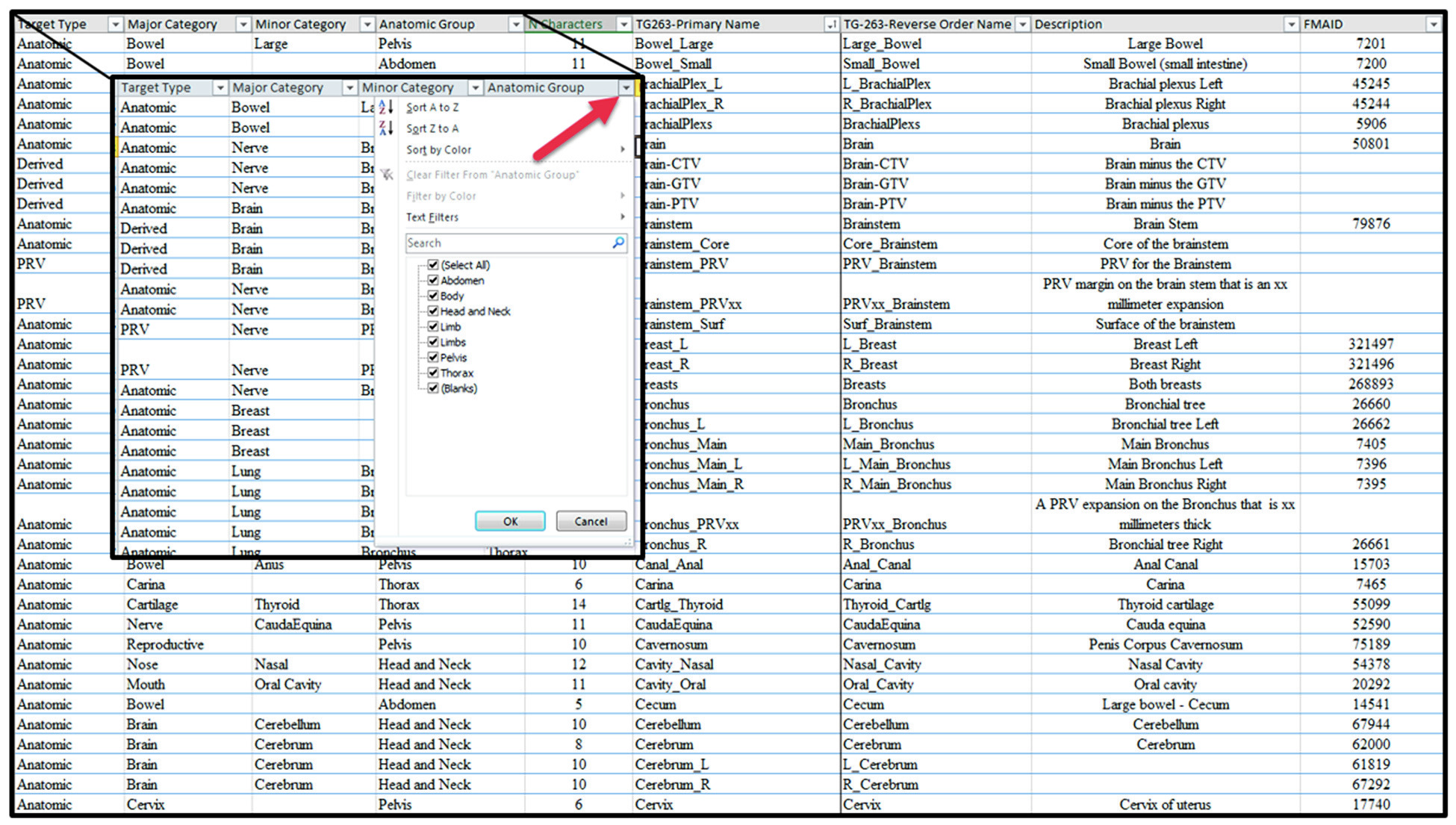
A tabela abaixo reúne as 717 estruturas não-alvo catalogadas pelo TG-263, organizadas em 7 grupos anatômicos. Use o campo de busca para localizar rapidamente qualquer estrutura por nome, categoria ou região. Os nomes seguem o formato TG263-Primary Name da planilha oficial; a coluna FMAID indica o identificador no Foundational Model of Anatomy quando disponível.
Cabeça e Pescoço (Head and Neck) — 282 estruturas
| Nome TG-263 | Tipo | Categoria | Descrição | FMAID |
|---|---|---|---|---|
| A_Carotid | Anatomic | Artery | Common Carotid Artery | 3939 |
| A_Carotid_L | Anatomic | Artery | Carotid Artery | 4058 |
| A_Carotid_R | Anatomic | Artery | Carotid Artery | 3941 |
| A_Coronary | Anatomic | Artery | Coronary Artery | 49893 |
| A_Hypophyseal_I | Anatomic | Artery | Hypophyseal Artery Inferior | 49846 |
| A_Hypophyseal_S | Anatomic | Artery | Hypophyseal Artery Superior | 49849 |
| Arytenoid | Anatomic | Cartilage | Arytenoid cartilage | 55109 |
| Arytenoid_L | Anatomic | Cartilage | Arytenoid cartilage Left | 55114 |
| Arytenoid_R | Anatomic | Cartilage | Arytenoid cartilage Right | 55113 |
| Bone_Ethmoid | Anatomic | Bone | Ethmoid Bone | 52740 |
| Bone_Frontal | Anatomic | Bone | Frontal Bone | 52734 |
| Bone_Hyoid | Anatomic | Bone | Hyoid Bone | 52749 |
| Bone_Incus | Anatomic | Ear | Incus | 52752 |
| Bone_Incus_L | Anatomic | Ear | Incus Left | 74051 |
| Bone_Incus_R | Anatomic | Ear | Incus Right | 74050 |
| Bone_Lacrimal | Anatomic | Bone | Lacrimal Bone | 52741 |
| Bone_Lacrimal_L | Anatomic | Bone | Lacrimal Bone Left | 53646 |
| Bone_Lacrimal_R | Anatomic | Bone | Lacrimal Bone Right | 53645 |
| Bone_Mandible | Anatomic | Bone | Mandible | 52748 |
| Bone_Mastoid | Anatomic | Bone | Both Mastoids | 52872 |
| Bone_Mastoid_L | Anatomic | Bone | Left Mastoid Bone | 52874 |
| Bone_Mastoid_R | Anatomic | Bone | Right Mastoid Bone | 52873 |
| Bone_Nasal | Anatomic | Bone | Nasal Bone | 52745 |
| Bone_Nasal_L | Anatomic | Bone | Nasal Bone Left | 53648 |
| Bone_Nasal_R | Anatomic | Bone | Nasal Bone Right | 53647 |
| Bone_Occipital | Anatomic | Bone | Occipital Bone | 52735 |
| Bone_Palatine | Anatomic | Bone | Palatine bone | 52746 |
| Bone_Palatine_L | Anatomic | Bone | Palatine bone Left | 53656 |
| Bone_Palatine_R | Anatomic | Bone | Palatine bone Right | 53655 |
| Bone_Parietal | Anatomic | Bone | Parietal bone | 9613 |
| Bone_Parietal_L | Anatomic | Bone | Parietal bone Left | 52789 |
| Bone_Parietal_R | Anatomic | Bone | Parietal bone Right | 52788 |
| Bone_Sphenoid | Anatomic | Bone | Sphenoid Bone | 52736 |
| Bone_Temporal | Anatomic | Bone | Temporal Bone | 52737 |
| Bone_Temporal_L | Anatomic | Bone | Temporal Bone Left | 52739 |
| Bone_Temporal_R | Anatomic | Brain | Temporal Bone Right | 52738 |
| Bone_Zygomatic_L | Anatomic | Bone | Zygomatic Bone Left | 52893 |
| Bone_Zygomatic_R | Anatomic | Bone | Zygomatic Bone Right | 52892 |
| Bone_Zygomatics | Anatomic | Bone | Zygomatic Bone | 52747 |
| Brain | Anatomic | Brain | Brain | 50801 |
| Brain-CTV | Derived | Brain | Brain minus the CTV | — |
| Brain-GTV | Derived | Brain | Brain minus the GTV | — |
| Brain-PTV | Derived | Brain | Brain minus the PTV | — |
| Brainstem | Anatomic | Nerve | Brain Stem | 79876 |
| Brainstem_Core | Anatomic | Nerve | Core of the brainstem | — |
| Brainstem_PRV | PRV | Nerve | PRV for the Brainstem | — |
| Brainstem_PRVxx | PRV | Nerve | PRV margin on the brain stem that is an xx millimeter expansion | — |
| Brainstem_Surf | Anatomic | Nerve | Surface of the brainstem | — |
| Cavity_Nasal | Anatomic | Nose | Nasal Cavity | 54378 |
| Cavity_Oral | Anatomic | Mouth | Oral cavity | 20292 |
| Cerebellum | Anatomic | Brain | Cerebellum | 67944 |
| Cerebrum | Anatomic | Brain | Cerebrum | 62000 |
| Cerebrum_L | Anatomic | Brain | 61819 | |
| Cerebrum_R | Anatomic | Brain | 67292 | |
| Cist_Pontine | Anatomic | Brain | Pontine Cistern | 83719 |
| Cist_Suprasellar | Anatomic | Brain | — | |
| CN_III | Anatomic | Nerve | Third Cranial Nerve (Oculomotor nerve) | 50864 |
| CN_III_L | Anatomic | Nerve | Third Cranial Nerve (Oculomotor nerve) Left | 50880 |
| CN_III_R | Anatomic | Nerve | Third Cranial Nerve (Oculomotor nerve) Right | 50879 |
| CN_IX | Anatomic | Nerve | Ninth Cranial Nerve (Glossopharyngeal nerve) | 50870 |
| CN_IX_L | Anatomic | Nerve | Ninth Cranial Nerve (Glossopharyngeal nerve) Left | 50892 |
| CN_IX_R | Anatomic | Nerve | Ninth Cranial Nerve (Glossopharyngeal nerve) Right | 50870 |
| CN_V | Anatomic | Nerve | Fifth Cranial Nerve (Trigeminal nerve) | 50866 |
| CN_V_L | Anatomic | Nerve | Fifth Cranial Nerve (Trigeminal nerve) Left | 50885 |
| CN_V_R | Anatomic | Nerve | Fifth Cranial Nerve (Trigeminal nerve) Right | 50884 |
| CN_VI | Anatomic | Nerve | Sixth Cranial Nerve (Abducens nerve) | 50867 |
| CN_VI_L | Anatomic | Nerve | Sixth Cranial Nerve (Abducens nerve) Left | 50887 |
| CN_VI_R | Anatomic | Nerve | Sixth Cranial Nerve (Abducens nerve) Right | 50886 |
| CN_VII | Anatomic | Nerve | Seventh Cranial Nerve (Facial) | 50868 |
| CN_VII_L | Anatomic | Nerve | Seventh Cranial Nerve (Facial) Left | 50889 |
| CN_VII_R | Anatomic | Nerve | Seventh Cranial Nerve (Facial) Right | 50888 |
| CN_VIII | Anatomic | Nerve | Eighth Cranial (Vestibulocochlear) Nerve | 50869 |
| CN_VIII_L | Anatomic | Nerve | Eighth Cranial (Vestibulocochlear) Nerve Left | 50891 |
| CN_VIII_R | Anatomic | Nerve | Eighth Cranial (Vestibulocochlear) Nerve Right | 50890 |
| CN_XI | Anatomic | Nerve | Eleventh Cranial Nerve (Spinal accessory nerve) | 6720 |
| CN_XI_L | Anatomic | Nerve | Eleventh Cranial Nerve (Spinal accessory nerve) Left | 50899 |
| CN_XI_R | Anatomic | Nerve | Eleventh Cranial Nerve (Spinal accessory nerve) Right | 50897 |
| CN_XII | Anatomic | Nerve | Twelfth Cranial Nerve (Hypoglossal nerve) | 50871 |
| CN_XII_L | Anatomic | Nerve | Twelfth Cranial Nerve (Hypoglossal nerve) Left | 50903 |
| CN_XII_R | Anatomic | Nerve | Twelfth Cranial Nerve (Hypoglossal nerve) Right | 50901 |
| Cochlea | Anatomic | Ear | Cochlea | 60201 |
| Cochlea_L | Anatomic | Ear | Left Cochlea | 60203 |
| Cochlea_R | Anatomic | Ear | Right Cochlea | 60202 |
| Cornea | Anatomic | Eye | Cornea | 58238 |
| Cornea_L | Anatomic | Eye | Cornea Left | 58240 |
| Cornea_R | Anatomic | Eye | Cornea Right | 58239 |
| CribriformPlate | Anatomic | Bone | Cribriform Plate | 52890 |
| Cricoid | Anatomic | Cartilage | Cricoid cartilage | 9615 |
| Cricopharyngeus | Anatomic | Pharynx | Cricopharyngeal part of inferior pharyngeal constrictor | 46661 |
| Dens | Anatomic | Bone | Cervical vertebrae – Bony part of dens of axis | 24043 |
| Ear_External_L | Anatomic | Ear | External Ear Left | 53644 |
| Ear_External_R | Anatomic | Ear | External Ear Right | 53643 |
| Ear_Externals | Anatomic | Ear | External Ear | 52781 |
| Ear_Internal_L | Anatomic | Ear | Internal Ear Left | 61021 |
| Ear_Internal_R | Anatomic | Ear | Internal Ear Right | 61020 |
| Ear_Internals | Anatomic | Ear | Internal Ear | 60909 |
| Ear_Middle | Anatomic | Ear | Middle Ear | 56513 |
| Ear_Middle_L | Anatomic | Ear | Middle Ear Left | 56515 |
| Ear_Middle_R | Anatomic | Ear | Middle Ear Right | 56514 |
| Eye_L | Anatomic | Eye | Eyeball Left | 12515 |
| Eye_R | Anatomic | Eye | Eyeball Right | 12514 |
| Eyes | Anatomic | Eye | Set of eyes | 268861 |
| Fossa_Jugular | Anatomic | Bone | Jugular Fossa | 56429 |
| Fossa_Posterior | Anatomic | Bone | Posterior Fossa | 54368 |
| Glnd_Lacrimal | Anatomic | Gland | Lacrimal Gland | 59101 |
| Glnd_Lacrimal_L | Anatomic | Gland | Lacrimal Gland Left | 59103 |
| Glnd_Lacrimal_R | Anatomic | Gland | Lacrimal Gland Right | 59102 |
| Glnd_Subling_L | Anatomic | Gland | Sublingual gland | 59805 |
| Glnd_Subling_R | Anatomic | Gland | Sublingual gland | 59804 |
| Glnd_Sublings | Anatomic | Gland | Sublingual gland | 320440 |
| Glnd_Submand_L | Anatomic | Gland | Submandibular Gland Left | 59803 |
| Glnd_Submand_R | Anatomic | Gland | Submandibular Gland Right | 59802 |
| Glnd_Submands | Anatomic | Gland | Submandibular Gland | 320442 |
| Glottis | Anatomic | Glottis | Glottis | 55414 |
| Hardpalate | Anatomic | Head | Hard palate | 55023 |
| Hemisphere_L | Anatomic | Brain | 61819 | |
| Hemisphere_R | Anatomic | Brain | 67292 | |
| Hemispheres | Anatomic | Brain | — | |
| Hippocampi | Anatomic | Brain | Hippocampus | 275020 |
| Hippocampus_L | Anatomic | Brain | Hippocampus Left | 275024 |
| Hippocampus_R | Anatomic | Brain | Hippocampus Right | 275022 |
| Hypothalmus | Anatomic | Brain | Hypothalamus | 62008 |
| Hypothalmus_PRV | PRV | Brain | — | |
| Hypothalmus_PRVx | PRV | Brain | — | |
| Joint_TM | Anatomic | Joint | Temperomandibular Joint | 54832 |
| Joint_TM_L | Anatomic | Joint | Temperomandibular Joint Left | 54834 |
| Joint_TM_R | Anatomic | Joint | Temperomandibular Joint Right | 54833 |
| Laryngl_Pharynx | Anatomic | Tissue | Laryngeal pharynx | 54880 |
| Larynx | Anatomic | Larynx | Larynx | 55097 |
| Larynx_SG | Anatomic | Larynx | Supraglottic Larynx | 55476 |
| Lens | Anatomic | Eye | Eye Lens | 58241 |
| Lens_L | Anatomic | Eye | Lens Left | 58243 |
| Lens_R | Anatomic | Eye | Lens Right | 58242 |
| Lips | Anatomic | Feature | Lips | 59815 |
| LN_Neck_IA_L | Anatomic | Lymph Node | Level IA (Submental) neck node Left | 235616 |
| LN_Neck_IA_R | Anatomic | Lymph Node | Level IA (Submental) neck node Right | 235614 |
| LN_Neck_IB_L | Anatomic | Lymph Node | Level IB (Submandibular) neck node Left | 232676 |
| LN_Neck_IB_R | Anatomic | Lymph Node | Level IB (Submandibular) neck node Right | 232673 |
| LN_Neck_II_L | Anatomic | Lymph Node | Level IIA & IIB (Upper Jugular) neck nodes Left | 265660 |
| LN_Neck_II_R | Anatomic | Lymph Node | Level IIA & IIB (Upper Jugular) neck nodes Left | 265658 |
| LN_Neck_IIA_L | Anatomic | Lymph Node | Level IIA (Upper Jugular) neck node Left | 241975 |
| LN_Neck_IIA_R | Anatomic | Lymph Node | Level IIA (Upper Jugular) neck node Right | 241973 |
| LN_Neck_IIB_L | Anatomic | Lymph Node | Level IIB (Upper Jugular) neck node Left | 241979 |
| LN_Neck_IIB_R | Anatomic | Lymph Node | Level IIB (Upper Jugular) neck node Right | 241977 |
| LN_Neck_III_L | Anatomic | Lymph Node | Level III (Middle Jugular) neck node Left | 241953 |
| LN_Neck_III_R | Anatomic | Lymph Node | Level III (Middle Jugular) neck node Right | 241951 |
| LN_Neck_IV_L | Anatomic | Lymph Node | Level IV neck (Lower Jugular) node Left | 241959 |
| LN_Neck_IV_R | Anatomic | Lymph Node | Level IV (Lower Jugular) neck node Right | 241957 |
| LN_Neck_V_L | Anatomic | Lymph Node | Level VA, VB and VC (Posterior Triangle) neck nodes Left | 241965 |
| LN_Neck_V_R | Anatomic | Lymph Node | Level VA, VB and VC (Posterior Triangle) neck nodes Right | 241963 |
| LN_Neck_VA_L | Anatomic | Lymph Node | Level VA (Posterior Triangle) neck node Left | 265629 |
| LN_Neck_VA_R | Anatomic | Lymph Node | Level VA (Posterior Triangle) neck node Right | 265626 |
| LN_Neck_VB_L | Anatomic | Lymph Node | Level VB (Posterior Triangle) neck node Left | — |
| LN_Neck_VB_R | Anatomic | Lymph Node | Level VB (Posterior Triangle) neck node Right | — |
| LN_Neck_VC_L | Anatomic | Lymph Node | Level VC (Posterior Triangle) neck node Left | 232721 |
| LN_Neck_VC_R | Anatomic | Lymph Node | Level VC (Posterior Triangle) neck node Right | 232719 |
| LN_Neck_VI_L | Anatomic | Lymph Node | Level VI (Anterior Triangle) neck node Left | 241971 |
| LN_Neck_VI_R | Anatomic | Lymph Node | Level VI (Anterior Triangle) neck node Right | 241969 |
| LN_Neck_VII_L | Anatomic | Lymph Node | Level VII (Upper Mediastinal) neck node Left | — |
| LN_Neck_VII_R | Anatomic | Lymph Node | Level VII (Upper Mediastinal) neck node Right | — |
| Lobe_Frontal | Anatomic | Brain | Frontal Lobe | 61824 |
| Lobe_Frontal_L | Anatomic | Brain | Frontal Lobe Left | 72970 |
| Lobe_Frontal_R | Anatomic | Brain | Frontal Lobe Left | 72969 |
| Lobe_Occipital | Anatomic | Brain | Occipital Lobe | 67325 |
| Lobe_Occipital_L | Anatomic | Brain | Occipital Lobe Left | 72976 |
| Lobe_Occipital_R | Anatomic | Brain | Occipital Lobe Right | 72975 |
| Lobe_Parietal | Anatomic | Brain | Parietal Lobe | 61826 |
| Lobe_Parietal_L | Anatomic | Brain | Parietal Lobe Left | 72974 |
| Lobe_Parietal_R | Anatomic | Brain | Parietal Lobe Right | 72973 |
| Lobe_Temporal | Anatomic | Brain | Temporal Lobe | 61825 |
| Lobe_Temporal_L | Anatomic | Brain | Temporal Lobe Left | 72972 |
| Lobe_Temporal_R | Anatomic | Brain | Temporal Lobe Right | 72971 |
| Malleus | Anatomic | Bone | Malleus | 52753 |
| Malleus_L | Anatomic | Bone | Malleus Left | 74053 |
| Malleus_R | Anatomic | Bone | Malleus Right | 74052 |
| Maxilla | Anatomic | Bone | Maxilla | 9711 |
| Maxilla_L | Anatomic | Bone | Maxilla Left | 53650 |
| Maxilla_R | Anatomic | Bone | Maxilla Right | 53649 |
| Musc_Constrict | Anatomic | Muscle | Constrictor Muscle of Pharynx | 46620 |
| Musc_Constrict_I | Anatomic | Muscle | Pharynx – Inferior pharyngeal constrictor | 46623 |
| Musc_Constrict_M | Anatomic | Muscle | Pharynx – Middle pharyngeal constrictor | 46622 |
| Musc_Constrict_S | Anatomic | Muscle | Pharynx – Superior pharyngeal constrictor | 46621 |
| Musc_Masseter | Anatomic | Muscle | Masseter Muscle | 48996 |
| Musc_Masseter_L | Anatomic | Muscle | Masseter Muscle Left | 48998 |
| Musc_Masseter_R | Anatomic | Muscle | Masseter Muscle Right | 48997 |
| Musc_Platysma_L | Anatomic | Muscle | Platysma Left | 45740 |
| Musc_Platysma_R | Anatomic | Muscle | Platysma Right | 45739 |
| Musc_Pterygoid_L | Anatomic | Muscle | Pterygoid muscles – Left | — |
| Musc_Pterygoid_R | Anatomic | Muscle | Pterygoid muscles – Right | — |
| Musc_Sclmast_L | Anatomic | Muscle | Sternocleidomastoid Left | 13409 |
| Musc_Sclmast_R | Anatomic | Muscle | Sternocleidomastoid Left | 13408 |
| Musc_Temporal_L | Anatomic | Muscle | Temporal muscle – Left | 49008 |
| Musc_Temporal_R | Anatomic | Muscle | Temporal muscle – Right | 49007 |
| Nasalconcha_LI | Anatomic | Nose | Inferior Nasal Concha Left | 54738 |
| Nasalconcha_RI | Anatomic | Nose | Inferior Nasal Concha Right | 54737 |
| Nasopharynx | Anatomic | Nose | Nasal part of pharynx | 54878 |
| Nose | Anatomic | Nose | Nose | 46472 |
| OpticChiasm | Anatomic | Nerve | Optic chiasm | 62045 |
| OpticChiasm_PRV | PRV | Nerve | PRV for Optic Chiasm | — |
| OpticChiasm_PRVx | PRV | Nerve | PRV expansion of x mm on the optic chiasm | — |
| OpticNrv | Anatomic | Nerve | Optic nerve | 50863 |
| OpticNrv_L | Anatomic | Nerve | Optic nerve | 50878 |
| OpticNrv_PRV | PRV | Nerve | PRV for Optic Nerve | — |
| OpticNrv_PRV_L | PRV | Nerve | — | |
| OpticNrv_PRV_R | PRV | Nerve | — | |
| OpticNrv_PRVxx_L | PRV | Nerve | PRV expansion of xx millimeters on the right optic nerve | — |
| OpticNrv_PRVxx_R | PRV | Nerve | PRV created with xx mm expansion on the left optic nerve | — |
| OpticNrv_R | Anatomic | Nerve | Optic nerve | 50875 |
| Orbit_L | Anatomic | Eye | Orbit Left | 54668 |
| Orbit_R | Anatomic | Eye | Orbit Right | 54667 |
| Oropharynx | Anatomic | Throat | Oral part of pharynx | 54879 |
| Palate_Soft | Anatomic | Muscle | Soft palate | 55021 |
| Parotid_L | Anatomic | Gland | Parotid Left | 59798 |
| Parotid_R | Anatomic | Gland | Parotid Right | 59797 |
| Parotids | Anatomic | Gland | Pair of Parotid Glands | 320436 |
| Pharynx | Anatomic | Throat | Pharynx | 46688 |
| Pineal | Anatomic | Gland | Pineal gland | 62033 |
| Pituitary | Anatomic | Gland | Pituitary gland | 13889 |
| Pituitary_PRVxx | PRV | Gland | PRV constructed as xx millimeter expansion on Pituitary | — |
| Pons | Anatomic | Brain | Pons | 67943 |
| Proc_Condyloid_L | Anatomic | Bone | Condyloid process of mandible – Right | 52838 |
| Proc_Condyloid_R | Anatomic | Bone | Condyloid process of mandible – Left | 52840 |
| Proc_Coronoid_L | Anatomic | Bone | Coronoid process of mandible – Left | 52835 |
| Proc_Coronoid_R | Anatomic | Bone | Coronoid process of mandible – Right | 52834 |
| Pterygoid_Lat_L | Anatomic | Muscle | Pterygoid muscles lateral – Left | 49017 |
| Pterygoid_Lat_R | Anatomic | Muscle | Pterygoid muscles lateral – Right | 49016 |
| Pterygoid_Med_L | Anatomic | Muscle | Pterygoid muscles medial – Left | 49013 |
| Pterygoid_Med_R | Anatomic | Muscle | Pterygoid muscles medial – Right | 49012 |
| Retina_L | Anatomic | Eye | Retina Left | 58303 |
| Retina_PRVxx_L | PRV | Eye | — | |
| Retina_PRVxx_R | PRV | Eye | PRV constructed as xx millimeter expansion on Retina | — |
| Retina_R | Anatomic | Eye | Retina Right | 58302 |
| Retinas | Anatomic | Eye | Both Retinas | 58301 |
| Scalp | Anatomic | Skin | 46494 | |
| Sinus_Ethmoid | Anatomic | Sinus | Ethmoidal Sinus | 84115 |
| Sinus_Frontal | Anatomic | Brain | Frontal Sinus | 57417 |
| Sinus_Frontal_L | Anatomic | Brain | Frontal Sinus Left | 57419 |
| Sinus_Frontal_R | Anatomic | Brain | Frontal Sinus Right | 57418 |
| Sinus_Maxilry | Anatomic | Sinus | Maxillary Sinus | 57715 |
| Sinus_Maxilry_L | Anatomic | Sinus | Maxillary Sinus | 57717 |
| Sinus_Maxilry_R | Anatomic | Sinus | Maxillary Sinus | 57716 |
| Sinus_Sphenoid | Anatomic | Bone | Sphenoidal Sinus | 54683 |
| Sinus_Sphenoid_L | Anatomic | Bone | Sphenoidal Sinus Left | 54708 |
| Sinus_Sphenoid_R | Anatomic | Bone | Sphenoidal Sinus Right | 54707 |
| Skull | Anatomic | Bone | Skeletal system of head | 46565 |
| Spc_Retrophar_L | Anatomic | Space | Retropharyngeal space Left | — |
| Spc_Retrophar_R | Anatomic | Space | Retropharyngeal space Right | — |
| Spc_Retrophars | Anatomic | Space | Retropharyngeal space | 286702 |
| Spc_Retrosty | Anatomic | Space | Retrostyloid space | — |
| Spc_Retrosty_L | Anatomic | Space | Retrostyloid space -Left | — |
| Spc_Retrosty_R | Anatomic | Space | Retrostyloid space -Left | — |
| SpinalCord_Cerv | Anatomic | Nerve | Spinal Cord Cervical | 71166 |
| Stapes | Anatomic | Ear | Stapes | 52751 |
| Stapes_L | Anatomic | Ear | Stapes Left | 74049 |
| Stapes_R | Anatomic | Ear | Stapes Right | 74048 |
| Sys_Ventricular | Anatomic | Brain | 242787 | |
| Tongue | Anatomic | Mouth | Tongue | 54640 |
| Tongue_All | Anatomic | Mouth | — | |
| Tongue_Base | Anatomic | Mouth | 54645 | |
| Tongue_Base_L | Anatomic | Mouth | — | |
| Tongue_Base_R | Anatomic | Mouth | — | |
| Tongue_Oral | Anatomic | Mouth | 54644 | |
| Tongue_Oral_L | Anatomic | Mouth | 281502 | |
| Tongue_Oral_R | Anatomic | Mouth | 281500 | |
| Tonsil | Anatomic | Mouth | 9609 | |
| V_Jugular | Anatomic | Vein | Any Jugular Vein | — |
| V_Jugular_Ext_L | Anatomic | Vein | 13112 | |
| V_Jugular_Ext_R | Anatomic | Vein | 13111 | |
| V_Jugular_Int_L | Anatomic | Vein | Internal jugular vein Right | 4754 |
| V_Jugular_Int_R | Anatomic | Vein | Internal jugular vein Left | 4762 |
| VB_C | Anatomic | Bone | Cervical vertebrae | 72063 |
| VB_C1 | Anatomic | Bone | Atlas – C1 | 12519 |
| VB_C2 | Anatomic | Bone | Axis – C2 | 12520 |
| VB_C3 | Anatomic | Bone | Cervical vertebra – C3 | 12521 |
| VB_C4 | Anatomic | Bone | Cervical vertebra – C4 | 12522 |
| VB_C5 | Anatomic | Bone | Cervical vertebra – C5 | 12523 |
| VB_C6 | Anatomic | Bone | Cervical vertebra – C6 | 12524 |
| VB_C7 | Anatomic | Bone | Cervical vertebra – C7 | 12525 |
| VocalCord_L | Anatomic | Larynx | 55459 | |
| VocalCord_R | Anatomic | Larynx | 55458 | |
| VocalCords | Anatomic | Larynx | Vocal Cords | 323919 |
| Vomer | Anatomic | Bone | Vomer | 9710 |
Tórax (Thorax) — 180 estruturas
| Nome TG-263 | Tipo | Categoria | Descrição | FMAID |
|---|---|---|---|---|
| A_Aorta | Anatomic | Artery | Aorta | 3734 |
| A_Aorta_Asc | Anatomic | Artery | Ascending Aorta | 3736 |
| A_Brachiocephls | Anatomic | Artery | Brachiocephalic Artery | 3932 |
| A_Coronary_L | Anatomic | Artery | Coronary Artery Left | 50040 |
| A_Coronary_R | Anatomic | Artery | Coronary Artery Right | 50039 |
| A_LAD | Anatomic | Artery | Anterior interventricular branch of LCA (left anterior descending artery) |
3862 |
| A_Pulmonary | Anatomic | Artery | Pulmonary Artery | 66326 |
| A_Subclavian | Anatomic | Artery | Subclavian Artery | 3951 |
| A_Subclavian_L | Anatomic | Artery | Subclavian Artery Left | 4694 |
| A_Subclavian_R | Anatomic | Artery | Subclavian Artery Right | 3953 |
| A_Vertebral | Anatomic | Artery | Vertebral arteries | 3956 |
| A_Vertebral_L | Anatomic | Artery | Vertebral arteries left | 4066 |
| A_Vertebral_R | Anatomic | Artery | Vertebral arteries right | 3958 |
| AirWay_Dist | Anatomic | Lung | Distal Airway | — |
| AirWay_Prox | Anatomic | Lung | Proximal Airway | — |
| Atrium | Anatomic | Heart | Atrium of the heart | 7099 |
| Atrium_L | Anatomic | Heart | Atrium of the heart Left | 7097 |
| Atrium_R | Anatomic | Heart | Atrium of the heart Right | 7096 |
| BrachialPlex_L | Anatomic | Nerve | Brachial plexus Left | 45245 |
| BrachialPlex_R | Anatomic | Nerve | Brachial plexus Right | 45244 |
| BrachialPlexs | Anatomic | Nerve | Brachial plexus | 5906 |
| Breast_L | Anatomic | Breast | Breast Left | 321497 |
| Breast_R | Anatomic | Breast | Breast Right | 321496 |
| Breasts | Anatomic | Breast | Both breasts | 268893 |
| Bronchus | Anatomic | Lung | Bronchial tree | 26660 |
| Bronchus_L | Anatomic | Lung | Bronchial tree Left | 26662 |
| Bronchus_Main | Anatomic | Lung | Main Bronchus | 7405 |
| Bronchus_Main_L | Anatomic | Lung | Main Bronchus Left | 7396 |
| Bronchus_Main_R | Anatomic | Lung | Main Bronchus Right | 7395 |
| Bronchus_PRVxx | Anatomic | Lung | A PRV expansion on the Bronchus that is xx millimeters thick | — |
| Bronchus_R | Anatomic | Lung | Bronchial tree Right | 26661 |
| Carina | Anatomic | Carina | Carina | 7465 |
| Cartlg_Thyroid | Anatomic | Cartilage | Thyroid cartilage | 55099 |
| Chestwall | Anatomic | Chest wall | Chest wall | 50060 |
| Chestwall_L | Anatomic | Chest wall | Left Chest Wall | 25559 |
| Chestwall_R | Anatomic | Chest wall | Right Chest Wall | 25558 |
| Clavicle_L | Anatomic | Bone | Clavicle Left | 13323 |
| Clavicle_R | Anatomic | Bone | Clavicle Right | 13322 |
| Diaphragm | Anatomic | Diaphragm | Diaphragm | 13295 |
| Esophagus | Anatomic | Esophagus | Esophagus | 7131 |
| Esophagus_I | Anatomic | Esophagus | Lower Esophagus (abdominal) | 9397 |
| Esophagus_M | Anatomic | Esophagus | Middle Esophagus (thoracic) | 9396 |
| Esophagus_NAdj | Anatomic | Esophagus | Non Adjacent Esophagus | — |
| Esophagus_S | Anatomic | Esophagus | Upper Esophagus (cervical) | — |
| Glnd_Adrenal_L | Anatomic | Gland | Adrenal glands left | 15629 |
| Glnd_Adrenal_R | Anatomic | Gland | Adrenal glands right | 15630 |
| Glnd_Parathyroid | Anatomic | Gland | Parathyroid gland | 13890 |
| Glnd_Thymus | Anatomic | Gland | Thymus Gland | 9607 |
| Glnd_Thyroid | Anatomic | Gland | Thyroid Gland | 9603 |
| GreatVes | Anatomic | Heart | Great Vessels of the heart (aorta, vena cava S&I, pulmonary A&V) | — |
| GreatVes_NAdj | Anatomic | Heart | Non Adjacent Great Vessels | — |
| Heart | Anatomic | Heart | Heart | 7088 |
| LN_Ax_Apical | Anatomic | Lymph Node | Set of apical axillary lymphatic vessels | 23394 |
| LN_Ax_Apical_L | Anatomic | Lymph Node | Axillary lymphatic chain – Apical Left | 73265 |
| LN_Ax_Apical_R | Anatomic | Lymph Node | Axillary lymphatic chain – Apical Right | 73264 |
| LN_Ax_Central_L | Anatomic | Lymph Node | Axillary lymphatic chain – Central Left | 73263 |
| LN_Ax_Central_R | Anatomic | Lymph Node | Axillary lymphatic chain – Central Left | 73262 |
| LN_Ax_Centrals | Anatomic | Lymph Node | Set of central axillary lymphatic vessels | 233482 |
| LN_Ax_L | Anatomic | Lymph Node | Axillary lymphatic chain Left | 73250 |
| LN_Ax_L1_L | Anatomic | Lymph Node | Level 1 Axillary Lymph Node Left | 276001 |
| LN_Ax_L1_R | Anatomic | Lymph Node | Level 1 Axillary Lymph Node Right | 275999 |
| LN_Ax_L2_L | Anatomic | Lymph Node | Level 2 Axillary Lymph Node Left | 276005 |
| LN_Ax_L2_R | Anatomic | Lymph Node | Level 2 Axillary Lymph Node Right | 276003 |
| LN_Ax_L3_L | Anatomic | Lymph Node | Level 3 Axillary Lymph Node Left | 276009 |
| LN_Ax_L3_R | Anatomic | Lymph Node | Level 3 Axillary Lymph Node Right | 276007 |
| LN_Ax_Lateral_L | Anatomic | Lymph Node | Axillary lymphatic chain – Lateral Left | 73256 |
| LN_Ax_Lateral_R | Anatomic | Lymph Node | Axillary lymphatic chain – Lateral Right | 73255 |
| LN_Ax_Laterals | Anatomic | Lymph Node | pair of Lungs | 233458 |
| LN_Ax_Pectoral_L | Anatomic | Lymph Node | Axillary lymphatic chain – Pectoral Left | 73253 |
| LN_Ax_Pectoral_R | Anatomic | Lymph Node | Axillary lymphatic chain – Pectoral Right | 73252 |
| LN_Ax_Pectorals | Anatomic | Lymph Node | Set of pectoral axillary lymphatic vessels | 233446 |
| LN_Ax_R | Anatomic | Lymph Node | Axillary lymphatic chain Right | 73249 |
| LN_Ax_Subscap_L | Anatomic | Lymph Node | Axillary lymphatic chain – Subscapular Left | 73259 |
| LN_Ax_Subscap_R | Anatomic | Lymph Node | Axillary lymphatic chain – Subscapular Right | 73258 |
| LN_Ax_Subscaps | Anatomic | Lymph Node | Set of subscapular axillary lymphatic vessels | 233470 |
| LN_Brachioceph_L | Anatomic | Lymph Node | Lymph nodes of thorax – Brachiocephalic Left | 5946 |
| LN_Brachioceph_R | Anatomic | Lymph Node | Lymph nodes of thorax – Brachiocephalic Right | 5945 |
| LN_Brachiocephs | Anatomic | Lymph Node | Lymph nodes of thorax – Brachiocephalic | 5944 |
| LN_Bronchpulm_L | Anatomic | Lymph Node | Lymph nodes of thorax – Bronchopulmonary Left | 5967 |
| LN_Bronchpulm_R | Anatomic | Lymph Node | Lymph nodes of thorax – Bronchopulmonary Right | 5966 |
| LN_Bronchpulms | Anatomic | Lymph Node | Lymph nodes of thorax – Bronchopulmonary | 5965 |
| LN_Diaphragmatic | Anatomic | Lymph Node | Lymph nodes of thorax – Diaphragmatic | 12773 |
| LN_IMN_L | Anatomic | Lymph Node | 5934 | |
| LN_IMN_R | Anatomic | Lymph Node | 5933 | |
| LN_IMNs | Anatomic | Lymph Node | Lymph nodes IMN | 5849 |
| LN_Intercostals | Anatomic | Lymph Node | Lymph nodes of thorax – Intercostal | 5932 |
| LN_Ligamentarter | Anatomic | Lymph Node | Lymph nodes of thorax – Ligamentum arteriosum | 74033 |
| LN_Mediastinals | Anatomic | Lymph Node | Lymph nodes of thorax – Mediastinal | 12774 |
| LN_Paramammary_L | Anatomic | Lymph Node | Lymph nodes of thorax – Paramammary Left | 232600 |
| LN_Paramammary_R | Anatomic | Lymph Node | Lymph nodes of thorax – Paramammary Right | 232598 |
| LN_Paramammarys | Anatomic | Lymph Node | Lymph nodes of thorax – Paramammary | 44313 |
| LN_Parasternal_L | Anatomic | Lymph Node | Lymph nodes of thorax – Parasternal Left | 5934 |
| LN_Parasternal_R | Anatomic | Lymph Node | Lymph nodes of thorax – Parasternal Right | 5933 |
| LN_Parasternals | Anatomic | Lymph Node | Lymph nodes of thorax – Parasternal | 5849 |
| LN_Pulmonary_L | Anatomic | Lymph Node | Lymph nodes of thorax – Pulmonary Left | 5970 |
| LN_Pulmonary_R | Anatomic | Lymph Node | Lymph nodes of thorax – Pulmonary Right | 5969 |
| LN_Pulmonarys | Anatomic | Lymph Node | Lymph nodes of thorax – Pulmonary | 5968 |
| LN_Supmammary_L | Anatomic | Lymph Node | Lymph nodes of thorax – Supramammary Left | 232604 |
| LN_Supmammary_R | Anatomic | Lymph Node | Lymph nodes of thorax – Supramammary Right | 232602 |
| LN_Supmammarys | Anatomic | Lymph Node | Lymph nodes of thorax – Supramammary | 12785 |
| LN_Trachbrnchs | Anatomic | Lymph Node | Lymph nodes of thorax – Tracheobronchial | 5950 |
| LN_Trachbrnchs_L | Anatomic | Lymph Node | Lymph nodes of thorax – Tracheobronchial Left | 5952 |
| LN_Trachbrnchs_R | Anatomic | Lymph Node | Lymph nodes of thorax – Tracheobronchial Right | 5951 |
| Lung_L | Anatomic | Lung | Lung Left | 7310 |
| Lung_LLL | Anatomic | Lung | Lung – lower lobe of left | 7371 |
| Lung_LUL | Anatomic | Lung | Lung – upper lobe of left | 7370 |
| Lung_R | Anatomic | Lung | Lung Right | 7309 |
| Lung_RLL | Anatomic | Lung | Lung – lower lobe of right | 7337 |
| Lung_RML | Anatomic | Lung | Lung – middle lobe of right | 7383 |
| Lung_RUL | Anatomic | Lung | Lung – upper lobe of right | 7333 |
| Lungs | Anatomic | Lung | Pair of Lungs | 68877 |
| Lungs-CTV | Derived | Lung | Total Lung minus the CTV | — |
| Lungs-GTV | Derived | Lung | Total Lung minus the GTV | — |
| Lungs-ITV | Derived | Lung | — | |
| Lungs-PTV | Derived | Lung | Total Lung minus the PTV | — |
| Mediastinum | Anatomic | Heart | Mediastinum | 9826 |
| Pacemaker | Non_Anatomic | Devices | Pacemaker | — |
| Pericardium | Anatomic | Heart | Pericardium | 9869 |
| Rib | Anatomic | Bone | Any Rib volume | 7574 |
| Rib01_L | Anatomic | Bone | First Rib Left | 7987 |
| Rib01_R | Anatomic | Bone | First Rib Right | 7857 |
| Rib02_L | Anatomic | Bone | Second rib Left | 8012 |
| Rib02_R | Anatomic | Bone | Second rib Right | 7882 |
| Rib03_L | Anatomic | Bone | Third rib Left | 8039 |
| Rib03_R | Anatomic | Bone | Third rib Right | 7909 |
| Rib04_L | Anatomic | Bone | Fourth rib Left | 8148 |
| Rib04_R | Anatomic | Bone | Fourth rib Right | 7957 |
| Rib05_L | Anatomic | Bone | Fifth rib Left | 8093 |
| Rib05_R | Anatomic | Bone | Fifth rib Right | 8066 |
| Rib06_L | Anatomic | Bone | Sixth rib Left | 8202 |
| Rib06_R | Anatomic | Bone | Sixth rib Right | 8175 |
| Rib07_L | Anatomic | Bone | Seventh rib Left | 8256 |
| Rib07_R | Anatomic | Bone | Seventh rib Right | 8229 |
| Rib08_L | Anatomic | Bone | Eighth rib Left | 8310 |
| Rib08_R | Anatomic | Bone | Eighth rib Right | 8283 |
| Rib09_L | Anatomic | Bone | Ninth rib Left | 8391 |
| Rib09_R | Anatomic | Bone | Ninth rib Right | 8364 |
| Rib10_L | Anatomic | Bone | Tenth rib Left | 8472 |
| Rib10_R | Anatomic | Bone | Tenth rib Right | 8445 |
| Rib11_L | Anatomic | Bone | Eleventh rib Left | 8532 |
| Rib11_R | Anatomic | Bone | Eleventh rib Right | 8531 |
| Rib12_L | Anatomic | Bone | Twelfth rib Left | 8534 |
| Rib12_R | Anatomic | Bone | Twelfth rib Right | 8533 |
| Scapula_L | Anatomic | Bone | Scapula Left | 13396 |
| Scapula_R | Anatomic | Bone | Scapula Right | 13395 |
| Spc_Supraclav_L | Anatomic | Space | Supraclavicular space – Left | 45797 |
| Spc_Supraclav_R | Anatomic | Space | Supraclavicular space – Right | 45796 |
| SpinalCord_Thor | Anatomic | Nerve | Spinal Cord Thoracic | 71167 |
| Thoracic_Duct | Anatomic | Duct | Thoracic Duct | 5031 |
| Trachea | Anatomic | Lung | Trachea | 7394 |
| Trachea_NAdj | Anatomic | Lung | Trachea non adjacent wall | — |
| V_Azygos | Anatomic | Vein | Azygos Vein | 4838 |
| V_Brachioceph_L | Anatomic | Vein | Brachiocephalic vein Left | 4761 |
| V_Brachioceph_R | Anatomic | Vein | Brachiocephalic vein Right | 4751 |
| V_Pulmonary | Anatomic | Vein | Pulmonary vein | 66643 |
| V_Subclavian_L | Anatomic | Vein | Subclavian Vein Left | 4763 |
| V_Subclavian_R | Anatomic | Vein | Subclavian Vein Right | 4755 |
| V_Subclavians | Anatomic | Vein | Subclavian Vein | 4725 |
| V_Venacava_I | Anatomic | Vein | Inferior vena cava | 10951 |
| V_Venacava_S | Anatomic | Vein | Superior vena cava | 4720 |
| Valve_Aortic | Anatomic | Valve | Aortic Valve | 7236 |
| Valve_Mitral | Anatomic | Valve | Mitral Valve | 7235 |
| Valve_Pulmonic | Anatomic | Valve | Pulmonic Valve | 7246 |
| Valve_Tricuspid | Anatomic | Valve | Tricuspid Valve | 7234 |
| VB_T | Anatomic | Bone | Thoracic Vertebra | 9139 |
| VB_T01 | Anatomic | Bone | Thoracic Vertebra T1 | 9165 |
| VB_T02 | Anatomic | Bone | Thoracic Vertebra T2 | 9187 |
| VB_T03 | Anatomic | Bone | Thoracic Vertebra T3 | 9209 |
| VB_T04 | Anatomic | Bone | Thoracic Vertebra T4 | 9248 |
| VB_T05 | Anatomic | Bone | Thoracic Vertebra T5 | 9922 |
| VB_T06 | Anatomic | Bone | Thoracic Vertebra T6 | 9945 |
| VB_T07 | Anatomic | Bone | Thoracic Vertebra T7 | 9968 |
| VB_T08 | Anatomic | Bone | Thoracic Vertebra T8 | 9991 |
| VB_T09 | Anatomic | Bone | Thoracic Vertebra T9 | 10014 |
| VB_T10 | Anatomic | Bone | Thoracic Vertebra T10 | 10037 |
| VB_T11 | Anatomic | Bone | Thoracic Vertebra T11 | 10059 |
| VB_T12 | Anatomic | Bone | Thoracic Vertebra T12 | 10081 |
| Ventricle | Anatomic | Heart | Ventricle (cardiac) | 7100 |
| Ventricle_L | Anatomic | Heart | Ventricle (cardiac) Left | 7101 |
| Ventricle_R | Anatomic | Heart | Ventricle (cardiac) Right | 7098 |
Abdômen (Abdômen) — 60 estruturas
| Nome TG-263 | Tipo | Categoria | Descrição | FMAID |
|---|---|---|---|---|
| A_Celiac | Anatomic | Artery | Celiac Artery | 50737 |
| A_Mesenteric_I | Anatomic | Artery | Inferior mesenteric artery | 14750 |
| A_Mesenteric_S | Anatomic | Artery | Superior mesenteric artery | 14749 |
| Appendix | Anatomic | Bowel | Appendix | 14542 |
| Bag_Bowel | Non_Anatomic | Bowel | Bowel Bag | — |
| BileDuct_Common | Anatomic | Bowel | Common bile duct | 14667 |
| Bowel | Anatomic | Bowel | 7199 | |
| Bowel_Small | Anatomic | Bowel | Small Bowel (small intestine) | 7200 |
| Cecum | Anatomic | Bowel | Large bowel – Cecum | 14541 |
| Colon | Anatomic | Bowel | Colon | 14543 |
| Colon_Ascending | Anatomic | Bowel | Large bowel – Ascending colon | 14545 |
| Colon_Decending | Anatomic | Bowel | Large bowel – Descending colon | 14547 |
| Colon_PTVxx | Anatomic | Bowel | PRV created with xx mm expansion on the left optic nerve | — |
| Colon_Sigmoid | Anatomic | Bowel | Large bowel – Sigmoid colon | 14548 |
| Colon_Transverse | Anatomic | Bowel | Large bowel -Transverse colon | 14546 |
| Duodenum | Anatomic | Gut | Small bowel – Duodenum | 7206 |
| Ileum | Anatomic | Gut | Small bowel – Ileum | 7208 |
| Jejunum | Anatomic | Gut | Small bowel – Jejunum | 7207 |
| Jejunum_Ileum | Anatomic | Gut | Both ileum and jejunum | — |
| Kidney_Cortex | Anatomic | Urinary | Renal cortex for both Kidneys | 15581 |
| Kidney_Cortex_L | Anatomic | Urinary | Renal cortex left | 15584 |
| Kidney_Cortex_R | Anatomic | Urinary | Renal cortex right | 15583 |
| Kidney_Hilum_L | Anatomic | Urinary | Renal Hilum Left | 15942 |
| Kidney_Hilum_R | Anatomic | Urinary | Renal Hilum Right | 15941 |
| Kidney_Hilums | Anatomic | Urinary | Renal Hilum for both Kidneys | 15610 |
| Kidney_L | Anatomic | Urinary | Kidney Left | 7205 |
| Kidney_L-GTV | Derived | Urinary | — | |
| Kidney_Pelvis_L | Anatomic | Urinary | Renal pelvis Left | 15579 |
| Kidney_Pelvis_R | Anatomic | Urinary | Renal pelvis Right | 15578 |
| Kidney_R | Anatomic | Urinary | Kidney Right | 7204 |
| Kidney_R-GTV | Derived | Urinary | — | |
| Kidney-GTV | Derived | Urinary | — | |
| Kidneys | Anatomic | Urinary | Both Kidneys | 264815 |
| Lig_Hepatogastrc | Anatomic | Ligament | Hepatogastric ligament | 16520 |
| Liver | Anatomic | Liver | Liver | 7197 |
| Liver-CTV | Derived | Liver | — | |
| Liver-GTV | Derived | Liver | Liver minus GTV | — |
| LN_Portahepatis | Anatomic | Lymph Node | Porta hepatis | 15758 |
| Musc_Digastric_L | Anatomic | Muscle | Digastric muscle Left | 46293 |
| Musc_Digastric_R | Anatomic | Muscle | Digastric muscle Right | 46292 |
| PancJejuno | Surgical | Gut | The pancreatic jejuno junction – generated by surgical procedure | — |
| Pancreas | Anatomic | Gland | Pancreas | 7198 |
| Pancreas_Head | Anatomic | Gland | Head of Pancreas | 10468 |
| Pancreas_Tail | Anatomic | Gland | Tail of Pancreas | 14519 |
| Peritoneum | Anatomic | Membrane | Peritoneal sac | 9908 |
| Skin_Peritoneum | Anatomic | Skin | — | |
| Spc_Bowel | Anatomic | Bowel | Space occupied by bowel | — |
| Spc_Bowel_Small | Anatomic | Space | — | |
| SpinalCord_Lum | Anatomic | Nerve | Spinal Cord Lumbar | 71168 |
| Spleen | Anatomic | Lymph Node | Spleen | 7196 |
| Spleen_Hilum | Anatomic | Lymph Node | Splenic hilum | 15841 |
| Stomach | Anatomic | Stomach | Stomach | 7148 |
| Stomach_PRVxx | PRV | Stomach | PRV created with xx mm expansion on the stomach | — |
| V_Portal | Anatomic | Vein | Portal Vein | 66645 |
| VB_L | Anatomic | Bone | Lumbar Vertebrae | 72065 |
| VB_L1 | Anatomic | Bone | Lumbar Vertebra L1 | 13072 |
| VB_L2 | Anatomic | Bone | Lumbar Vertebra L2 | 13073 |
| VB_L3 | Anatomic | Bone | Lumbar Vertebra L3 | 13074 |
| VB_L4 | Anatomic | Bone | Lumbar Vertebra L4 | 13075 |
| VB_L5 | Anatomic | Bone | Lumbar Vertebra L5 | 13076 |
Pelve (Pelvis) — 109 estruturas
| Nome TG-263 | Tipo | Categoria | Descrição | FMAID |
|---|---|---|---|---|
| A_Iliac_Cflx_L | Anatomic | Artery | Circumflex Left Iliac Artery | — |
| A_Iliac_Cflx_R | Anatomic | Artery | Circumflex Right Iliac Artery | — |
| A_Iliac_Ext_L | Anatomic | Artery | External iliac artery Left | 18807 |
| A_Iliac_Ext_R | Anatomic | Artery | External iliac artery Right | 18806 |
| A_Iliac_Int_L | Anatomic | Artery | Internal iliac artery Left | 18810 |
| A_Iliac_Int_R | Anatomic | Artery | Internal iliac artery Right | 18809 |
| A_Iliac_L | Anatomic | Artery | Common iliac artery Left | 14766 |
| A_Iliac_R | Anatomic | Artery | Common iliac artery Right | 14765 |
| Acetabulum_L | Anatomic | Bone | Acetabulum | 16599 |
| Acetabulum_R | Anatomic | Bone | Acetabulum | 16598 |
| Acetabulums | Anatomic | Bone | Acetabulum | 16579 |
| Anus | Anatomic | Bowel | Anus | 15711 |
| Bladder | Anatomic | Bladder | Urinary Bladder | 15900 |
| Bladder_Wall | Anatomic | Bladder | Bladder Wall | 15902 |
| Bladder-CTV | Derived | Bladder | Bladder minus CTV | — |
| Bone_Ilium | Anatomic | Bone | Ilium | 42832 |
| Bone_Ilium_L | Anatomic | Bone | Ilium Left | 16591 |
| Bone_Ilium_R | Anatomic | Bone | Ilium Right | 16590 |
| Bone_Ischium_L | Anatomic | Bone | Ischium Left | 16594 |
| Bone_Ischium_R | Anatomic | Bone | Ischium Right | 16593 |
| Bone_Pelvic | Anatomic | Bone | Pelvic Bones (Bony Pelvis) | 16580 |
| Bone_Pelvic_L | Anatomic | Bone | Bony Pelvis Left | 20227 |
| Bone_Pelvic_R | Anatomic | Bone | Bony Pelvis Right | 20226 |
| Bowel_Large | Anatomic | Bowel | Large Bowel | 7201 |
| Canal_Anal | Anatomic | Bowel | Anal Canal | 15703 |
| CaudaEquina | Anatomic | Nerve | Cauda equina | 52590 |
| Cavernosum | Anatomic | Reproductive | Penis Corpus Cavernosum | 75189 |
| Cervix | Anatomic | Cervix | Cervix of uterus | 17740 |
| Femur_Base_L | Anatomic | Bone | Femur Base Left | 32846 |
| Femur_Base_R | Anatomic | Bone | Femur Base Right | 32845 |
| Femur_Head_L | Anatomic | Bone | Femur Head & Neck Left | 32843 |
| Femur_Head_R | Anatomic | Bone | Femur Head & Neck Right | 32842 |
| Femur_Joint_L | Anatomic | Joint | Femoral Joint Left | 35180 |
| Femur_Joint_R | Anatomic | Joint | Femoral Joint Right | 35179 |
| Femur_Neck_L | Anatomic | Bone | Femur Neck Right | 42386 |
| Femur_Neck_R | Anatomic | Bone | Femur Neck Left | 42387 |
| Femur_Shaft_L | Anatomic | Bone | Femur Shaft Left | 32849 |
| Femur_Shaft_R | Anatomic | Bone | Femur Shaft Right | 32848 |
| Foley | Non-Anatomic | Bladder | Foley Catheter | — |
| Gallbladder | Anatomic | Gallbladder | Gall bladder | 7202 |
| Genitals | Anatomic | Reproductive | Genitals | 45643 |
| LN_Iliac_Ext_L | Anatomic | Lymph Node | Lymph nodes of pelvis – external iliac Left | 229177 |
| LN_Iliac_Ext_R | Anatomic | Lymph Node | Lymph nodes of pelvis – external iliac Right | 229177 |
| LN_Iliac_Int_L | Anatomic | Lymph Node | Lymph nodes of pelvis – internal iliac Left | 224275 |
| LN_Iliac_L | Anatomic | Lymph Node | Lymph nodes of pelvis – common iliac Left | 224269 |
| LN_Iliac_R | Anatomic | Lymph Node | Lymph nodes of pelvis – common iliac Right | 224269 |
| LN_Inguinofem | Anatomic | Lymph Node | Lymph nodes of pelvis – inguinofemoral | 236337 |
| LN_Inguinofem_L | Anatomic | Lymph Node | Lymph nodes of pelvis – inguinofemoral | 236341 |
| LN_Inguinofem_R | Anatomic | Lymph Node | Lymph nodes of pelvis – inguinofemoral | 236339 |
| LN_lliac_Int_R | Anatomic | Lymph Node | Lymph nodes of pelvis – internal iliac Right | 224275 |
| LN_Obturator_L | Anatomic | Lymph Node | Lymph nodes of pelvis – obturator Left | 16676 |
| LN_Obturator_R | Anatomic | Lymph Node | Lymph nodes of pelvis – obturator Right | 16676 |
| LN_Paraaortic | Anatomic | Lymph Node | Lymph nodes of abdomen- para-aortic | 223899 |
| LN_Pelvic_L | Anatomic | Lymph Node | Pelvic Lymph Nodes Left | — |
| LN_Pelvic_R | Anatomic | Lymph Node | Pelvic Lymph Nodes Right | — |
| LN_Pelvics | Anatomic | Lymph Node | Pelvic Lymph Nodes | — |
| LN_Presacral_L | Anatomic | Lymph Node | Lymph nodes of pelvis – presacral Left | 234280 |
| LN_Presacral_R | Anatomic | Lymph Node | Lymph nodes of pelvis – presacral Right | 234280 |
| Ovaries | Anatomic | Reproductive | Ovary | 7409 |
| Ovary_L | Anatomic | Reproductive | Ovary Left | 7214 |
| Ovary_R | Anatomic | Reproductive | Ovary Right | 7213 |
| Parametrium | Anatomic | Reproductive | Parametrium | 77061 |
| PenileBulb | Anatomic | Reproductive | Penile Bulb | 19614 |
| Penis | Anatomic | Reproductive | Penis | 9707 |
| Perineum | Anatomic | Perineum | Perineum | 9579 |
| Prostate | Anatomic | Gland | Prostate | 9600 |
| ProstateBed | Anatomic | Surgery | Prostate Bed | — |
| PubicSymphys | Anatomic | Bone | Pubic Symphysis | 16950 |
| PubicSymphys_L | Anatomic | Bone | Pubic bone Left | 16597 |
| PubicSymphys_R | Anatomic | Bone | Pubic bone Right | 16596 |
| Rectal_Wall | Anatomic | Rectum | Rectal Wall | 14626 |
| Rectum | Anatomic | Rectum | Large bowel – Rectum | 14544 |
| SacralPlex | Anatomic | Nerve | Sacral Plexus | 5909 |
| Sacrum | Anatomic | Bone | Sacrum | 16202 |
| Scrotum | Anatomic | Skin | Scrotum (skin & cremasteric fascia) | 18252 |
| SeminalVes | Anatomic | Gland | Seminal vesicle | 19387 |
| SeminalVes_Dist | Anatomic | Gland | Distal Seminal Vesicle | — |
| SeminalVes_Prox | Anatomic | Gland | Proximal Seminal Vesicle | — |
| Skin_Perineum | Anatomic | Skin | 20429 | |
| Sphincter_Anal | Anatomic | Bowel | Internal Anal Sphincter | 15710 |
| SpinalCord_Sac | Anatomic | Nerve | Spinal Cord Sacral | 256623 |
| Spongiosum | Anatomic | Reproductive | Penis Corpus Spongiosum | 19617 |
| Testis | Anatomic | Reproductive | Testis | 7210 |
| Testis_L | Anatomic | Reproductive | Testis Left | 7212 |
| Testis_R | Anatomic | Reproductive | Testis Right | 7211 |
| Ureter_L | Anatomic | Urinary | Ureter Left | 17888 |
| Ureter_R | Anatomic | Urinary | Ureter Right | 17887 |
| UreterDivert | Anatomic | Urinary | Urinary Divergence | — |
| Ureters | Anatomic | Urinary | Both Ureters | 264814 |
| Urethra | Anatomic | Urinary | Urethra | 19667 |
| Urethra_Prostatc | Anatomic | Urinary | Prostatic Urethra | — |
| Uterus | Anatomic | Reproductive | Uterus | 17558 |
| V_Iliac_Ext_L | Anatomic | Vein | External iliac vein Left | 18886 |
| V_Iliac_Ext_R | Anatomic | Vein | External iliac vein Right | 18885 |
| V_Iliac_Int_L | Anatomic | Vein | Internal iliac vein Left | 18810 |
| V_Iliac_Int_R | Anatomic | Vein | Internal iliac vein Right | 18809 |
| V_Iliac_L | Anatomic | Vein | Common iliac vein Right | 21387 |
| V_Iliac_R | Anatomic | Vein | Common iliac vein Left | 21388 |
| Vagina | Anatomic | Reproductive | Vagina | 19949 |
| Vagina_Surf | Anatomic | Reproductive | — | |
| VaginalCuff | Anatomic | Reproductive | Vaginal Cuff | — |
| VB_S | Anatomic | Bone | Sacral Vertebra | 12526 |
| VB_S1 | Anatomic | Bone | Sacral Vertebra S1 | 13077 |
| VB_S2 | Anatomic | Bone | Sacral Vertebra S2 | 13078 |
| VB_S3 | Anatomic | Bone | Sacral Vertebra S3 | 13079 |
| VB_S4 | Anatomic | Bone | Sacral Vertebra S4 | 13080 |
| VB_S5 | Anatomic | Bone | Sacral Vertebra S5 | 13081 |
| Vulva | Anatomic | Reproductive | Vulva | 20462 |
| Wall_Vagina | Anatomic | Reproductive | Wall of vagina | 19971 |
Corpo / Sistêmico (Body) — 52 estruturas
| Nome TG-263 | Tipo | Categoria | Descrição | FMAID |
|---|---|---|---|---|
| Bag_Ostomy | Non_Anatomic | Devices | Ostomy Bag | — |
| Body | Anatomic | Body | Only the body | 256135 |
| Body-PTV | Derived | Body | Body minus PTV | — |
| Bolus | Non_Anatomic | Bolus | — | |
| Bolus_xxmm | Non_Anatomic | Bolus | Bolus that is xx millimeters thick e.g. Bolus_03mm, Bolus_10mm | — |
| Bone | Anatomic | Bone | Bone | 30317 |
| BoneMarrow | Anatomic | Bone | Bone Marrow | 9608 |
| BoneMarrow_Act | Anatomic | Bone | Active Bone Marrow | — |
| Boost | Non-Anatomic | Body | Boost Volume | — |
| CTV | Target | CTV | Clinical Tumor Volume | — |
| Edema | Anatomic | Skin | Edema | — |
| E-PTV_Ev05_xxxx | Non-Anatomic | Body | All tissue excluding the 5 mm expanded PTV. Generated by subtracting the 5 mm expanded PTV receiving a dose of xxxx cGy from the external contour. | — |
| E-PTV_xxxx | Non-Anatomic | Derived | All tissue excluding the PTV. Generated by subtracting the PTV receiving a dose of xxxx cGy from the external contour. | — |
| Eval | Non-Anatomic | Body | Evaluation Structure | — |
| External | Anatomic | Body | Contour encompassing body plus other external items | — |
| GrowthPlate_L | Anatomic | Bone | — | |
| GrowthPlate_R | Anatomic | Bone | — | |
| GTV | Target | GTV | Gross Tumor Volume | — |
| IDL | Non-Anatomic | Dose | Isodose Line e.g. IDL_5000 isodose line for 50 Gy | — |
| ITV | Target | ITV | Internal Target Volume | — |
| Joint_Surface | Anatomic | Joint | — | |
| Leads | Non_Anatomic | Devices | — | |
| LN | Anatomic | Lymph Node | Lymph Node | 5034 |
| LN_L | Anatomic | Lymph Node | Lymph Node Left | — |
| LN_R | Anatomic | Lymph Node | Lymph Node Right | — |
| LN_Sclav_L | Anatomic | Lymph Node | Supraclavicular Lymph Node Left | 232719 |
| LN_Sclav_R | Anatomic | Lymph Node | Supraclavicular Lymph Node Right | 232721 |
| Markers | Non_Anatomic | Devices | — | |
| Musc | Anatomic | Muscle | Muscle | 30316 |
| Nrv_Peripheral | Anatomic | Nerve | Peripheral Nerve | — |
| Nrv_Root | Anatomic | Nerve | Nerve Root | 5981 |
| Postop | Non_Anatomic | Surgery | Post operative volume | — |
| Preop | Non_Anatomic | Surgery | Region originally occupied by the gross tumor volume | — |
| Prosthesis | Anatomic | Surgery | Prosthesis | — |
| PTV | Target | PTV | Planning Target Volume | — |
| Scar | Anatomic | Skin | Scar | — |
| Scar_Boost | Anatomic | Skin | — | |
| Skin | Anatomic | Skin | Skin | 7163 |
| Spc | Anatomic | Space | Space | — |
| SpinalCanal | Anatomic | Canal | Vertebral canal | 9680 |
| SpinalCanal_PRV | PRV | PRV | — | |
| SpinalCanal_PRVx | PRV | PRV | A PRV created with an x millimeter expansion on the spinal canal | — |
| SpinalCord | Anatomic | Nerve | Spinal Cord | 7647 |
| SpinalCord_PRV | PRV | PRV | — | |
| SpinalCord_PRVxx | PRV | PRV | A PRV created with an xx millimeter expansion on the spinal cord | — |
| Strct | Anatomic | Body | Structure | — |
| SurgicalBed | Anatomic | Surgery | — | |
| ThecalSac | Anatomic | Membrane | 83720 | |
| TumorBed | Non_Anatomic | Surgery | Tumor Bed | — |
| Valve | Anatomic | Valve | Valve | — |
| VB | Anatomic | Bone | Vertebral Body | — |
| VBs | Anatomic | Bone | Vertebral Bodies | 11945 |
Membros (singular) (Limb) — 16 estruturas
| Nome TG-263 | Tipo | Categoria | Descrição | FMAID |
|---|---|---|---|---|
| A_Femoral_Cflx_L | Anatomic | Artery | Circumflex Left Femoral Artery | — |
| A_Femoral_Cflx_R | Anatomic | Artery | Circumflex Right Femoral Artery | — |
| A_Femoral_L | Anatomic | Artery | Femoral Artery Left | 70250 |
| A_Femoral_R | Anatomic | Artery | Femoral Artery Right | 70249 |
| A_Humeral_Cflx_L | Anatomic | Artery | Circumflex Humeral Artery Left | — |
| A_Humeral_Cflx_R | Anatomic | Artery | Circumflex Humeral Artery Right | — |
| A_Humeral_L | Anatomic | Artery | Humeral Artery Left | — |
| A_Humeral_R | Anatomic | Artery | Humeral Artery Right | — |
| Femur_L | Anatomic | Bone | Femur Whole Left | 24475 |
| Femur_R | Anatomic | Bone | Femur Whole Right | 24474 |
| Femurs | Anatomic | Bone | Both Femurs | 9611 |
| Radius_L | Anatomic | Bone | Radius Left | 23465 |
| Radius_R | Anatomic | Bone | Radius Right | 23464 |
| Strct_Suprapatel | Anatomic | Joint | Suprapatellar Structures | — |
| Tendon | Anatomic | Tendon | 9721 | |
| Tendon_Quad | Anatomic | Tendon | 46900 |
Membros (bilateral) (Limbs) — 17 estruturas
| Nome TG-263 | Tipo | Categoria | Descrição | FMAID |
|---|---|---|---|---|
| Elbow | Anatomic | Joint | Elbow | 24901 |
| Elbow_L | Anatomic | Joint | Elbow Left | 24903 |
| Elbow_R | Anatomic | Joint | Elbow Right | 24902 |
| Fibula | Anatomic | Bone | Fibula | 24479 |
| Fibula_L | Anatomic | Bone | Fibula Left | 24481 |
| Fibula_R | Anatomic | Bone | Fibula Right | 24480 |
| Humerus_L | Anatomic | Bone | Humerus Left | 23131 |
| Humerus_R | Anatomic | Bone | Humerus Right | 23130 |
| Joint_Elbow | Anatomic | Joint | Elbow joint | 35289 |
| Joint_Elbow_L | Anatomic | Joint | Left Elbow joint | 35295 |
| Joint_Elbow_R | Anatomic | Joint | Right Elbow joint | 35294 |
| Joint_Glenohum | Anatomic | Joint | Glenohumeral Joint | 25912 |
| Joint_Glenohum_L | Anatomic | Joint | Glenohumeral Joint Left | 25929 |
| Joint_Glenohum_R | Anatomic | Joint | Glenohumeral Joint Right | 25927 |
| Knee | Anatomic | Joint | Knee | 24974 |
| Knee_L | Anatomic | Joint | Knee Left | 24978 |
| Knee_R | Anatomic | Joint | Knee Right | 24977 |
Integração com sistemas de planejamento e inteligência artificial
A padronização de nomenclatura ganha relevância operacional quando se conecta com os sistemas que consomem e produzem nomes de estruturas no dia a dia: sistemas de planejamento de tratamento (TPS), ferramentas de auto-segmentação e plataformas de análise de dados. O TG-263 não é um documento isolado — é uma camada de interoperabilidade que permite que diferentes elos da cadeia se comuniquem sem mapeamento manual.
Por que a nomenclatura padrão importa para IA
Modelos de auto-segmentação baseados em deep learning dependem de três condições para funcionar bem: dados de treinamento volumosos, rótulos consistentes e mapeamento previsível entre a saída do modelo e as estruturas clínicas do plano de tratamento. O TG-263 atende diretamente a segunda e terceira condições.
Quando um modelo é treinado com contornos rotulados como Parotid_L em todas as instituições contribuintes, o rótulo de saída pode ser diretamente inserido no plano sem etapa de tradução. Se cada instituição usa seu próprio nome, o modelo precisa de um dicionário de sinônimos que cresce a cada novo dataset incorporado — e cada entrada ausente nesse dicionário é uma estrutura que não será mapeada corretamente na clínica.
A escala do problema fica evidente em projetos como o TCIA (The Cancer Imaging Archive) e os AAPM Grand Challenges, onde dados de dezenas de instituições são combinados para treinamento e validação. Sem nomenclatura padrão, a etapa de harmonização consome mais tempo do que o treinamento do modelo. Com o TG-263 adotado como convenção de rotulação, os dados já chegam prontos para uso.
Ferramentas que suportam nomenclatura TG-263
O ecossistema de radioterapia já oferece ferramentas que reconhecem, mapeiam ou impõe nomenclatura TG-263. A lista abaixo descreve as principais em tom educativo e neutro, sem hierarquia de preferência.
AutoSeg (RT Medical Systems) é uma plataforma de auto-segmentação que produz contornos com nomes TG-263 como saída padrão. A integração com o RTConnect permite que os contornos gerados fluam diretamente para o TPS com nomenclatura conforme, eliminando a etapa manual de renomeação. O pipeline completo — recebimento de imagem, segmentação, nomeação e entrega — respeita o padrão de ponta a ponta.
Limbus Contour combina deep learning com abordagens atlas-based para auto-contorno. A ferramenta permite configurar templates de nomenclatura que mapeiam as saídas do modelo para nomes TG-263, facilitando a integração com workflows que já seguem o padrão.
MVision AI opera como serviço cloud de auto-contorno, recebendo imagens via DICOM e retornando conjuntos de estruturas segmentadas. O sistema oferece mapeamento de nomes de saída para convenções TG-263, útil para serviços que adotam o padrão e recebem contornos de diferentes provedores.
Radformation AutoContour usa uma combinação de métodos atlas e deep learning para segmentação automática. A plataforma suporta customização de nomes de estrutura, permitindo que serviços configurem a saída para seguir a convenção TG-263 do seu template institucional.
MIM Software oferece workflows de contorno com templates de estrutura customizáveis. A capacidade de definir templates com nomes TG-263 e aplicá-los a novos casos facilita a adoção do padrão em serviços que processam volume alto de pacientes.
Varian Eclipse inclui, a partir do ARIA 13.x, um Structure Dictionary que associa nomes TG-263 a FMAIDs e sinônimos reconhecidos. Quando o físico cria uma nova estrutura, o sistema sugere o nome padrão e permite busca por sinônimo. Esse recurso reduz a barreira de adoção porque o profissional não precisa memorizar o catálogo inteiro — o sistema o orienta durante o delineamento.
Elekta Monaco suporta gerenciamento de conjuntos de estrutura e templates que podem ser configurados com nomes TG-263. A ferramenta de template permite que o serviço defina antecipadamente as estruturas esperadas para cada sítio de tratamento, impondo a nomenclatura desde a criação do plano.
RaySearch RayStation oferece capacidades de scripting via IronPython e C# que permitem construir validadores de nomenclatura. Um script pode verificar, ao salvar o plano, se todos os nomes de estrutura aderem ao padrão TG-263 e alertar o usuário caso encontre desvios. Essa abordagem transforma a nomenclatura de recomendação em regra operacional.
Impacto em Big Data e pesquisa multicêntrica
O valor acumulado da padronização aparece com mais força em escala. Quando dezenas ou centenas de instituições alimentam um repositório centralizado com dados dosimétricos e de contorno — como ocorre em Learning Health Systems, registros de desfechos e projetos de predição de toxicidade — a nomenclatura consistente é pré-requisito para que os dados sejam utilizáveis sem curadoria manual intensiva.
Projetos que analisam correlação entre dose em órgãos de risco e desfechos clínicos (modelos NTCP, por exemplo) precisam agregar DVHs de milhares de pacientes. Se cada instituição nomeia o esôfago de forma diferente, o pipeline de análise precisa de uma etapa de resolução de entidades que é trabalhosa, propensa a erros e difícil de auditar. O TG-263 elimina essa etapa ao definir Esophagus como nome canônico, universalmente reconhecido.
O mesmo princípio se aplica a competições de segmentação como os AAPM Grand Challenges e a repositórios públicos como o TCIA. A adoção do TG-263 como convenção de rotulação nesses ambientes já está em andamento e tende a se tornar requisito formal em publicações futuras. Serviços que adotam o padrão agora posicionam seus dados para participar dessas iniciativas sem retrabalho retroativo.
Fluxo de implementação em 10 passos
A Seção 13 do relatório TG-263 define um fluxo de implementação em 10 passos projetado para ser aplicável a qualquer serviço de radioterapia, independentemente de porte ou maturidade operacional. O fluxo não exige parar a operação — é um processo incremental que pode ser executado em paralelo com a rotina clínica.
Passo 1: Identificar sítios de tratamento comuns e equipe envolvida. O ponto de partida é mapear quais sítios de doença o serviço trata com mais frequência e quais profissionais participam do delineamento, planejamento e revisão para cada sítio. Esse mapeamento define o escopo inicial da adoção e evita o erro de tentar padronizar tudo de uma vez.
Passo 2: Detalhar as convenções atuais de nomenclatura. Antes de mudar qualquer nome, o serviço precisa documentar o que já usa. Essa etapa revela a real extensão da inconsistência — é comum que equipes descubram variações que não sabiam existir. Listar os nomes atualmente em uso para as estruturas mais frequentes cria a base de comparação para o padrão TG-263.
Passo 3: Baixar a lista completa do TG-263. O material suplementar do relatório, disponível no site da AAPM, contém a planilha com as 717 estruturas e todas as 9 colunas. Essa planilha é o documento de referência para todo o processo.
Passo 4: Salvar e criar uma cópia de trabalho. O serviço deve manter uma cópia intacta da planilha original e trabalhar em uma versão separada. A cópia de trabalho será customizada para a realidade do serviço; a original serve como referência imutável para consultas futuras e para novos profissionais que precisem entender o padrão.
Passo 5: Remover estruturas que o serviço não utiliza. A planilha completa contém 717 estruturas, mas nenhum serviço usa todas. Um centro especializado em cabeça e pescoço pode começar removendo estruturas de pelve e abdômen que não fazem parte da sua prática. Essa poda reduz o catálogo a um tamanho gerenciável e foca a atenção da equipe nas estruturas que realmente importam.
Passo 6: Discutir com grupos de sítio de doença e stakeholders. Cada estrutura mantida na lista deve ser validada pelos profissionais que a utilizam. Médicos precisam concordar que os nomes padrão são clinicamente adequados. Físicos precisam confirmar que os nomes são compatíveis com scripts e ferramentas existentes. Dosimetristas precisam verificar que os nomes são práticos no fluxo diário de delineamento.
Passo 7: Identificar templates e documentos que precisam de atualização. A nomenclatura não vive só no TPS. Protocolos institucionais, checklists de QA, formulários de prescrição, scripts de automação e relatórios de dosimetria podem conter nomes de estrutura. Todos precisam ser revisados para refletir o padrão adotado.
Passo 8: Desenvolver um plano de rollout faseado. A implementação mais eficaz começa por um sítio de doença (tipicamente o mais frequente), valida o padrão com casos reais e só então expande para outros sítios. Cada fase inclui treinamento, acompanhamento e ajuste antes de avançar. Tentativas de implementar todos os sítios simultaneamente costumam resultar em adesão parcial e eventual abandono.
Passo 9: Criar templates no TPS com nomes padrão. Templates de estrutura no sistema de planejamento são o mecanismo de imposição mais eficaz. Quando o físico ou dosimetrista abre um novo caso e carrega o template para “cabeça e pescoço”, todas as estruturas já vêm nomeadas conforme o TG-263. Isso elimina digitação manual e reduz dramaticamente a chance de desvio.
Passo 10: Manter a lista completa acessível para referência futura. Novos profissionais, novas modalidades e novos sítios de doença vão surgir. A planilha completa deve estar disponível em um local conhecido (rede, intranet, sistema de gestão de documentos) para que qualquer pessoa possa consultar o padrão quando precisar adicionar uma estrutura ao catálogo local.
Relação com o delineamento de volumes-alvo
A nomenclatura TG-263 não existe isolada do processo de delineamento. Pelo contrário: ela foi projetada para se integrar diretamente ao workflow de contorno, funcionando como a camada de identidade que conecta o que o médico delineia ao que o sistema de planejamento calcula e ao que o banco de dados armazena.
Quando um radioterapeuta delineia o GTV de um tumor primário de orofaringe, o TG-263 define que essa estrutura deve ser nomeada GTV_p. Se houver envolvimento nodal, os linfonodos delineados como doença macroscópica viram GTV_n. O CTV que cobre a extensão microscópica do primário será CTV_p, e o do nodal, CTV_n. O PTV gerado a partir do CTV primário com a dose mais alta será PTV_p_High ou PTV_7000 (se a dose for de 70 Gy). Cada nome carrega informação clínica que qualquer profissional treinado no padrão consegue decodificar sem consultar o prontuário.
Essa integração é particularmente valiosa em sítios de cabeça e pescoço, onde o número de estruturas por plano pode ultrapassar 40 e a distinção entre órgãos de risco, alvos primários e alvos nodais precisa ser inequívoca. Um plano de nasofaringe com três níveis de dose, múltiplos GTVs e uma densa rede de órgãos de risco se torna significativamente mais legível quando a nomenclatura segue um padrão previsível.
O mesmo princípio se aplica a todos os sítios anatômicos. No delineamento de orofaringe, a distinção entre GTV mucoso e GTV nodal é imediatamente visível nos nomes. Em laringe, onde estruturas de cartilagem como Arytenoid_L, Cricoid e Thyroid_Cart são críticas para definição de margens, os nomes TG-263 eliminam dúvidas sobre qual cartilagem está sendo referenciada. Casos de hipofaringe, cavidade oral, tumores de cavidade nasal e seios paranasais e glândulas salivares seguem a mesma lógica de nomes padronizados por região.
Em tratamentos de mama, a nomenclatura padrão facilita a distinção entre Breast_L (mama inteira como órgão) e estruturas de planejamento como zBreast_Flash. Planos de pulmão se beneficiam da clareza entre Lung_L, Lung~_L (parcial) e Lungs (bilateral), cada nome com implicação dosimétrica distinta.
Na pelve, o delineamento de próstata usa Prostate, SeminalVes, Rectum, Bladder e Femur_L/Femur_R como órgãos de risco padrão. Para câncer retal, a nomenclatura dos níveis nodais segue a convenção LN_ do TG-263, facilitando a identificação de quais cadeias linfonodais estão incluídas no CTV. O delineamento de bexiga, ginecologia definitiva, ginecologia pós-operatória e câncer anal segue a mesma lógica. No abdômen, sítios como câncer gástrico, pâncreas e carcinoma hepatocelular se beneficiam particularmente da nomenclatura padrão para estruturas vasculares como A_Celiac, V_Portal e A_Mesenteric_S.
Em cenários como metástases cerebrais tratadas com SRS, a nomenclatura dos volumes-alvo com identificação por número (GTV_1, GTV_2, PTV_1) se torna crítica para rastreabilidade. O TG-263 permite essa numeração dentro do framework de composição de nomes.
A conexão entre nomenclatura e delineamento se estende também a técnicas especiais. Em braquiterapia guiada por imagem, estruturas como Applicator, Tandem e órgãos de risco pélvicos seguem o mesmo padrão. Para esôfago, linfoma e sarcoma de partes moles, o TG-263 fornece nomes padrão para as estruturas anatômicas específicas de cada sítio. Casos de tumores malignos do SNC, tumores benignos do SNC, seminoma testicular, câncer de vulva, tireoide e irradiação nodal da mama demonstram que o padrão se aplica a todo o espectro de sítios de tratamento.
Para uma visão abrangente de como o delineamento de volumes-alvo se integra ao fluxo de trabalho em radioterapia, consulte nosso guia completo de delineamento de volume-alvo, que cobre princípios, técnicas e recomendações por sítio anatômico.
O futuro da padronização em radioterapia
O TG-263 representa o estado da arte em nomenclatura de estruturas para radioterapia, mas o campo continua evoluindo. Vários desenvolvimentos em andamento prometem expandir o alcance e a profundidade da padronização.
Integração com DICOM RT Structure Set. O padrão DICOM já suporta o conceito de Structure Set, mas a adoção de nomenclatura TG-263 como vocabulário controlado dentro do DICOM está em discussão. O Supplement 196, proposto pelo DICOM Working Group 7, define um mecanismo para incluir templates de estrutura diretamente no padrão DICOM, permitindo que sistemas interoperem não apenas no formato dos dados, mas também na semântica dos nomes. Quando esse suplemento for amplamente implementado, o nome Parotid_L em um arquivo DICOM será não apenas um rótulo, mas um identificador semântico vinculado a uma ontologia.
HL7 FHIR e interoperabilidade com prontuários. O padrão HL7 FHIR, cada vez mais adotado para troca de informações clínicas, oferece recursos para codificação de procedimentos e achados anatômicos. A ponte entre TG-263 (nomenclatura de radioterapia) e FHIR (interoperabilidade de saúde) passa pelo mapeamento de FMAIDs e códigos SNOMED CT. Esse mapeamento permite que dados de radioterapia sejam integrados ao prontuário eletrônico com semântica preservada, viabilizando consultas como “quais pacientes receberam dose > 50 Gy na parótida esquerda” diretamente no sistema de informação hospitalar.
Registros de modelos de IA. À medida que modelos de auto-segmentação proliferam, surge a necessidade de registros que documentem a nomenclatura de treinamento de cada modelo. Se um modelo foi treinado com rótulos TG-263, qualquer serviço que use o padrão pode adotá-lo sem mapeamento. Se foi treinado com rótulos proprietários, o mapeamento precisa ser documentado e validado. A tendência é que registros de modelos incluam a tabela de mapeamento TG-263 como metadado obrigatório.
Tabelas de tradução multilinguagem. O TG-263 foi publicado em inglês, mas serviços em países não anglófonos precisam de mapeamento entre nomes TG-263 e nomes locais. Tabelas de tradução que associam, por exemplo, Brainstem a “tronco encefálico” e SpinalCord a “medula espinhal” já estão em desenvolvimento em vários países. A expectativa é que a AAPM ou um grupo de trabalho internacional publique tabelas oficiais de correspondência que preservem o nome TG-263 como identificador canônico e ofereçam traduções como aliases de interface.
Sucessão do grupo de trabalho. O TG-263 original foi publicado em 2018 e cobre as estruturas anatômicas conhecidas até aquela data. Novas técnicas de tratamento, novas modalidades de imagem e novas abordagens de delineamento continuarão a demandar adições ao catálogo. A manutenção do padrão precisará de um grupo sucessor — seja vinculado a AAPM, a ASTRO ou a uma entidade conjunta — que revise periodicamente a planilha, incorpore novas estruturas e publique versões atualizadas. O modelo de governança desse grupo definirá se o TG-263 permanece um padrão vivo ou se congela na versão de 2018.
Conclusão
O TG-263 transformou a nomenclatura de estruturas em radioterapia de uma questão de preferência pessoal para um padrão técnico documentado, testado e adotável. As 717 estruturas catalogadas, os 15 princípios para órgãos de risco, os 10 princípios para volumes-alvo e a notação padronizada de DVH formam um kit completo para qualquer serviço que queira operar com consistência.
O impacto clínico é direto. Revisão de planos mais rápida. Dados históricos utilizáveis. Automação de QA confiável. Compatibilidade com modelos de auto-segmentação. Participação em estudos multicêntricos sem retrabalho. Treinamento de novos profissionais facilitado. Nenhum desses benefícios depende de tecnologia sofisticada — depende de disciplina na nomenclatura.
A implementação não precisa ser um projeto de meses. O fluxo de 10 passos do próprio relatório mostra que começar por um sítio de doença, criar templates no TPS e treinar a equipe já produz resultados tangíveis na primeira semana. A expansão para outros sítios acontece naturalmente à medida que a equipe internaliza a lógica do padrão.
Se o seu serviço ainda não adotou o TG-263, o melhor momento para começar é agora. Baixe a planilha, identifique as estruturas do seu sítio de tratamento mais frequente e crie o primeiro template padronizado. A RT Medical Systems oferece ferramentas como o AutoSeg e o RTConnect que integram a nomenclatura TG-263 diretamente no fluxo clínico — da segmentação automática até a entrega do contorno no TPS, com nomes conformes desde a origem. Se precisar de suporte nessa jornada, nossa equipe está disponível para avaliar o cenário do seu serviço e propor um plano de adoção personalizado.