- 1. El TG-263 y el lenguaje común de la radioterapia
- 2. Que es el TG-263
- 3. Problemas reales causados por la falta de estandarización
- 4. Como aplicar el TG-263 en la rutina clínica
- 5. Tabla completa de nomenclatura TG-263 717 estructuras
- 6. Integración con sistemas de planificación e inteligencia artificial
- 7. Flujo de implementación en 10 pasos
- 8. Relación con la delineación de volúmenes blanco
- 9. El futuro de la estandarización en radioterapia
- 10. Conclusión
El TG-263 y el lenguaje común de la radioterapia
Un físico médico recibe un plan de tratamiento exportado desde otra institución. Al abrir el archivo DICOM, encuentra la parotida izquierda nombrada como Lt Parotid. En el caso siguiente, proveniente del mismo servicio, el nombre aparece como PAROTID_L. En un tercer paciente, parotid_left. Y en el template del propio servicio receptor, la misma estructura figura como L_Parotid_Gland. Cinco nombres diferentes para el mismo órgano de riesgo, dentro de un universo relativamente pequeño de casos.
Este escenario no es hipotético. Reproduce datos reales recopilados por la AAPM antes de la publicación del TG-263. En 20 instituciones encuestadas, el equipo encontró entre 21 y 311 nombres definidos para estructuras anatómicas, con variaciones que iban desde abreviaturas personales hasta convenciones enteras creadas por un único profesional y nunca documentadas formalmente.
El problema parece menor cuando se observa un caso aislado. Pero se acumula rápidamente. Cuando el servicio intenta automatizar la revisión de DVH, entrenar un modelo de auto-segmentación, consolidar datos para un estudio multicéntrico o simplemente comparar planes entre pacientes tratados en años diferentes, la falta de estandarización se transforma en retrabajo constante. Cada análisis requiere una etapa previa de «traducción» que consume tiempo, introduce errores e impide la automatización real.
La AAPM reconoció este cuello de botella y, en 2012, conformo el Task Group 263 con un mandato claro: crear un estándar de nomenclatura para estructuras anatómicas, volúmenes blanco y métricas de DVH que pudiera ser adoptado por cualquier servicio de radioterapia, independientemente del fabricante, pais o escala operacional. El grupo reunio 57 participantes — 33 físicos hospitalarios, 15 médicos radioterapeutas, 8 representantes de fabricantes y 1 dosimetrista — y trabajó durante cinco años hasta la publicación del informe en enero de 2018.
El resultado no es simplemente una lista de nombres. El TG-263 define principios de construcción de nomenclatura, reglas de lateralidad, convenciones para volúmenes blanco y sus niveles de dosis, notación estandarizada para métricas dosimétricas y un flujo de implementación en 10 pasos que permite a cualquier departamento adoptar el estándar sin interrumpir la operación clínica.
Esta guia cubre el contenido completo del informe, incluye la tabla integral con las 717 estructuras no blanco catalogadas, explica como los principios se aplican en la práctica diaria y detalla la integración con sistemas de planificación, herramientas de inteligencia artificial y flujos de trabajo de investigación multicéntrica. El objetivo es funcionar como la referencia en español para cualquier profesional que necesite implementar, auditar o expandir la nomenclatura TG-263 en su servicio.
Que es el TG-263
El Task Group 263 de la AAPM (American Association of Physicists in Medicine) surgió de la constatación de que la radioterapia necesitaba un vocabulario técnico compartido para nombrar estructuras anatómicas en los sistemas de planificación de tratamiento. Antes de este estándar, cada institución desarrollaba sus propias convenciones — cuando las desarrollaba. El resultado era una fragmentación que dificultaba cualquier actividad que dependiera de datos consistentes entre pacientes, equipos o centros.
El grupo fue formalmente constituido en 2012 con miembros designados tanto por la AAPM como por la ASTRO (American Society for Radiation Oncology). La composición final incluyo 39 miembros de la AAPM y 41 de la ASTRO, con superposición entre las dos sociedades, totalizando 57 participantes únicos. La diversidad del grupo no fue accidental: la presencia de físicos, médicos, dosimetristas y representantes de fabricantes garantizó que el estándar fuera viable tanto desde el punto de vista clínico como tecnológico.
El informe fue publicado en enero de 2018 como AAPM Report No. 263, acompañado por una publicación peer-reviewed en Medical Physics (el artículo S0360 de 2018). El documento principal define los principios; el material suplementario, disponible en el sitio de la AAPM, contiene la planilla completa con todas las estructuras catalogadas.
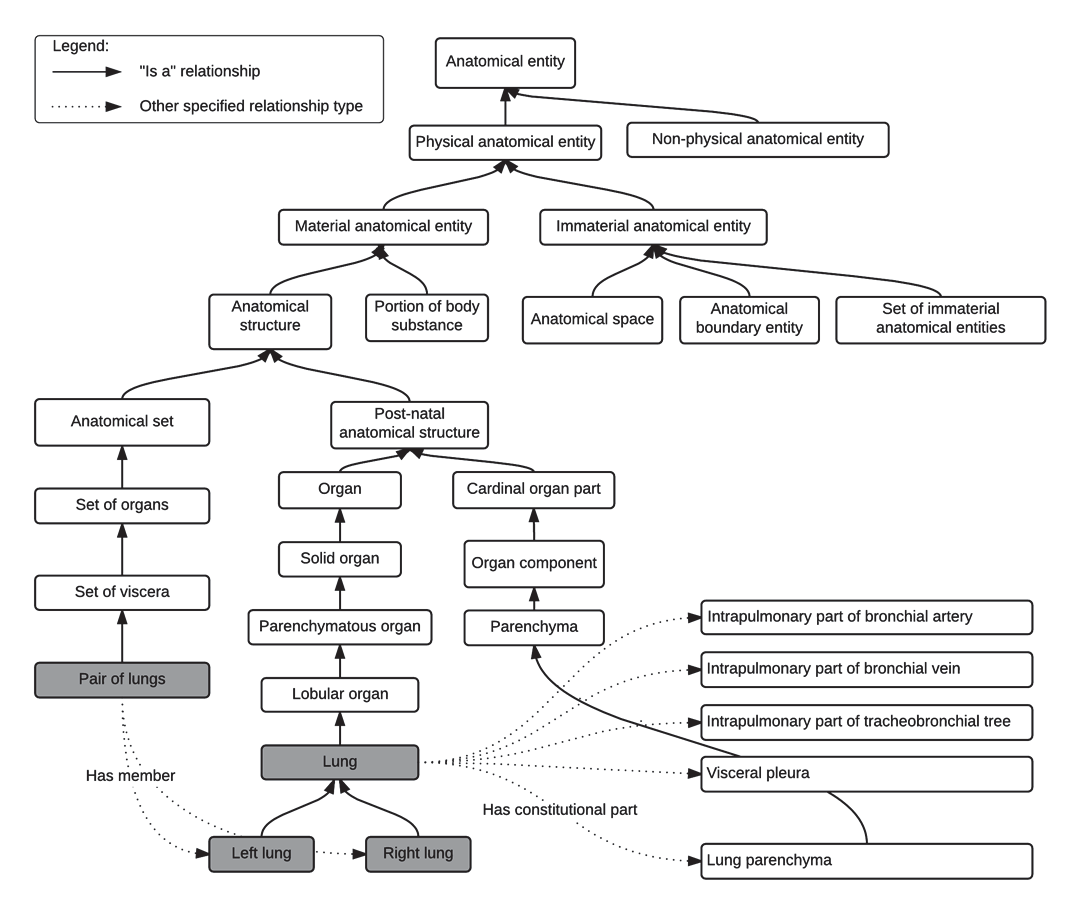
La estructura de la planilla
El núcleo del TG-263 es una planilla organizada en 9 columnas que clasifican cada estructura de forma sistemática. Esta organización no es arbitraria — cada columna cumple un propósito específico en la cadena de uso clínico e informático:
Target Type distingue si la estructura es anatómica, un volumen blanco (GTV, CTV, PTV), un PRV o una estructura derivada para planificación. Major Category agrupa por sistema anatómico amplio — hueso, nervio, órgano, vaso, ganglio linfático. Minor Category refina esa agrupación con subcategorias más específicas. Anatomic Group indica la región corporal: cabeza y cuello, torax, abdomen, pelvis, cuerpo, miembro.
N Characters registra la longitud del nombre estandarizado, información crítica porque el TG-263 recomienda un límite máximo de 16 caracteres para garantizar compatibilidad con sistemas legados y campos de interfaz. TG263-Primary Name es el nombre principal que debe usarse en el sistema de planificación — por ejemplo, Parotid_L para la parotida izquierda. TG-263-Reverse Order Name ofrece una versión invertida (L_Parotid) para facilitar la busqueda y ordenación en listas extensas.
Description proporciona el nombre anatómico completo sin abreviaturas. FMAID mapea la estructura al Foundational Model of Anatomy, una ontología anatómica mantenida por la Universidad de Washington que permite interoperabilidad con SNOMED CT, DICOM y otros estándares informáticos en salud.
Primary Name versus Reverse Order Name
La distinción entre estos dos campos es uno de los conceptos más importantes del TG-263 y frecuentemente mal comprendida. El Primary Name sigue la lógica Estructura_Lateralidad — por ejemplo, Kidney_L, Femur_R, CN_VII_L. Este formato facilita la lectura humana y sigue la convención natural de nombrar primero la estructura y luego calificarla.
El Reverse Order Name invierte a Lateralidad_Estructura — L_Kidney, R_Femur, L_CN_VII. Este formato es útil cuando la lista de estructuras necesita ser ordenada alfabeticamente por lateralidad, agrupando todas las estructuras izquierdas y todas las derechas juntas. Algunos sistemas de planificación y herramientas de análisis se benefician de esta ordenación para revisión rápida.
El TG-263 recomienda que el Primary Name sea usado como nombre preferencial en el TPS. El Reverse Order Name existe como alternativa documentada, no como sustituto. Los servicios que adoptan el estándar deben elegir una de las convenciones y aplicarla de forma consistente en toda la operación.
Alcance: 717 estructuras no blanco
La planilla cataloga 717 estructuras no blanco, organizadas en 7 grupos anatómicos: Cabeza y Cuello (282), Torax (180), Abdomen (60), Pelvis (109), Cuerpo/Sistémico (52), Miembro singular (16) y Miembros bilaterales (17). Este catálogo cubre practicamente toda estructura anatómica que un servicio de radioterapia encuentra en la práctica clínica, desde huesos y nervios craneales hasta vasos, ganglios linfáticos, órganos abdominales y estructuras pélvicas.
Además de las estructuras anatómicas, el TG-263 define convenciones separadas para volúmenes blanco (GTV, CTV, ITV, PTV y sus variantes), estructuras de planificación (PRV, estructuras auxiliares con prefijo z), y métricas dosimétricas (DVH). Estos tres dominios siguen principios propios, detallados en las secciones siguientes de esta guia.
Problemas reales causados por la falta de estandarización
El TG-263 no surgió de una preocupación teórica. Antes de definir cualquier estándar, el grupo realizo un relevamiento en 20 instituciones norteamericanas para documentar el estado real de la nomenclatura en radioterapia. Los resultados fueron reveladores.
De las 20 instituciones encuestadas, 16 declararon tener alguna forma de nomenclatura definida para al menos algunos sitios de enfermedad. Pero «tener nomenclatura» no significaba tener consistencia. El número de estructuras definidas variaba de 21 a 311 entre las instituciones, y dentro de cada una habia variaciones entre profesionales, entre salas y entre períodos. Ninguna de las 20 cubria todas las estructuras anatómicas necesarias para todas las modalidades de tratamiento.
El ejemplo más citado en el informe es el del nervio óptico izquierdo. Al recopilar los nombres usados por las instituciones encuestadas, el grupo encontró 12 variantes para una única estructura: Lt Optic Nerve, L_Optic_Nerve, OpticNrv_L, Optic_Nerve_Left, entre otras. Cada variante era internamente lógica para quien la creo, pero incompatible con las demas cuando los datos necesitaban ser combinados.
Impacto en la mineria de datos
Un servicio que acumula 10 años de planes de tratamiento posee un acervo valioso para investigación, benchmarking y mejora de calidad. Pero si esos planes usan nombres inconsistentes para las mismas estructuras, cualquier consulta a la base de datos se convierte en un ejercicio de mapeo manual. Extraer «todas las dosis medias en la medula espinal» exige primero identificar si la medula fue nombrada como SpinalCord, Spinal_Cord, SC, MedulaEspinal, Cord o cualquier otra variación local.
Este costo de mapeo no es trivial. En estudios multicéntricos con miles de pacientes, la etapa de armonización de nomenclatura puede consumir semanas de trabajo y aun así contener errores. El TG-263 elimina este problema en el origen: si todos los centros usan SpinalCord, la consulta a la base de datos retorna resultados completos sin intervención manual.
Impacto en la auto-segmentación e IA
Los modelos de deep learning para auto-segmentación necesitan datos de entrenamiento etiquetados de forma consistente. Un modelo entrenado con contornos etiquetados como Parotid_L no puede usar automaticamente datos etiquetados como Lt_Parotid_Gland — el mapeo debe realizarse manualmente para cada variante, y cualquier error en ese mapeo contamina el entrenamiento.
Cuando un servicio adopta la nomenclatura TG-263, sus datos se vuelven inmediatamente compatibles con modelos entrenados en otros servicios que siguen el mismo estándar. Esto acelera la adopción de la auto-segmentación, mejora la calidad del entrenamiento al permitir datasets mayores y viabiliza la validación cruzada entre instituciones.
Impacto en la automatización de QA
Los protocolos automatizados de garantía de calidad dependen de nombres predecibles. Un script que verifica si la dosis máxima en el cristalino no excede el límite institucional necesita saber exactamente como esta nombrado el cristalino. Si el nombre cambia entre Lens_L, L_Lens, Left_Lens y Cristalino_I, el script necesita una tabla de sinónimos que crece con cada nueva variante encontrada — o, peor, falla silenciosamente cuando encuentra un nombre no catalogado.
El TG-263 permite que las herramientas de QA sean escritas una vez y funcionen en cualquier servicio adherente. La predecibilidad de los nombres es la base para una automatización confiable.
Impacto en estudios multicéntricos y ensayos clínicos
Los ensayos clínicos de radioterapia que recolectan datos dosimétricos de múltiples instituciones enfrentan el problema de nomenclatura a escala. El RTOG (ahora NRG Oncology) público directrices de nomenclatura para estudios específicos, pero sin un estándar universal adoptado por la comunidad, cada nuevo ensayo repetia el mismo ciclo de definición, comunicación y verificación. El TG-263 ofrece una base permanente que reduce esta sobrecarga para cualquier ensayo futuro.
Como aplicar el TG-263 en la rutina clínica
El TG-263 define dos conjuntos de principios: 15 para estructuras no blanco (órganos de riesgo y estructuras anatómicas) y 10 para volúmenes blanco. Además, estandariza la notación de métricas dosimétricas. Cada conjunto fue diseñado para resolver problemas específicos de la práctica clínica.
Principios para estructuras no blanco
Límite de 16 caracteres. El nombre estandarizado no debe exceder 16 caracteres. Este límite no es arbitrario — refleja restricciones reales de campos de interfaz en sistemas de planificación legados y contemporaneos. Los nombres más largos son truncados por algunos TPS, generando ambigüedad. El límite fuerza concisión e impide la proliferación de nombres descriptivos largos que nadie digita de forma idéntica dos veces.
Unicidad por case. Cada nombre debe ser único independientemente de mayusculas y minusculas. Brainstem y brainstem no pueden coexistir como estructuras distintas. Esta regla previene errores en sistemas que ignoran case en la busqueda u ordenación.
Sin espacios, underscore como separador. Los espacios estan prohibidos en los nombres TG-263. El separador estándar es el underscore (_). Así, Optic_Nerve_L y no Optic Nerve L. Esta convención evita problemas con parsers, scripts e interfaces que tratan los espacios como delimitadores de campo.
Sufijos de lateralidad: _L, _R, _A, _P. Las estructuras lateralizadas reciben el sufijo correspondiente al final del nombre. El estándar usa letras únicas para izquierda (_L), derecha (_R), anterior (_A) y posterior (_P). Las estructuras bilaterales sin lateralidad definida usan el plural — por ejemplo, Kidneys para ambos riñones, Kidney_L y Kidney_R para cada uno individualmente.
Raices de categoria. Las estructuras de categorias específicas usan prefijos estandarizados que facilitan la agrupación y busqueda:
A_ para arterias (A_Carotid_L), V_ para venas (V_Jugular_R), LN_ para ganglios linfáticos (LN_Ax_L1_L), CN_ para nervios craneales (CN_VII_L), Bone_ para huesos (Bone_Mandible), Musc_ para musculos (Musc_Masseter_L). Estos prefijos garantizan que todas las arterias queden agrupadas en la lista, todos los ganglios linfáticos juntos, y así sucesivamente.
Estructuras PRV. Los Planning Risk Volumes (PRV) siguen la convención Estructura_PRV para margen genérico o Estructura_PRVxx donde xx indica el margen en milimetros. Ejemplos: Brainstem_PRV para un PRV del tronco encefálico con margen no especificado, SpinalCord_PRV05 para un PRV de la medula con expansión de 5 mm. Esta convención permite que cualquier profesional identifique inmediatamente la estructura base y el margen aplicado sin consultar documentación externa.
Estructuras parciales: la tilde (~). Cuando solo parte de una estructura es delineada, el TG-263 usa la tilde como sufijo: Brain~ para cerebro parcial, Lung~_L para pulmon izquierdo parcial. Esta situación es común en tratamientos donde el campo de adquisición o de tratamiento no cubre la estructura completa — la tilde señala explicitamente que la cobertura es incompleta, evitando que las métricas de DVH sean interpretadas como representativas del órgano entero.
Estructuras de planificación: prefijo z. Las estructuras creadas exclusivamente para optimización de plan — anillos, estructuras de sustracción, auxiliares de dosis — reciben el prefijo z para quedar al final de la lista alfabética y no mezclarse con estructuras anatómicas reales. Ejemplos: zPTVopt, zRing, zBolus. La convención es simple y eficaz: cuando un físico recorre la lista de estructuras, todo lo que comienza con z es auxiliar de planificación y puede ser filtrado o ignorado según el contexto.
Principios para volúmenes blanco
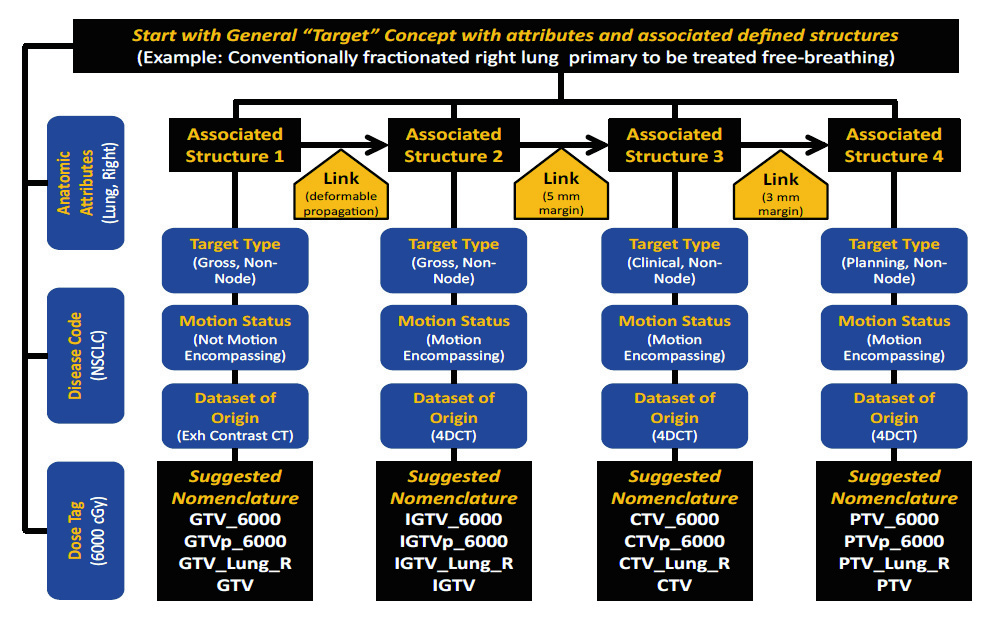
La nomenclatura de volúmenes blanco sigue 10 principios construidos para reflejar la jerarquía clínica entre volumen bruto de enfermedad, volumen clínico, margenes internos y volumen de planificación.
Tipos de volumen. El TG-263 define los siguientes tipos: GTV (Gross Tumor Volume), CTV (Clinical Target Volume), ITV (Internal Target Volume), IGTV (Internal Gross Target Volume), ICTV (Internal Clinical Target Volume), PTV (Planning Target Volume) y PTV! (PTV de evaluación, desvinculado de restricciones de optimización). Cada tipo ocupa una posición precisa en la cadena de derivación clínica.
Clasificadores. Los volúmenes pueden recibir clasificadores que indican la naturaleza de la enfermedad: n para nodal (GTV_n), p para primario (CTV_p), sb para lecho quirúrgico (CTV_sb), par para parenquimatoso. Estos clasificadores se combinan con el tipo de volumen y permiten identificar el origen clínico sin ambigüedad. Un plan con GTV_p, GTV_n, CTV_p y CTV_n comunica en cuatro nombres toda la estrategia de cobertura del tumor primario y de la enfermedad nodal.
Niveles de dosis. Cuando el plan prescribe dosis diferentes para volúmenes distintos, el TG-263 permite indicar el nivel en el nombre: PTV_High, PTV_Low, PTV_Mid para niveles relativos, o PTV_5040 para dosis absoluta en cGy. Esta convención es particularmente útil en planes SIB (Simultaneous Integrated Boost), donde tres o más niveles de dosis coexisten y la claridad sobre cual PTV recibe cual prescripción es crítica para la seguridad del tratamiento.
Composición de nombres blanco. Los elementos se combinan en una lógica predecible: Tipo_Clasificador_NivelDosis. Así, PTV_n_High identifica inequivocamente el volumen de planificación nodal que recibe la dosis más alta. CTV_sb_Low es el volumen clínico del lecho quirúrgico en el nivel de dosis baja. La composición es modular y extensible sin violar las reglas de construcción.
Nomenclatura de métricas dosimétricas (DVH)

El TG-263 estandariza la forma de escribir métricas de DVH para eliminar ambigüedad. La notación sigue el formato MetricaValorUnidad[UnidadResultado]:
V20Gy[%] — volumen que recibe al menos 20 Gy, expresado en porcentaje. V20Gy[cc] — el mismo volumen, expresado en centimetros cúbicos. D0.1cc[Gy] — dosis que cubre al menos 0,1 cc del volumen, en Gy. D95%[Gy] — dosis en el punto que cubre el 95% del volumen. Mean[Gy] — dosis media en el volumen. Max[Gy] — dosis máxima puntual.
Esta notación resuelve un problema crónico: la misma métrica escrita de formas diferentes (V20, V_20Gy, V20_pct, Vol_20Gy_%) en informes, protocolos y scripts. Con el estándar TG-263, un script que calcula V20Gy[%] produce una salida legible por cualquier otro script o profesional que conozca la convención.
Tabla completa de nomenclatura TG-263
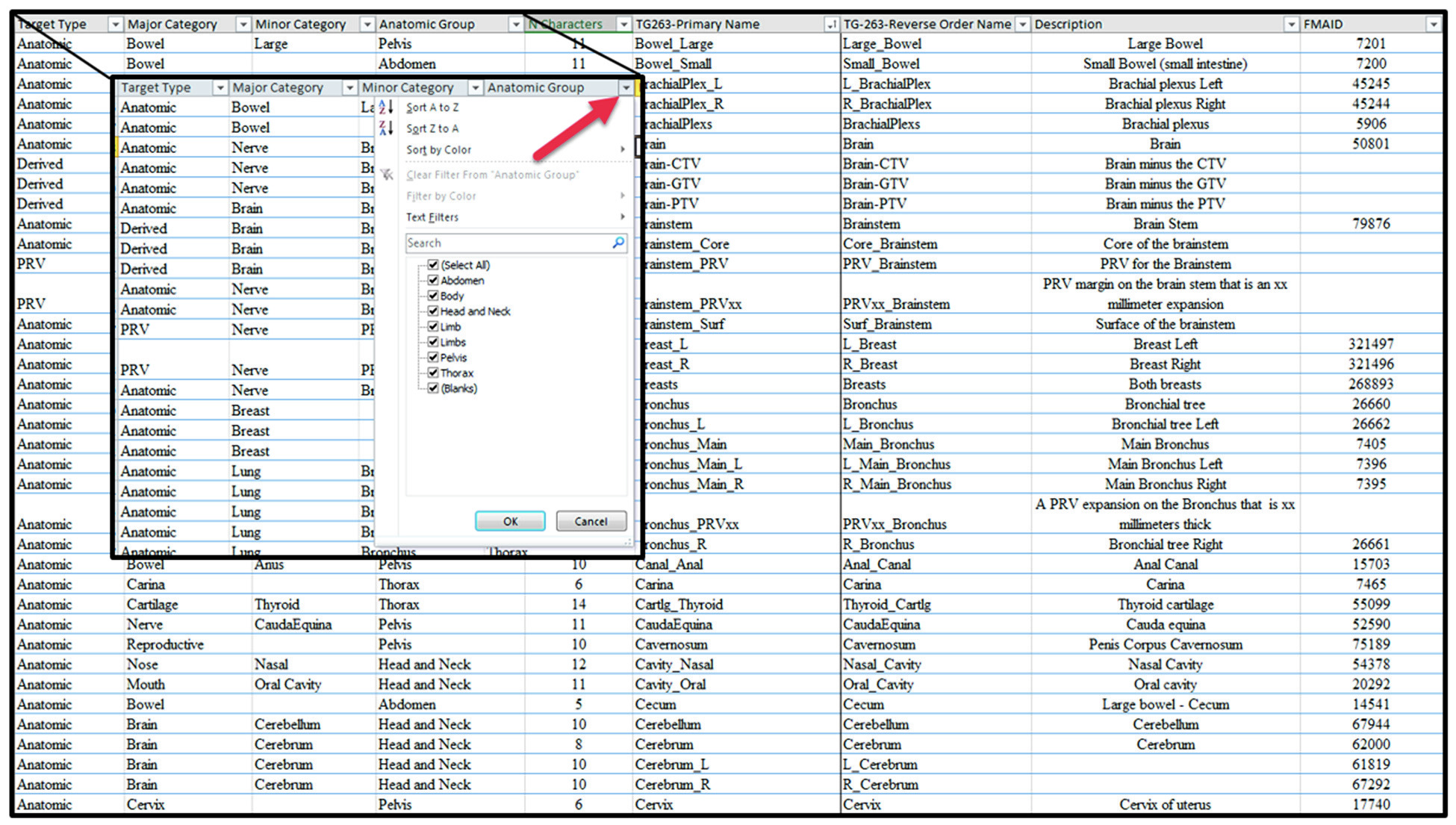
La tabla a continuación reune las 717 estructuras no blanco catalogadas por el TG-263, organizadas en 7 grupos anatómicos. Utilice el campo de busqueda para localizar rápidamente cualquier estructura por nombre, categoria o región. Los nombres siguen el formato TG263-Primary Name de la planilla oficial; la columna FMAID indica el identificador en el Foundational Model of Anatomy cuando esta disponible.
Cabeza y Cuello (Head and Neck) — 282 estructuras
| Nombre TG-263 | Tipo | Categoria | Descripción | FMAID |
|---|---|---|---|---|
| A_Carotid | Anatomic | Artery | Common Carotid Artery | 3939 |
| A_Carotid_L | Anatomic | Artery | Carotid Artery | 4058 |
| A_Carotid_R | Anatomic | Artery | Carotid Artery | 3941 |
| A_Coronary | Anatomic | Artery | Coronary Artery | 49893 |
| A_Hypophyseal_I | Anatomic | Artery | Hypophyseal Artery Inferior | 49846 |
| A_Hypophyseal_S | Anatomic | Artery | Hypophyseal Artery Superior | 49849 |
| Arytenoid | Anatomic | Cartilage | Arytenoid cartilage | 55109 |
| Arytenoid_L | Anatomic | Cartilage | Arytenoid cartilage Left | 55114 |
| Arytenoid_R | Anatomic | Cartilage | Arytenoid cartilage Right | 55113 |
| Bone_Ethmoid | Anatomic | Bone | Ethmoid Bone | 52740 |
| Bone_Frontal | Anatomic | Bone | Frontal Bone | 52734 |
| Bone_Hyoid | Anatomic | Bone | Hyoid Bone | 52749 |
| Bone_Incus | Anatomic | Ear | Incus | 52752 |
| Bone_Incus_L | Anatomic | Ear | Incus Left | 74051 |
| Bone_Incus_R | Anatomic | Ear | Incus Right | 74050 |
| Bone_Lacrimal | Anatomic | Bone | Lacrimal Bone | 52741 |
| Bone_Lacrimal_L | Anatomic | Bone | Lacrimal Bone Left | 53646 |
| Bone_Lacrimal_R | Anatomic | Bone | Lacrimal Bone Right | 53645 |
| Bone_Mandible | Anatomic | Bone | Mandible | 52748 |
| Bone_Mastoid | Anatomic | Bone | Both Mastoids | 52872 |
| Bone_Mastoid_L | Anatomic | Bone | Left Mastoid Bone | 52874 |
| Bone_Mastoid_R | Anatomic | Bone | Right Mastoid Bone | 52873 |
| Bone_Nasal | Anatomic | Bone | Nasal Bone | 52745 |
| Bone_Nasal_L | Anatomic | Bone | Nasal Bone Left | 53648 |
| Bone_Nasal_R | Anatomic | Bone | Nasal Bone Right | 53647 |
| Bone_Occipital | Anatomic | Bone | Occipital Bone | 52735 |
| Bone_Palatine | Anatomic | Bone | Palatine bone | 52746 |
| Bone_Palatine_L | Anatomic | Bone | Palatine bone Left | 53656 |
| Bone_Palatine_R | Anatomic | Bone | Palatine bone Right | 53655 |
| Bone_Parietal | Anatomic | Bone | Parietal bone | 9613 |
| Bone_Parietal_L | Anatomic | Bone | Parietal bone Left | 52789 |
| Bone_Parietal_R | Anatomic | Bone | Parietal bone Right | 52788 |
| Bone_Sphenoid | Anatomic | Bone | Sphenoid Bone | 52736 |
| Bone_Temporal | Anatomic | Bone | Temporal Bone | 52737 |
| Bone_Temporal_L | Anatomic | Bone | Temporal Bone Left | 52739 |
| Bone_Temporal_R | Anatomic | Brain | Temporal Bone Right | 52738 |
| Bone_Zygomatic_L | Anatomic | Bone | Zygomatic Bone Left | 52893 |
| Bone_Zygomatic_R | Anatomic | Bone | Zygomatic Bone Right | 52892 |
| Bone_Zygomatics | Anatomic | Bone | Zygomatic Bone | 52747 |
| Brain | Anatomic | Brain | Brain | 50801 |
| Brain-CTV | Derived | Brain | Brain minus the CTV | — |
| Brain-GTV | Derived | Brain | Brain minus the GTV | — |
| Brain-PTV | Derived | Brain | Brain minus the PTV | — |
| Brainstem | Anatomic | Nerve | Brain Stem | 79876 |
| Brainstem_Core | Anatomic | Nerve | Core of the brainstem | — |
| Brainstem_PRV | PRV | Nerve | PRV for the Brainstem | — |
| Brainstem_PRVxx | PRV | Nerve | PRV margin on the brain stem that is an xx millimeter expansión | — |
| Brainstem_Surf | Anatomic | Nerve | Surface of the brainstem | — |
| Cavity_Nasal | Anatomic | Nose | Nasal Cavity | 54378 |
| Cavity_Oral | Anatomic | Mouth | Oral cavity | 20292 |
| Cerebellum | Anatomic | Brain | Cerebellum | 67944 |
| Cerebrum | Anatomic | Brain | Cerebrum | 62000 |
| Cerebrum_L | Anatomic | Brain | 61819 | |
| Cerebrum_R | Anatomic | Brain | 67292 | |
| Cist_Pontine | Anatomic | Brain | Pontine Cistern | 83719 |
| Cist_Suprasellar | Anatomic | Brain | — | |
| CN_III | Anatomic | Nerve | Third Cranial Nerve (Oculomotor nerve) | 50864 |
| CN_III_L | Anatomic | Nerve | Third Cranial Nerve (Oculomotor nerve) Left | 50880 |
| CN_III_R | Anatomic | Nerve | Third Cranial Nerve (Oculomotor nerve) Right | 50879 |
| CN_IX | Anatomic | Nerve | Ninth Cranial Nerve (Glossopharyngeal nerve) | 50870 |
| CN_IX_L | Anatomic | Nerve | Ninth Cranial Nerve (Glossopharyngeal nerve) Left | 50892 |
| CN_IX_R | Anatomic | Nerve | Ninth Cranial Nerve (Glossopharyngeal nerve) Right | 50870 |
| CN_V | Anatomic | Nerve | Fifth Cranial Nerve (Trigeminal nerve) | 50866 |
| CN_V_L | Anatomic | Nerve | Fifth Cranial Nerve (Trigeminal nerve) Left | 50885 |
| CN_V_R | Anatomic | Nerve | Fifth Cranial Nerve (Trigeminal nerve) Right | 50884 |
| CN_VI | Anatomic | Nerve | Sixth Cranial Nerve (Abducens nerve) | 50867 |
| CN_VI_L | Anatomic | Nerve | Sixth Cranial Nerve (Abducens nerve) Left | 50887 |
| CN_VI_R | Anatomic | Nerve | Sixth Cranial Nerve (Abducens nerve) Right | 50886 |
| CN_VII | Anatomic | Nerve | Seventh Cranial Nerve (Facial) | 50868 |
| CN_VII_L | Anatomic | Nerve | Seventh Cranial Nerve (Facial) Left | 50889 |
| CN_VII_R | Anatomic | Nerve | Seventh Cranial Nerve (Facial) Right | 50888 |
| CN_VIII | Anatomic | Nerve | Eighth Cranial (Vestibulocochlear) Nerve | 50869 |
| CN_VIII_L | Anatomic | Nerve | Eighth Cranial (Vestibulocochlear) Nerve Left | 50891 |
| CN_VIII_R | Anatomic | Nerve | Eighth Cranial (Vestibulocochlear) Nerve Right | 50890 |
| CN_XI | Anatomic | Nerve | Eleventh Cranial Nerve (Spinal accessory nerve) | 6720 |
| CN_XI_L | Anatomic | Nerve | Eleventh Cranial Nerve (Spinal accessory nerve) Left | 50899 |
| CN_XI_R | Anatomic | Nerve | Eleventh Cranial Nerve (Spinal accessory nerve) Right | 50897 |
| CN_XII | Anatomic | Nerve | Twelfth Cranial Nerve (Hypoglossal nerve) | 50871 |
| CN_XII_L | Anatomic | Nerve | Twelfth Cranial Nerve (Hypoglossal nerve) Left | 50903 |
| CN_XII_R | Anatomic | Nerve | Twelfth Cranial Nerve (Hypoglossal nerve) Right | 50901 |
| Cochlea | Anatomic | Ear | Cochlea | 60201 |
| Cochlea_L | Anatomic | Ear | Left Cochlea | 60203 |
| Cochlea_R | Anatomic | Ear | Right Cochlea | 60202 |
| Cornea | Anatomic | Eye | Cornea | 58238 |
| Cornea_L | Anatomic | Eye | Cornea Left | 58240 |
| Cornea_R | Anatomic | Eye | Cornea Right | 58239 |
| CribriformPlate | Anatomic | Bone | Cribriform Plate | 52890 |
| Cricoid | Anatomic | Cartilage | Cricoid cartilage | 9615 |
| Cricopharyngeus | Anatomic | Pharynx | Cricopharyngeal part of inferior pharyngeal constrictor | 46661 |
| Dens | Anatomic | Bone | Cervical vertebrae – Bony part of dens of axis | 24043 |
| Ear_External_L | Anatomic | Ear | External Ear Left | 53644 |
| Ear_External_R | Anatomic | Ear | External Ear Right | 53643 |
| Ear_Externals | Anatomic | Ear | External Ear | 52781 |
| Ear_Internal_L | Anatomic | Ear | Internal Ear Left | 61021 |
| Ear_Internal_R | Anatomic | Ear | Internal Ear Right | 61020 |
| Ear_Internals | Anatomic | Ear | Internal Ear | 60909 |
| Ear_Middle | Anatomic | Ear | Middle Ear | 56513 |
| Ear_Middle_L | Anatomic | Ear | Middle Ear Left | 56515 |
| Ear_Middle_R | Anatomic | Ear | Middle Ear Right | 56514 |
| Eye_L | Anatomic | Eye | Eyeball Left | 12515 |
| Eye_R | Anatomic | Eye | Eyeball Right | 12514 |
| Eyes | Anatomic | Eye | Set of eyes | 268861 |
| Fossa_Jugular | Anatomic | Bone | Jugular Fossa | 56429 |
| Fossa_Posterior | Anatomic | Bone | Posterior Fossa | 54368 |
| Glnd_Lacrimal | Anatomic | Gland | Lacrimal Gland | 59101 |
| Glnd_Lacrimal_L | Anatomic | Gland | Lacrimal Gland Left | 59103 |
| Glnd_Lacrimal_R | Anatomic | Gland | Lacrimal Gland Right | 59102 |
| Glnd_Subling_L | Anatomic | Gland | Sublingual gland | 59805 |
| Glnd_Subling_R | Anatomic | Gland | Sublingual gland | 59804 |
| Glnd_Sublings | Anatomic | Gland | Sublingual gland | 320440 |
| Glnd_Submand_L | Anatomic | Gland | Submandibular Gland Left | 59803 |
| Glnd_Submand_R | Anatomic | Gland | Submandibular Gland Right | 59802 |
| Glnd_Submands | Anatomic | Gland | Submandibular Gland | 320442 |
| Glottis | Anatomic | Glottis | Glottis | 55414 |
| Hardpalate | Anatomic | Head | Hard palate | 55023 |
| Hemisphere_L | Anatomic | Brain | 61819 | |
| Hemisphere_R | Anatomic | Brain | 67292 | |
| Hemispheres | Anatomic | Brain | — | |
| Hippocampi | Anatomic | Brain | Hippocampus | 275020 |
| Hippocampus_L | Anatomic | Brain | Hippocampus Left | 275024 |
| Hippocampus_R | Anatomic | Brain | Hippocampus Right | 275022 |
| Hypothalmus | Anatomic | Brain | Hypothalamus | 62008 |
| Hypothalmus_PRV | PRV | Brain | — | |
| Hypothalmus_PRVx | PRV | Brain | — | |
| Joint_TM | Anatomic | Joint | Temperomandibular Joint | 54832 |
| Joint_TM_L | Anatomic | Joint | Temperomandibular Joint Left | 54834 |
| Joint_TM_R | Anatomic | Joint | Temperomandibular Joint Right | 54833 |
| Laryngl_Pharynx | Anatomic | Tissue | Laryngeal pharynx | 54880 |
| Larynx | Anatomic | Larynx | Larynx | 55097 |
| Larynx_SG | Anatomic | Larynx | Supraglottic Larynx | 55476 |
| Lens | Anatomic | Eye | Eye Lens | 58241 |
| Lens_L | Anatomic | Eye | Lens Left | 58243 |
| Lens_R | Anatomic | Eye | Lens Right | 58242 |
| Lips | Anatomic | Feature | Lips | 59815 |
| LN_Neck_IA_L | Anatomic | Lymph Node | Level IA (Submental) neck node Left | 235616 |
| LN_Neck_IA_R | Anatomic | Lymph Node | Level IA (Submental) neck node Right | 235614 |
| LN_Neck_IB_L | Anatomic | Lymph Node | Level IB (Submandibular) neck node Left | 232676 |
| LN_Neck_IB_R | Anatomic | Lymph Node | Level IB (Submandibular) neck node Right | 232673 |
| LN_Neck_II_L | Anatomic | Lymph Node | Level IIA & IIB (Upper Jugular) neck nodes Left | 265660 |
| LN_Neck_II_R | Anatomic | Lymph Node | Level IIA & IIB (Upper Jugular) neck nodes Left | 265658 |
| LN_Neck_IIA_L | Anatomic | Lymph Node | Level IIA (Upper Jugular) neck node Left | 241975 |
| LN_Neck_IIA_R | Anatomic | Lymph Node | Level IIA (Upper Jugular) neck node Right | 241973 |
| LN_Neck_IIB_L | Anatomic | Lymph Node | Level IIB (Upper Jugular) neck node Left | 241979 |
| LN_Neck_IIB_R | Anatomic | Lymph Node | Level IIB (Upper Jugular) neck node Right | 241977 |
| LN_Neck_III_L | Anatomic | Lymph Node | Level III (Middle Jugular) neck node Left | 241953 |
| LN_Neck_III_R | Anatomic | Lymph Node | Level III (Middle Jugular) neck node Right | 241951 |
| LN_Neck_IV_L | Anatomic | Lymph Node | Level IV neck (Lower Jugular) node Left | 241959 |
| LN_Neck_IV_R | Anatomic | Lymph Node | Level IV (Lower Jugular) neck node Right | 241957 |
| LN_Neck_V_L | Anatomic | Lymph Node | Level VA, VB and VC (Posterior Triangle) neck nodes Left | 241965 |
| LN_Neck_V_R | Anatomic | Lymph Node | Level VA, VB and VC (Posterior Triangle) neck nodes Right | 241963 |
| LN_Neck_VA_L | Anatomic | Lymph Node | Level VA (Posterior Triangle) neck node Left | 265629 |
| LN_Neck_VA_R | Anatomic | Lymph Node | Level VA (Posterior Triangle) neck node Right | 265626 |
| LN_Neck_VB_L | Anatomic | Lymph Node | Level VB (Posterior Triangle) neck node Left | — |
| LN_Neck_VB_R | Anatomic | Lymph Node | Level VB (Posterior Triangle) neck node Right | — |
| LN_Neck_VC_L | Anatomic | Lymph Node | Level VC (Posterior Triangle) neck node Left | 232721 |
| LN_Neck_VC_R | Anatomic | Lymph Node | Level VC (Posterior Triangle) neck node Right | 232719 |
| LN_Neck_VI_L | Anatomic | Lymph Node | Level VI (Anterior Triangle) neck node Left | 241971 |
| LN_Neck_VI_R | Anatomic | Lymph Node | Level VI (Anterior Triangle) neck node Right | 241969 |
| LN_Neck_VII_L | Anatomic | Lymph Node | Level VII (Upper Mediastinal) neck node Left | — |
| LN_Neck_VII_R | Anatomic | Lymph Node | Level VII (Upper Mediastinal) neck node Right | — |
| Lobe_Frontal | Anatomic | Brain | Frontal Lobe | 61824 |
| Lobe_Frontal_L | Anatomic | Brain | Frontal Lobe Left | 72970 |
| Lobe_Frontal_R | Anatomic | Brain | Frontal Lobe Left | 72969 |
| Lobe_Occipital | Anatomic | Brain | Occipital Lobe | 67325 |
| Lobe_Occipital_L | Anatomic | Brain | Occipital Lobe Left | 72976 |
| Lobe_Occipital_R | Anatomic | Brain | Occipital Lobe Right | 72975 |
| Lobe_Parietal | Anatomic | Brain | Parietal Lobe | 61826 |
| Lobe_Parietal_L | Anatomic | Brain | Parietal Lobe Left | 72974 |
| Lobe_Parietal_R | Anatomic | Brain | Parietal Lobe Right | 72973 |
| Lobe_Temporal | Anatomic | Brain | Temporal Lobe | 61825 |
| Lobe_Temporal_L | Anatomic | Brain | Temporal Lobe Left | 72972 |
| Lobe_Temporal_R | Anatomic | Brain | Temporal Lobe Right | 72971 |
| Malleus | Anatomic | Bone | Malleus | 52753 |
| Malleus_L | Anatomic | Bone | Malleus Left | 74053 |
| Malleus_R | Anatomic | Bone | Malleus Right | 74052 |
| Maxilla | Anatomic | Bone | Maxilla | 9711 |
| Maxilla_L | Anatomic | Bone | Maxilla Left | 53650 |
| Maxilla_R | Anatomic | Bone | Maxilla Right | 53649 |
| Musc_Constrict | Anatomic | Muscle | Constrictor Muscle of Pharynx | 46620 |
| Musc_Constrict_I | Anatomic | Muscle | Pharynx – Inferior pharyngeal constrictor | 46623 |
| Musc_Constrict_M | Anatomic | Muscle | Pharynx – Middle pharyngeal constrictor | 46622 |
| Musc_Constrict_S | Anatomic | Muscle | Pharynx – Superior pharyngeal constrictor | 46621 |
| Musc_Masseter | Anatomic | Muscle | Masseter Muscle | 48996 |
| Musc_Masseter_L | Anatomic | Muscle | Masseter Muscle Left | 48998 |
| Musc_Masseter_R | Anatomic | Muscle | Masseter Muscle Right | 48997 |
| Musc_Platysma_L | Anatomic | Muscle | Platysma Left | 45740 |
| Musc_Platysma_R | Anatomic | Muscle | Platysma Right | 45739 |
| Musc_Pterygoid_L | Anatomic | Muscle | Pterygoid muscles – Left | — |
| Musc_Pterygoid_R | Anatomic | Muscle | Pterygoid muscles – Right | — |
| Musc_Sclmast_L | Anatomic | Muscle | Sternocleidomastoid Left | 13409 |
| Musc_Sclmast_R | Anatomic | Muscle | Sternocleidomastoid Left | 13408 |
| Musc_Temporal_L | Anatomic | Muscle | Temporal muscle – Left | 49008 |
| Musc_Temporal_R | Anatomic | Muscle | Temporal muscle – Right | 49007 |
| Nasalconcha_LI | Anatomic | Nose | Inferior Nasal Concha Left | 54738 |
| Nasalconcha_RI | Anatomic | Nose | Inferior Nasal Concha Right | 54737 |
| Nasopharynx | Anatomic | Nose | Nasal part of pharynx | 54878 |
| Nose | Anatomic | Nose | Nose | 46472 |
| OpticChiasm | Anatomic | Nerve | Optic chiasm | 62045 |
| OpticChiasm_PRV | PRV | Nerve | PRV for Optic Chiasm | — |
| OpticChiasm_PRVx | PRV | Nerve | PRV expansión of x mm on the optic chiasm | — |
| OpticNrv | Anatomic | Nerve | Optic nerve | 50863 |
| OpticNrv_L | Anatomic | Nerve | Optic nerve | 50878 |
| OpticNrv_PRV | PRV | Nerve | PRV for Optic Nerve | — |
| OpticNrv_PRV_L | PRV | Nerve | — | |
| OpticNrv_PRV_R | PRV | Nerve | — | |
| OpticNrv_PRVxx_L | PRV | Nerve | PRV expansión of xx millimeters on the right optic nerve | — |
| OpticNrv_PRVxx_R | PRV | Nerve | PRV created with xx mm expansión on the left optic nerve | — |
| OpticNrv_R | Anatomic | Nerve | Optic nerve | 50875 |
| Orbit_L | Anatomic | Eye | Orbit Left | 54668 |
| Orbit_R | Anatomic | Eye | Orbit Right | 54667 |
| Oropharynx | Anatomic | Throat | Oral part of pharynx | 54879 |
| Palate_Soft | Anatomic | Muscle | Soft palate | 55021 |
| Parotid_L | Anatomic | Gland | Parotid Left | 59798 |
| Parotid_R | Anatomic | Gland | Parotid Right | 59797 |
| Parotids | Anatomic | Gland | Pair of Parotid Glands | 320436 |
| Pharynx | Anatomic | Throat | Pharynx | 46688 |
| Pineal | Anatomic | Gland | Pineal gland | 62033 |
| Pituitary | Anatomic | Gland | Pituitary gland | 13889 |
| Pituitary_PRVxx | PRV | Gland | PRV constructed as xx millimeter expansión on Pituitary | — |
| Pons | Anatomic | Brain | Pons | 67943 |
| Proc_Condyloid_L | Anatomic | Bone | Condyloid process of mandible – Right | 52838 |
| Proc_Condyloid_R | Anatomic | Bone | Condyloid process of mandible – Left | 52840 |
| Proc_Coronoid_L | Anatomic | Bone | Coronoid process of mandible – Left | 52835 |
| Proc_Coronoid_R | Anatomic | Bone | Coronoid process of mandible – Right | 52834 |
| Pterygoid_Lat_L | Anatomic | Muscle | Pterygoid muscles lateral – Left | 49017 |
| Pterygoid_Lat_R | Anatomic | Muscle | Pterygoid muscles lateral – Right | 49016 |
| Pterygoid_Med_L | Anatomic | Muscle | Pterygoid muscles medial – Left | 49013 |
| Pterygoid_Med_R | Anatomic | Muscle | Pterygoid muscles medial – Right | 49012 |
| Retina_L | Anatomic | Eye | Retina Left | 58303 |
| Retina_PRVxx_L | PRV | Eye | — | |
| Retina_PRVxx_R | PRV | Eye | PRV constructed as xx millimeter expansión on Retina | — |
| Retina_R | Anatomic | Eye | Retina Right | 58302 |
| Retinas | Anatomic | Eye | Both Retinas | 58301 |
| Scalp | Anatomic | Skin | 46494 | |
| Sinus_Ethmoid | Anatomic | Sinus | Ethmoidal Sinus | 84115 |
| Sinus_Frontal | Anatomic | Brain | Frontal Sinus | 57417 |
| Sinus_Frontal_L | Anatomic | Brain | Frontal Sinus Left | 57419 |
| Sinus_Frontal_R | Anatomic | Brain | Frontal Sinus Right | 57418 |
| Sinus_Maxilry | Anatomic | Sinus | Maxillary Sinus | 57715 |
| Sinus_Maxilry_L | Anatomic | Sinus | Maxillary Sinus | 57717 |
| Sinus_Maxilry_R | Anatomic | Sinus | Maxillary Sinus | 57716 |
| Sinus_Sphenoid | Anatomic | Bone | Sphenoidal Sinus | 54683 |
| Sinus_Sphenoid_L | Anatomic | Bone | Sphenoidal Sinus Left | 54708 |
| Sinus_Sphenoid_R | Anatomic | Bone | Sphenoidal Sinus Right | 54707 |
| Skull | Anatomic | Bone | Skeletal system of head | 46565 |
| Spc_Retrophar_L | Anatomic | Space | Retropharyngeal space Left | — |
| Spc_Retrophar_R | Anatomic | Space | Retropharyngeal space Right | — |
| Spc_Retrophars | Anatomic | Space | Retropharyngeal space | 286702 |
| Spc_Retrosty | Anatomic | Space | Retrostyloid space | — |
| Spc_Retrosty_L | Anatomic | Space | Retrostyloid space -Left | — |
| Spc_Retrosty_R | Anatomic | Space | Retrostyloid space -Left | — |
| SpinalCord_Cerv | Anatomic | Nerve | Spinal Cord Cervical | 71166 |
| Stapes | Anatomic | Ear | Stapes | 52751 |
| Stapes_L | Anatomic | Ear | Stapes Left | 74049 |
| Stapes_R | Anatomic | Ear | Stapes Right | 74048 |
| Sys_Ventricular | Anatomic | Brain | 242787 | |
| Tongue | Anatomic | Mouth | Tongue | 54640 |
| Tongue_All | Anatomic | Mouth | — | |
| Tongue_Base | Anatomic | Mouth | 54645 | |
| Tongue_Base_L | Anatomic | Mouth | — | |
| Tongue_Base_R | Anatomic | Mouth | — | |
| Tongue_Oral | Anatomic | Mouth | 54644 | |
| Tongue_Oral_L | Anatomic | Mouth | 281502 | |
| Tongue_Oral_R | Anatomic | Mouth | 281500 | |
| Tonsil | Anatomic | Mouth | 9609 | |
| V_Jugular | Anatomic | Vein | Any Jugular Vein | — |
| V_Jugular_Ext_L | Anatomic | Vein | 13112 | |
| V_Jugular_Ext_R | Anatomic | Vein | 13111 | |
| V_Jugular_Int_L | Anatomic | Vein | Internal jugular vein Right | 4754 |
| V_Jugular_Int_R | Anatomic | Vein | Internal jugular vein Left | 4762 |
| VB_C | Anatomic | Bone | Cervical vertebrae | 72063 |
| VB_C1 | Anatomic | Bone | Atlas – C1 | 12519 |
| VB_C2 | Anatomic | Bone | Axis – C2 | 12520 |
| VB_C3 | Anatomic | Bone | Cervical vertebra – C3 | 12521 |
| VB_C4 | Anatomic | Bone | Cervical vertebra – C4 | 12522 |
| VB_C5 | Anatomic | Bone | Cervical vertebra – C5 | 12523 |
| VB_C6 | Anatomic | Bone | Cervical vertebra – C6 | 12524 |
| VB_C7 | Anatomic | Bone | Cervical vertebra – C7 | 12525 |
| VocalCord_L | Anatomic | Larynx | 55459 | |
| VocalCord_R | Anatomic | Larynx | 55458 | |
| VocalCords | Anatomic | Larynx | Vocal Cords | 323919 |
| Vomer | Anatomic | Bone | Vomer | 9710 |
Torax (Thorax) — 180 estructuras
| Nombre TG-263 | Tipo | Categoria | Descripción | FMAID |
|---|---|---|---|---|
| A_Aorta | Anatomic | Artery | Aorta | 3734 |
| A_Aorta_Asc | Anatomic | Artery | Ascending Aorta | 3736 |
| A_Brachiocephls | Anatomic | Artery | Brachiocephalic Artery | 3932 |
| A_Coronary_L | Anatomic | Artery | Coronary Artery Left | 50040 |
| A_Coronary_R | Anatomic | Artery | Coronary Artery Right | 50039 |
| A_LAD | Anatomic | Artery | Anterior interventricular branch of LCA (left anterior descending artery) |
3862 |
| A_Pulmonary | Anatomic | Artery | Pulmonary Artery | 66326 |
| A_Subclavian | Anatomic | Artery | Subclavian Artery | 3951 |
| A_Subclavian_L | Anatomic | Artery | Subclavian Artery Left | 4694 |
| A_Subclavian_R | Anatomic | Artery | Subclavian Artery Right | 3953 |
| A_Vertebral | Anatomic | Artery | Vertebral arteries | 3956 |
| A_Vertebral_L | Anatomic | Artery | Vertebral arteries left | 4066 |
| A_Vertebral_R | Anatomic | Artery | Vertebral arteries right | 3958 |
| AirWay_Dist | Anatomic | Lung | Distal Airway | — |
| AirWay_Prox | Anatomic | Lung | Proximal Airway | — |
| Atrium | Anatomic | Heart | Atrium of the heart | 7099 |
| Atrium_L | Anatomic | Heart | Atrium of the heart Left | 7097 |
| Atrium_R | Anatomic | Heart | Atrium of the heart Right | 7096 |
| BrachialPlex_L | Anatomic | Nerve | Brachial plexus Left | 45245 |
| BrachialPlex_R | Anatomic | Nerve | Brachial plexus Right | 45244 |
| BrachialPlexs | Anatomic | Nerve | Brachial plexus | 5906 |
| Breast_L | Anatomic | Breast | Breast Left | 321497 |
| Breast_R | Anatomic | Breast | Breast Right | 321496 |
| Breasts | Anatomic | Breast | Both breasts | 268893 |
| Bronchus | Anatomic | Lung | Bronchial tree | 26660 |
| Bronchus_L | Anatomic | Lung | Bronchial tree Left | 26662 |
| Bronchus_Main | Anatomic | Lung | Main Bronchus | 7405 |
| Bronchus_Main_L | Anatomic | Lung | Main Bronchus Left | 7396 |
| Bronchus_Main_R | Anatomic | Lung | Main Bronchus Right | 7395 |
| Bronchus_PRVxx | Anatomic | Lung | A PRV expansión on the Bronchus that is xx millimeters thick | — |
| Bronchus_R | Anatomic | Lung | Bronchial tree Right | 26661 |
| Carina | Anatomic | Carina | Carina | 7465 |
| Cartlg_Thyroid | Anatomic | Cartilage | Thyroid cartilage | 55099 |
| Chestwall | Anatomic | Chest wall | Chest wall | 50060 |
| Chestwall_L | Anatomic | Chest wall | Left Chest Wall | 25559 |
| Chestwall_R | Anatomic | Chest wall | Right Chest Wall | 25558 |
| Clavicle_L | Anatomic | Bone | Clavicle Left | 13323 |
| Clavicle_R | Anatomic | Bone | Clavicle Right | 13322 |
| Diaphragm | Anatomic | Diaphragm | Diaphragm | 13295 |
| Esophagus | Anatomic | Esophagus | Esophagus | 7131 |
| Esophagus_I | Anatomic | Esophagus | Lower Esophagus (abdominal) | 9397 |
| Esophagus_M | Anatomic | Esophagus | Middle Esophagus (thoracic) | 9396 |
| Esophagus_NAdj | Anatomic | Esophagus | Non Adjacent Esophagus | — |
| Esophagus_S | Anatomic | Esophagus | Upper Esophagus (cervical) | — |
| Glnd_Adrenal_L | Anatomic | Gland | Adrenal glands left | 15629 |
| Glnd_Adrenal_R | Anatomic | Gland | Adrenal glands right | 15630 |
| Glnd_Parathyroid | Anatomic | Gland | Parathyroid gland | 13890 |
| Glnd_Thymus | Anatomic | Gland | Thymus Gland | 9607 |
| Glnd_Thyroid | Anatomic | Gland | Thyroid Gland | 9603 |
| GreatVes | Anatomic | Heart | Great Vessels of the heart (aorta, vena cava S&I, pulmonary A&V) | — |
| GreatVes_NAdj | Anatomic | Heart | Non Adjacent Great Vessels | — |
| Heart | Anatomic | Heart | Heart | 7088 |
| LN_Ax_Apical | Anatomic | Lymph Node | Set of apical axillary lymphatic vessels | 23394 |
| LN_Ax_Apical_L | Anatomic | Lymph Node | Axillary lymphatic chain – Apical Left | 73265 |
| LN_Ax_Apical_R | Anatomic | Lymph Node | Axillary lymphatic chain – Apical Right | 73264 |
| LN_Ax_Central_L | Anatomic | Lymph Node | Axillary lymphatic chain – Central Left | 73263 |
| LN_Ax_Central_R | Anatomic | Lymph Node | Axillary lymphatic chain – Central Left | 73262 |
| LN_Ax_Centrals | Anatomic | Lymph Node | Set of central axillary lymphatic vessels | 233482 |
| LN_Ax_L | Anatomic | Lymph Node | Axillary lymphatic chain Left | 73250 |
| LN_Ax_L1_L | Anatomic | Lymph Node | Level 1 Axillary Lymph Node Left | 276001 |
| LN_Ax_L1_R | Anatomic | Lymph Node | Level 1 Axillary Lymph Node Right | 275999 |
| LN_Ax_L2_L | Anatomic | Lymph Node | Level 2 Axillary Lymph Node Left | 276005 |
| LN_Ax_L2_R | Anatomic | Lymph Node | Level 2 Axillary Lymph Node Right | 276003 |
| LN_Ax_L3_L | Anatomic | Lymph Node | Level 3 Axillary Lymph Node Left | 276009 |
| LN_Ax_L3_R | Anatomic | Lymph Node | Level 3 Axillary Lymph Node Right | 276007 |
| LN_Ax_Lateral_L | Anatomic | Lymph Node | Axillary lymphatic chain – Lateral Left | 73256 |
| LN_Ax_Lateral_R | Anatomic | Lymph Node | Axillary lymphatic chain – Lateral Right | 73255 |
| LN_Ax_Laterals | Anatomic | Lymph Node | pair of Lungs | 233458 |
| LN_Ax_Pectoral_L | Anatomic | Lymph Node | Axillary lymphatic chain – Pectoral Left | 73253 |
| LN_Ax_Pectoral_R | Anatomic | Lymph Node | Axillary lymphatic chain – Pectoral Right | 73252 |
| LN_Ax_Pectorals | Anatomic | Lymph Node | Set of pectoral axillary lymphatic vessels | 233446 |
| LN_Ax_R | Anatomic | Lymph Node | Axillary lymphatic chain Right | 73249 |
| LN_Ax_Subscap_L | Anatomic | Lymph Node | Axillary lymphatic chain – Subscapular Left | 73259 |
| LN_Ax_Subscap_R | Anatomic | Lymph Node | Axillary lymphatic chain – Subscapular Right | 73258 |
| LN_Ax_Subscaps | Anatomic | Lymph Node | Set of subscapular axillary lymphatic vessels | 233470 |
| LN_Brachioceph_L | Anatomic | Lymph Node | Lymph nodes of thorax – Brachiocephalic Left | 5946 |
| LN_Brachioceph_R | Anatomic | Lymph Node | Lymph nodes of thorax – Brachiocephalic Right | 5945 |
| LN_Brachiocephs | Anatomic | Lymph Node | Lymph nodes of thorax – Brachiocephalic | 5944 |
| LN_Bronchpulm_L | Anatomic | Lymph Node | Lymph nodes of thorax – Bronchopulmonary Left | 5967 |
| LN_Bronchpulm_R | Anatomic | Lymph Node | Lymph nodes of thorax – Bronchopulmonary Right | 5966 |
| LN_Bronchpulms | Anatomic | Lymph Node | Lymph nodes of thorax – Bronchopulmonary | 5965 |
| LN_Diaphragmatic | Anatomic | Lymph Node | Lymph nodes of thorax – Diaphragmatic | 12773 |
| LN_IMN_L | Anatomic | Lymph Node | 5934 | |
| LN_IMN_R | Anatomic | Lymph Node | 5933 | |
| LN_IMNs | Anatomic | Lymph Node | Lymph nodes IMN | 5849 |
| LN_Intercostals | Anatomic | Lymph Node | Lymph nodes of thorax – Intercostal | 5932 |
| LN_Ligamentarter | Anatomic | Lymph Node | Lymph nodes of thorax – Ligamentum arteriosum | 74033 |
| LN_Mediastinals | Anatomic | Lymph Node | Lymph nodes of thorax – Mediastinal | 12774 |
| LN_Paramammary_L | Anatomic | Lymph Node | Lymph nodes of thorax – Paramammary Left | 232600 |
| LN_Paramammary_R | Anatomic | Lymph Node | Lymph nodes of thorax – Paramammary Right | 232598 |
| LN_Paramammarys | Anatomic | Lymph Node | Lymph nodes of thorax – Paramammary | 44313 |
| LN_Parasternal_L | Anatomic | Lymph Node | Lymph nodes of thorax – Parasternal Left | 5934 |
| LN_Parasternal_R | Anatomic | Lymph Node | Lymph nodes of thorax – Parasternal Right | 5933 |
| LN_Parasternals | Anatomic | Lymph Node | Lymph nodes of thorax – Parasternal | 5849 |
| LN_Pulmonary_L | Anatomic | Lymph Node | Lymph nodes of thorax – Pulmonary Left | 5970 |
| LN_Pulmonary_R | Anatomic | Lymph Node | Lymph nodes of thorax – Pulmonary Right | 5969 |
| LN_Pulmonarys | Anatomic | Lymph Node | Lymph nodes of thorax – Pulmonary | 5968 |
| LN_Supmammary_L | Anatomic | Lymph Node | Lymph nodes of thorax – Supramammary Left | 232604 |
| LN_Supmammary_R | Anatomic | Lymph Node | Lymph nodes of thorax – Supramammary Right | 232602 |
| LN_Supmammarys | Anatomic | Lymph Node | Lymph nodes of thorax – Supramammary | 12785 |
| LN_Trachbrnchs | Anatomic | Lymph Node | Lymph nodes of thorax – Tracheobronchial | 5950 |
| LN_Trachbrnchs_L | Anatomic | Lymph Node | Lymph nodes of thorax – Tracheobronchial Left | 5952 |
| LN_Trachbrnchs_R | Anatomic | Lymph Node | Lymph nodes of thorax – Tracheobronchial Right | 5951 |
| Lung_L | Anatomic | Lung | Lung Left | 7310 |
| Lung_LLL | Anatomic | Lung | Lung – lower lobe of left | 7371 |
| Lung_LUL | Anatomic | Lung | Lung – upper lobe of left | 7370 |
| Lung_R | Anatomic | Lung | Lung Right | 7309 |
| Lung_RLL | Anatomic | Lung | Lung – lower lobe of right | 7337 |
| Lung_RML | Anatomic | Lung | Lung – middle lobe of right | 7383 |
| Lung_RUL | Anatomic | Lung | Lung – upper lobe of right | 7333 |
| Lungs | Anatomic | Lung | Pair of Lungs | 68877 |
| Lungs-CTV | Derived | Lung | Total Lung minus the CTV | — |
| Lungs-GTV | Derived | Lung | Total Lung minus the GTV | — |
| Lungs-ITV | Derived | Lung | — | |
| Lungs-PTV | Derived | Lung | Total Lung minus the PTV | — |
| Mediastinum | Anatomic | Heart | Mediastinum | 9826 |
| Pacemaker | Non_Anatomic | Devices | Pacemaker | — |
| Pericardium | Anatomic | Heart | Pericardium | 9869 |
| Rib | Anatomic | Bone | Any Rib volume | 7574 |
| Rib01_L | Anatomic | Bone | First Rib Left | 7987 |
| Rib01_R | Anatomic | Bone | First Rib Right | 7857 |
| Rib02_L | Anatomic | Bone | Second rib Left | 8012 |
| Rib02_R | Anatomic | Bone | Second rib Right | 7882 |
| Rib03_L | Anatomic | Bone | Third rib Left | 8039 |
| Rib03_R | Anatomic | Bone | Third rib Right | 7909 |
| Rib04_L | Anatomic | Bone | Fourth rib Left | 8148 |
| Rib04_R | Anatomic | Bone | Fourth rib Right | 7957 |
| Rib05_L | Anatomic | Bone | Fifth rib Left | 8093 |
| Rib05_R | Anatomic | Bone | Fifth rib Right | 8066 |
| Rib06_L | Anatomic | Bone | Sixth rib Left | 8202 |
| Rib06_R | Anatomic | Bone | Sixth rib Right | 8175 |
| Rib07_L | Anatomic | Bone | Seventh rib Left | 8256 |
| Rib07_R | Anatomic | Bone | Seventh rib Right | 8229 |
| Rib08_L | Anatomic | Bone | Eighth rib Left | 8310 |
| Rib08_R | Anatomic | Bone | Eighth rib Right | 8283 |
| Rib09_L | Anatomic | Bone | Ninth rib Left | 8391 |
| Rib09_R | Anatomic | Bone | Ninth rib Right | 8364 |
| Rib10_L | Anatomic | Bone | Tenth rib Left | 8472 |
| Rib10_R | Anatomic | Bone | Tenth rib Right | 8445 |
| Rib11_L | Anatomic | Bone | Eleventh rib Left | 8532 |
| Rib11_R | Anatomic | Bone | Eleventh rib Right | 8531 |
| Rib12_L | Anatomic | Bone | Twelfth rib Left | 8534 |
| Rib12_R | Anatomic | Bone | Twelfth rib Right | 8533 |
| Scapula_L | Anatomic | Bone | Scapula Left | 13396 |
| Scapula_R | Anatomic | Bone | Scapula Right | 13395 |
| Spc_Supraclav_L | Anatomic | Space | Supraclavicular space – Left | 45797 |
| Spc_Supraclav_R | Anatomic | Space | Supraclavicular space – Right | 45796 |
| SpinalCord_Thor | Anatomic | Nerve | Spinal Cord Thoracic | 71167 |
| Thoracic_Duct | Anatomic | Duct | Thoracic Duct | 5031 |
| Trachea | Anatomic | Lung | Trachea | 7394 |
| Trachea_NAdj | Anatomic | Lung | Trachea non adjacent wall | — |
| V_Azygos | Anatomic | Vein | Azygos Vein | 4838 |
| V_Brachioceph_L | Anatomic | Vein | Brachiocephalic vein Left | 4761 |
| V_Brachioceph_R | Anatomic | Vein | Brachiocephalic vein Right | 4751 |
| V_Pulmonary | Anatomic | Vein | Pulmonary vein | 66643 |
| V_Subclavian_L | Anatomic | Vein | Subclavian Vein Left | 4763 |
| V_Subclavian_R | Anatomic | Vein | Subclavian Vein Right | 4755 |
| V_Subclavians | Anatomic | Vein | Subclavian Vein | 4725 |
| V_Venacava_I | Anatomic | Vein | Inferior vena cava | 10951 |
| V_Venacava_S | Anatomic | Vein | Superior vena cava | 4720 |
| Valve_Aortic | Anatomic | Valve | Aortic Valve | 7236 |
| Valve_Mitral | Anatomic | Valve | Mitral Valve | 7235 |
| Valve_Pulmonic | Anatomic | Valve | Pulmonic Valve | 7246 |
| Valve_Tricuspid | Anatomic | Valve | Tricuspid Valve | 7234 |
| VB_T | Anatomic | Bone | Thoracic Vertebra | 9139 |
| VB_T01 | Anatomic | Bone | Thoracic Vertebra T1 | 9165 |
| VB_T02 | Anatomic | Bone | Thoracic Vertebra T2 | 9187 |
| VB_T03 | Anatomic | Bone | Thoracic Vertebra T3 | 9209 |
| VB_T04 | Anatomic | Bone | Thoracic Vertebra T4 | 9248 |
| VB_T05 | Anatomic | Bone | Thoracic Vertebra T5 | 9922 |
| VB_T06 | Anatomic | Bone | Thoracic Vertebra T6 | 9945 |
| VB_T07 | Anatomic | Bone | Thoracic Vertebra T7 | 9968 |
| VB_T08 | Anatomic | Bone | Thoracic Vertebra T8 | 9991 |
| VB_T09 | Anatomic | Bone | Thoracic Vertebra T9 | 10014 |
| VB_T10 | Anatomic | Bone | Thoracic Vertebra T10 | 10037 |
| VB_T11 | Anatomic | Bone | Thoracic Vertebra T11 | 10059 |
| VB_T12 | Anatomic | Bone | Thoracic Vertebra T12 | 10081 |
| Ventricle | Anatomic | Heart | Ventricle (cardiac) | 7100 |
| Ventricle_L | Anatomic | Heart | Ventricle (cardiac) Left | 7101 |
| Ventricle_R | Anatomic | Heart | Ventricle (cardiac) Right | 7098 |
Abdomen (Abdomen) — 60 estructuras
| Nombre TG-263 | Tipo | Categoria | Descripción | FMAID |
|---|---|---|---|---|
| A_Celiac | Anatomic | Artery | Celiac Artery | 50737 |
| A_Mesenteric_I | Anatomic | Artery | Inferior mesenteric artery | 14750 |
| A_Mesenteric_S | Anatomic | Artery | Superior mesenteric artery | 14749 |
| Appendix | Anatomic | Bowel | Appendix | 14542 |
| Bag_Bowel | Non_Anatomic | Bowel | Bowel Bag | — |
| BileDuct_Common | Anatomic | Bowel | Common bile duct | 14667 |
| Bowel | Anatomic | Bowel | 7199 | |
| Bowel_Small | Anatomic | Bowel | Small Bowel (small intestine) | 7200 |
| Cecum | Anatomic | Bowel | Large bowel – Cecum | 14541 |
| Colon | Anatomic | Bowel | Colon | 14543 |
| Colon_Ascending | Anatomic | Bowel | Large bowel – Ascending colon | 14545 |
| Colon_Decending | Anatomic | Bowel | Large bowel – Descending colon | 14547 |
| Colon_PTVxx | Anatomic | Bowel | PRV created with xx mm expansión on the left optic nerve | — |
| Colon_Sigmoid | Anatomic | Bowel | Large bowel – Sigmoid colon | 14548 |
| Colon_Transverse | Anatomic | Bowel | Large bowel -Transverse colon | 14546 |
| Duodenum | Anatomic | Gut | Small bowel – Duodenum | 7206 |
| Ileum | Anatomic | Gut | Small bowel – Ileum | 7208 |
| Jejunum | Anatomic | Gut | Small bowel – Jejunum | 7207 |
| Jejunum_Ileum | Anatomic | Gut | Both ileum and jejunum | — |
| Kidney_Cortex | Anatomic | Urinary | Renal cortex for both Kidneys | 15581 |
| Kidney_Cortex_L | Anatomic | Urinary | Renal cortex left | 15584 |
| Kidney_Cortex_R | Anatomic | Urinary | Renal cortex right | 15583 |
| Kidney_Hilum_L | Anatomic | Urinary | Renal Hilum Left | 15942 |
| Kidney_Hilum_R | Anatomic | Urinary | Renal Hilum Right | 15941 |
| Kidney_Hilums | Anatomic | Urinary | Renal Hilum for both Kidneys | 15610 |
| Kidney_L | Anatomic | Urinary | Kidney Left | 7205 |
| Kidney_L-GTV | Derived | Urinary | — | |
| Kidney_Pelvis_L | Anatomic | Urinary | Renal pelvis Left | 15579 |
| Kidney_Pelvis_R | Anatomic | Urinary | Renal pelvis Right | 15578 |
| Kidney_R | Anatomic | Urinary | Kidney Right | 7204 |
| Kidney_R-GTV | Derived | Urinary | — | |
| Kidney-GTV | Derived | Urinary | — | |
| Kidneys | Anatomic | Urinary | Both Kidneys | 264815 |
| Lig_Hepatogastrc | Anatomic | Ligament | Hepatogastric ligament | 16520 |
| Liver | Anatomic | Liver | Liver | 7197 |
| Liver-CTV | Derived | Liver | — | |
| Liver-GTV | Derived | Liver | Liver minus GTV | — |
| LN_Portahepatis | Anatomic | Lymph Node | Porta hepatis | 15758 |
| Musc_Digastric_L | Anatomic | Muscle | Digastric muscle Left | 46293 |
| Musc_Digastric_R | Anatomic | Muscle | Digastric muscle Right | 46292 |
| PancJejuno | Surgical | Gut | The pancreatic jejuno junction – generated by surgical procedure | — |
| Pancreas | Anatomic | Gland | Pancreas | 7198 |
| Pancreas_Head | Anatomic | Gland | Head of Pancreas | 10468 |
| Pancreas_Tail | Anatomic | Gland | Tail of Pancreas | 14519 |
| Peritoneum | Anatomic | Membrane | Peritoneal sac | 9908 |
| Skin_Peritoneum | Anatomic | Skin | — | |
| Spc_Bowel | Anatomic | Bowel | Space occupied by bowel | — |
| Spc_Bowel_Small | Anatomic | Space | — | |
| SpinalCord_Lum | Anatomic | Nerve | Spinal Cord Lumbar | 71168 |
| Spleen | Anatomic | Lymph Node | Spleen | 7196 |
| Spleen_Hilum | Anatomic | Lymph Node | Splenic hilum | 15841 |
| Stomach | Anatomic | Stomach | Stomach | 7148 |
| Stomach_PRVxx | PRV | Stomach | PRV created with xx mm expansión on the stomach | — |
| V_Portal | Anatomic | Vein | Portal Vein | 66645 |
| VB_L | Anatomic | Bone | Lumbar Vertebrae | 72065 |
| VB_L1 | Anatomic | Bone | Lumbar Vertebra L1 | 13072 |
| VB_L2 | Anatomic | Bone | Lumbar Vertebra L2 | 13073 |
| VB_L3 | Anatomic | Bone | Lumbar Vertebra L3 | 13074 |
| VB_L4 | Anatomic | Bone | Lumbar Vertebra L4 | 13075 |
| VB_L5 | Anatomic | Bone | Lumbar Vertebra L5 | 13076 |
Pelvis (Pelvis) — 109 estructuras
| Nombre TG-263 | Tipo | Categoria | Descripción | FMAID |
|---|---|---|---|---|
| A_Iliac_Cflx_L | Anatomic | Artery | Circumflex Left Iliac Artery | — |
| A_Iliac_Cflx_R | Anatomic | Artery | Circumflex Right Iliac Artery | — |
| A_Iliac_Ext_L | Anatomic | Artery | External iliac artery Left | 18807 |
| A_Iliac_Ext_R | Anatomic | Artery | External iliac artery Right | 18806 |
| A_Iliac_Int_L | Anatomic | Artery | Internal iliac artery Left | 18810 |
| A_Iliac_Int_R | Anatomic | Artery | Internal iliac artery Right | 18809 |
| A_Iliac_L | Anatomic | Artery | Common iliac artery Left | 14766 |
| A_Iliac_R | Anatomic | Artery | Common iliac artery Right | 14765 |
| Acetabulum_L | Anatomic | Bone | Acetabulum | 16599 |
| Acetabulum_R | Anatomic | Bone | Acetabulum | 16598 |
| Acetabulums | Anatomic | Bone | Acetabulum | 16579 |
| Anus | Anatomic | Bowel | Anus | 15711 |
| Bladder | Anatomic | Bladder | Urinary Bladder | 15900 |
| Bladder_Wall | Anatomic | Bladder | Bladder Wall | 15902 |
| Bladder-CTV | Derived | Bladder | Bladder minus CTV | — |
| Bone_Ilium | Anatomic | Bone | Ilium | 42832 |
| Bone_Ilium_L | Anatomic | Bone | Ilium Left | 16591 |
| Bone_Ilium_R | Anatomic | Bone | Ilium Right | 16590 |
| Bone_Ischium_L | Anatomic | Bone | Ischium Left | 16594 |
| Bone_Ischium_R | Anatomic | Bone | Ischium Right | 16593 |
| Bone_Pelvic | Anatomic | Bone | Pelvic Bones (Bony Pelvis) | 16580 |
| Bone_Pelvic_L | Anatomic | Bone | Bony Pelvis Left | 20227 |
| Bone_Pelvic_R | Anatomic | Bone | Bony Pelvis Right | 20226 |
| Bowel_Large | Anatomic | Bowel | Large Bowel | 7201 |
| Canal_Anal | Anatomic | Bowel | Anal Canal | 15703 |
| CaudaEquina | Anatomic | Nerve | Cauda equina | 52590 |
| Cavernosum | Anatomic | Reproductive | Penis Corpus Cavernosum | 75189 |
| Cervix | Anatomic | Cervix | Cervix of uterus | 17740 |
| Femur_Base_L | Anatomic | Bone | Femur Base Left | 32846 |
| Femur_Base_R | Anatomic | Bone | Femur Base Right | 32845 |
| Femur_Head_L | Anatomic | Bone | Femur Head & Neck Left | 32843 |
| Femur_Head_R | Anatomic | Bone | Femur Head & Neck Right | 32842 |
| Femur_Joint_L | Anatomic | Joint | Femoral Joint Left | 35180 |
| Femur_Joint_R | Anatomic | Joint | Femoral Joint Right | 35179 |
| Femur_Neck_L | Anatomic | Bone | Femur Neck Right | 42386 |
| Femur_Neck_R | Anatomic | Bone | Femur Neck Left | 42387 |
| Femur_Shaft_L | Anatomic | Bone | Femur Shaft Left | 32849 |
| Femur_Shaft_R | Anatomic | Bone | Femur Shaft Right | 32848 |
| Foley | Non-Anatomic | Bladder | Foley Catheter | — |
| Gallbladder | Anatomic | Gallbladder | Gall bladder | 7202 |
| Genitals | Anatomic | Reproductive | Genitals | 45643 |
| LN_Iliac_Ext_L | Anatomic | Lymph Node | Lymph nodes of pelvis – external iliac Left | 229177 |
| LN_Iliac_Ext_R | Anatomic | Lymph Node | Lymph nodes of pelvis – external iliac Right | 229177 |
| LN_Iliac_Int_L | Anatomic | Lymph Node | Lymph nodes of pelvis – internal iliac Left | 224275 |
| LN_Iliac_L | Anatomic | Lymph Node | Lymph nodes of pelvis – common iliac Left | 224269 |
| LN_Iliac_R | Anatomic | Lymph Node | Lymph nodes of pelvis – common iliac Right | 224269 |
| LN_Inguinofem | Anatomic | Lymph Node | Lymph nodes of pelvis – inguinofemoral | 236337 |
| LN_Inguinofem_L | Anatomic | Lymph Node | Lymph nodes of pelvis – inguinofemoral | 236341 |
| LN_Inguinofem_R | Anatomic | Lymph Node | Lymph nodes of pelvis – inguinofemoral | 236339 |
| LN_lliac_Int_R | Anatomic | Lymph Node | Lymph nodes of pelvis – internal iliac Right | 224275 |
| LN_Obturator_L | Anatomic | Lymph Node | Lymph nodes of pelvis – obturator Left | 16676 |
| LN_Obturator_R | Anatomic | Lymph Node | Lymph nodes of pelvis – obturator Right | 16676 |
| LN_Paraaortic | Anatomic | Lymph Node | Lymph nodes of abdomen- para-aortic | 223899 |
| LN_Pelvic_L | Anatomic | Lymph Node | Pelvic Lymph Nodes Left | — |
| LN_Pelvic_R | Anatomic | Lymph Node | Pelvic Lymph Nodes Right | — |
| LN_Pelvics | Anatomic | Lymph Node | Pelvic Lymph Nodes | — |
| LN_Presacral_L | Anatomic | Lymph Node | Lymph nodes of pelvis – presacral Left | 234280 |
| LN_Presacral_R | Anatomic | Lymph Node | Lymph nodes of pelvis – presacral Right | 234280 |
| Ovaries | Anatomic | Reproductive | Ovary | 7409 |
| Ovary_L | Anatomic | Reproductive | Ovary Left | 7214 |
| Ovary_R | Anatomic | Reproductive | Ovary Right | 7213 |
| Parametrium | Anatomic | Reproductive | Parametrium | 77061 |
| PenileBulb | Anatomic | Reproductive | Penile Bulb | 19614 |
| Penis | Anatomic | Reproductive | Penis | 9707 |
| Perineum | Anatomic | Perineum | Perineum | 9579 |
| Prostate | Anatomic | Gland | Prostate | 9600 |
| ProstateBed | Anatomic | Surgery | Prostate Bed | — |
| PubicSymphys | Anatomic | Bone | Pubic Symphysis | 16950 |
| PubicSymphys_L | Anatomic | Bone | Pubic bone Left | 16597 |
| PubicSymphys_R | Anatomic | Bone | Pubic bone Right | 16596 |
| Rectal_Wall | Anatomic | Rectum | Rectal Wall | 14626 |
| Rectum | Anatomic | Rectum | Large bowel – Rectum | 14544 |
| SacralPlex | Anatomic | Nerve | Sacral Plexus | 5909 |
| Sacrum | Anatomic | Bone | Sacrum | 16202 |
| Scrotum | Anatomic | Skin | Scrotum (skin & cremasteric fascia) | 18252 |
| SeminalVes | Anatomic | Gland | Seminal vesicle | 19387 |
| SeminalVes_Dist | Anatomic | Gland | Distal Seminal Vesicle | — |
| SeminalVes_Prox | Anatomic | Gland | Proximal Seminal Vesicle | — |
| Skin_Perineum | Anatomic | Skin | 20429 | |
| Sphincter_Anal | Anatomic | Bowel | Internal Anal Sphincter | 15710 |
| SpinalCord_Sac | Anatomic | Nerve | Spinal Cord Sacral | 256623 |
| Spongiosum | Anatomic | Reproductive | Penis Corpus Spongiosum | 19617 |
| Testis | Anatomic | Reproductive | Testis | 7210 |
| Testis_L | Anatomic | Reproductive | Testis Left | 7212 |
| Testis_R | Anatomic | Reproductive | Testis Right | 7211 |
| Ureter_L | Anatomic | Urinary | Ureter Left | 17888 |
| Ureter_R | Anatomic | Urinary | Ureter Right | 17887 |
| UreterDivert | Anatomic | Urinary | Urinary Divergence | — |
| Ureters | Anatomic | Urinary | Both Ureters | 264814 |
| Urethra | Anatomic | Urinary | Urethra | 19667 |
| Urethra_Prostatc | Anatomic | Urinary | Prostatic Urethra | — |
| Uterus | Anatomic | Reproductive | Uterus | 17558 |
| V_Iliac_Ext_L | Anatomic | Vein | External iliac vein Left | 18886 |
| V_Iliac_Ext_R | Anatomic | Vein | External iliac vein Right | 18885 |
| V_Iliac_Int_L | Anatomic | Vein | Internal iliac vein Left | 18810 |
| V_Iliac_Int_R | Anatomic | Vein | Internal iliac vein Right | 18809 |
| V_Iliac_L | Anatomic | Vein | Common iliac vein Right | 21387 |
| V_Iliac_R | Anatomic | Vein | Common iliac vein Left | 21388 |
| Vagina | Anatomic | Reproductive | Vagina | 19949 |
| Vagina_Surf | Anatomic | Reproductive | — | |
| VaginalCuff | Anatomic | Reproductive | Vaginal Cuff | — |
| VB_S | Anatomic | Bone | Sacral Vertebra | 12526 |
| VB_S1 | Anatomic | Bone | Sacral Vertebra S1 | 13077 |
| VB_S2 | Anatomic | Bone | Sacral Vertebra S2 | 13078 |
| VB_S3 | Anatomic | Bone | Sacral Vertebra S3 | 13079 |
| VB_S4 | Anatomic | Bone | Sacral Vertebra S4 | 13080 |
| VB_S5 | Anatomic | Bone | Sacral Vertebra S5 | 13081 |
| Vulva | Anatomic | Reproductive | Vulva | 20462 |
| Wall_Vagina | Anatomic | Reproductive | Wall of vagina | 19971 |
Cuerpo / Sistémico (Body) — 52 estructuras
| Nombre TG-263 | Tipo | Categoria | Descripción | FMAID |
|---|---|---|---|---|
| Bag_Ostomy | Non_Anatomic | Devices | Ostomy Bag | — |
| Body | Anatomic | Body | Only the body | 256135 |
| Body-PTV | Derived | Body | Body minus PTV | — |
| Bolus | Non_Anatomic | Bolus | — | |
| Bolus_xxmm | Non_Anatomic | Bolus | Bolus that is xx millimeters thick e.g. Bolus_03mm, Bolus_10mm | — |
| Bone | Anatomic | Bone | Bone | 30317 |
| BoneMarrow | Anatomic | Bone | Bone Marrow | 9608 |
| BoneMarrow_Act | Anatomic | Bone | Active Bone Marrow | — |
| Boost | Non-Anatomic | Body | Boost Volume | — |
| CTV | Target | CTV | Clinical Tumor Volume | — |
| Edema | Anatomic | Skin | Edema | — |
| E-PTV_Ev05_xxxx | Non-Anatomic | Body | All tissue excluding the 5 mm expanded PTV. Generated by subtracting the 5 mm expanded PTV receiving a dose of xxxx cGy from the external contour. | — |
| E-PTV_xxxx | Non-Anatomic | Derived | All tissue excluding the PTV. Generated by subtracting the PTV receiving a dose of xxxx cGy from the external contour. | — |
| Eval | Non-Anatomic | Body | Evaluation Structure | — |
| External | Anatomic | Body | Contour encompassing body plus other external items | — |
| GrowthPlate_L | Anatomic | Bone | — | |
| GrowthPlate_R | Anatomic | Bone | — | |
| GTV | Target | GTV | Gross Tumor Volume | — |
| IDL | Non-Anatomic | Dose | Isodose Line e.g. IDL_5000 isodose line for 50 Gy | — |
| ITV | Target | ITV | Internal Target Volume | — |
| Joint_Surface | Anatomic | Joint | — | |
| Leads | Non_Anatomic | Devices | — | |
| LN | Anatomic | Lymph Node | Lymph Node | 5034 |
| LN_L | Anatomic | Lymph Node | Lymph Node Left | — |
| LN_R | Anatomic | Lymph Node | Lymph Node Right | — |
| LN_Sclav_L | Anatomic | Lymph Node | Supraclavicular Lymph Node Left | 232719 |
| LN_Sclav_R | Anatomic | Lymph Node | Supraclavicular Lymph Node Right | 232721 |
| Markers | Non_Anatomic | Devices | — | |
| Musc | Anatomic | Muscle | Muscle | 30316 |
| Nrv_Peripheral | Anatomic | Nerve | Peripheral Nerve | — |
| Nrv_Root | Anatomic | Nerve | Nerve Root | 5981 |
| Postop | Non_Anatomic | Surgery | Post operative volume | — |
| Preop | Non_Anatomic | Surgery | Región originally occupied by the gross tumor volume | — |
| Prosthesis | Anatomic | Surgery | Prosthesis | — |
| PTV | Target | PTV | Planning Target Volume | — |
| Scar | Anatomic | Skin | Scar | — |
| Scar_Boost | Anatomic | Skin | — | |
| Skin | Anatomic | Skin | Skin | 7163 |
| Spc | Anatomic | Space | Space | — |
| SpinalCanal | Anatomic | Canal | Vertebral canal | 9680 |
| SpinalCanal_PRV | PRV | PRV | — | |
| SpinalCanal_PRVx | PRV | PRV | A PRV created with an x millimeter expansión on the spinal canal | — |
| SpinalCord | Anatomic | Nerve | Spinal Cord | 7647 |
| SpinalCord_PRV | PRV | PRV | — | |
| SpinalCord_PRVxx | PRV | PRV | A PRV created with an xx millimeter expansión on the spinal cord | — |
| Strct | Anatomic | Body | Structure | — |
| SurgicalBed | Anatomic | Surgery | — | |
| ThecalSac | Anatomic | Membrane | 83720 | |
| TumorBed | Non_Anatomic | Surgery | Tumor Bed | — |
| Valve | Anatomic | Valve | Valve | — |
| VB | Anatomic | Bone | Vertebral Body | — |
| VBs | Anatomic | Bone | Vertebral Bodies | 11945 |
Miembros (singular) (Limb) — 16 estructuras
| Nombre TG-263 | Tipo | Categoria | Descripción | FMAID |
|---|---|---|---|---|
| A_Femoral_Cflx_L | Anatomic | Artery | Circumflex Left Femoral Artery | — |
| A_Femoral_Cflx_R | Anatomic | Artery | Circumflex Right Femoral Artery | — |
| A_Femoral_L | Anatomic | Artery | Femoral Artery Left | 70250 |
| A_Femoral_R | Anatomic | Artery | Femoral Artery Right | 70249 |
| A_Humeral_Cflx_L | Anatomic | Artery | Circumflex Humeral Artery Left | — |
| A_Humeral_Cflx_R | Anatomic | Artery | Circumflex Humeral Artery Right | — |
| A_Humeral_L | Anatomic | Artery | Humeral Artery Left | — |
| A_Humeral_R | Anatomic | Artery | Humeral Artery Right | — |
| Femur_L | Anatomic | Bone | Femur Whole Left | 24475 |
| Femur_R | Anatomic | Bone | Femur Whole Right | 24474 |
| Femurs | Anatomic | Bone | Both Femurs | 9611 |
| Radius_L | Anatomic | Bone | Radius Left | 23465 |
| Radius_R | Anatomic | Bone | Radius Right | 23464 |
| Strct_Suprapatel | Anatomic | Joint | Suprapatellar Structures | — |
| Tendon | Anatomic | Tendon | 9721 | |
| Tendon_Quad | Anatomic | Tendon | 46900 |
Miembros (bilateral) (Limbs) — 17 estructuras
| Nombre TG-263 | Tipo | Categoria | Descripción | FMAID |
|---|---|---|---|---|
| Elbow | Anatomic | Joint | Elbow | 24901 |
| Elbow_L | Anatomic | Joint | Elbow Left | 24903 |
| Elbow_R | Anatomic | Joint | Elbow Right | 24902 |
| Fibula | Anatomic | Bone | Fibula | 24479 |
| Fibula_L | Anatomic | Bone | Fibula Left | 24481 |
| Fibula_R | Anatomic | Bone | Fibula Right | 24480 |
| Humerus_L | Anatomic | Bone | Humerus Left | 23131 |
| Humerus_R | Anatomic | Bone | Humerus Right | 23130 |
| Joint_Elbow | Anatomic | Joint | Elbow joint | 35289 |
| Joint_Elbow_L | Anatomic | Joint | Left Elbow joint | 35295 |
| Joint_Elbow_R | Anatomic | Joint | Right Elbow joint | 35294 |
| Joint_Glenohum | Anatomic | Joint | Glenohumeral Joint | 25912 |
| Joint_Glenohum_L | Anatomic | Joint | Glenohumeral Joint Left | 25929 |
| Joint_Glenohum_R | Anatomic | Joint | Glenohumeral Joint Right | 25927 |
| Knee | Anatomic | Joint | Knee | 24974 |
| Knee_L | Anatomic | Joint | Knee Left | 24978 |
| Knee_R | Anatomic | Joint | Knee Right | 24977 |
Integración con sistemas de planificación e inteligencia artificial
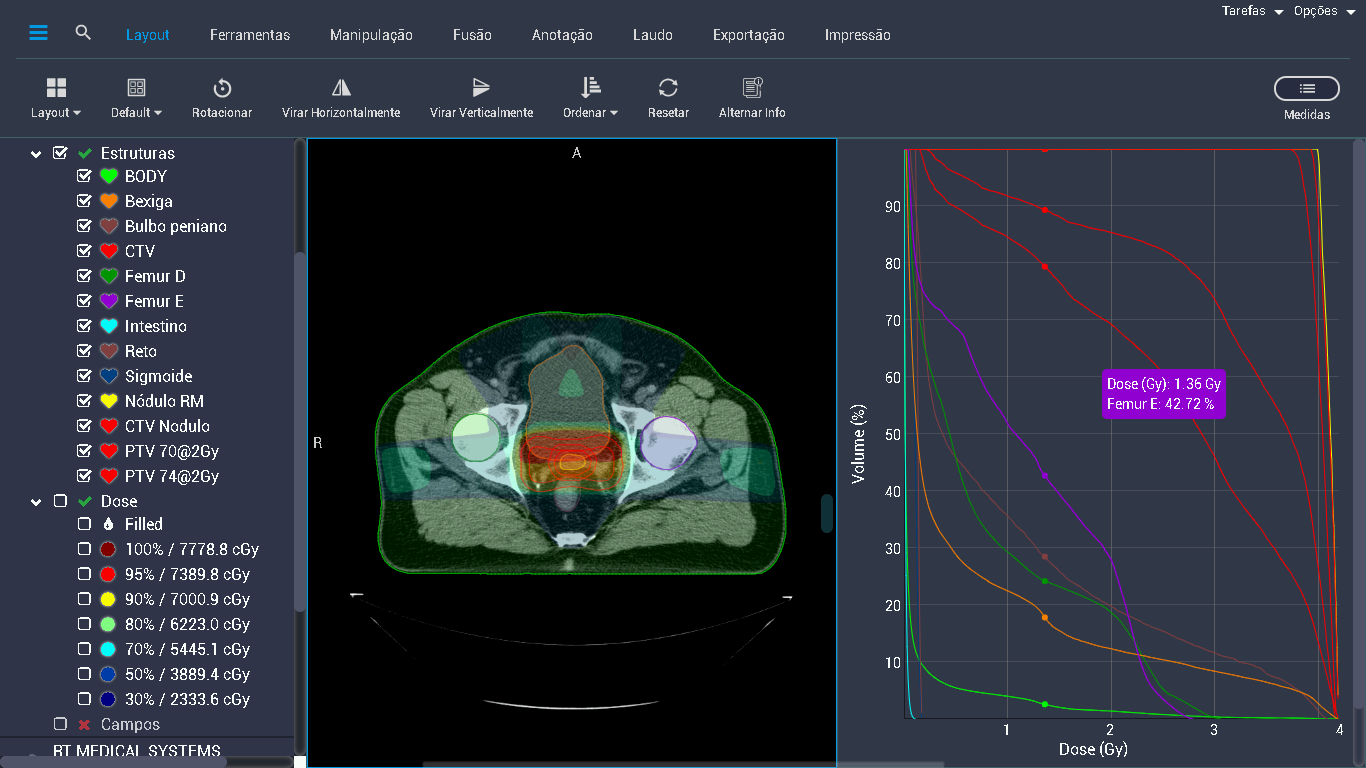
La estandarización de nomenclatura gana relevancia operacional cuando se conecta con los sistemas que consumen y producen nombres de estructuras en el día a día: sistemas de planificación de tratamiento (TPS), herramientas de auto-segmentación y plataformas de análisis de datos. El TG-263 no es un documento aislado — es una capa de interoperabilidad que permite que diferentes eslabones de la cadena se comuniquen sin mapeo manual.
Por que la nomenclatura estándar importa para la IA
Los modelos de auto-segmentación basados en deep learning dependen de tres condiciones para funcionar bien: datos de entrenamiento voluminosos, etiquetas consistentes y mapeo predecible entre la salida del modelo y las estructuras clínicas del plan de tratamiento. El TG-263 atiende directamente la segunda y tercera condiciones.
Cuando un modelo es entrenado con contornos etiquetados como Parotid_L en todas las instituciones contribuyentes, la etiqueta de salida puede ser directamente insertada en el plan sin etapa de traducción. Si cada institución usa su propio nombre, el modelo necesita un diccionario de sinónimos que crece con cada nuevo dataset incorporado — y cada entrada ausente en ese diccionario es una estructura que no sera mapeada correctamente en la clínica.
La escala del problema se hace evidente en proyectos como el TCIA (The Cancer Imaging Archive) y los AAPM Grand Challenges, donde datos de decenas de instituciones se combinan para entrenamiento y validación. Sin nomenclatura estándar, la etapa de armonización consume más tiempo que el entrenamiento del modelo. Con el TG-263 adoptado como convención de etiquetado, los datos llegan listos para uso.
Herramientas que soportan la nomenclatura TG-263
El ecosistema de radioterapia ya ofrece herramientas que reconocen, mapean o imponen nomenclatura TG-263. La lista a continuación describe las principales en tono educativo y neutro, sin jerarquía de preferencia.
AutoSeg (RT Medical Systems) es una plataforma de auto-segmentación que produce contornos con nombres TG-263 como salida estándar. La integración con RTConnect permite que los contornos generados fluyan directamente al TPS con nomenclatura conforme, eliminando la etapa manual de renombramiento. El pipeline completo — recepción de imagen, segmentación, nombramiento y entrega — respeta el estándar de punta a punta.
Limbus Contour combina deep learning con abordajes atlas-based para auto-contorno. La herramienta permite configurar templates de nomenclatura que mapean las salidas del modelo a nombres TG-263, facilitando la integración con flujos de trabajo que ya siguen el estándar.
MVision AI opera como servicio cloud de auto-contorno, recibiendo imágenes via DICOM y retornando conjuntos de estructuras segmentadas. El sistema ofrece mapeo de nombres de salida hacia convenciones TG-263, útil para servicios que adoptan el estándar y reciben contornos de diferentes proveedores.
Radformation AutoContour usa una combinación de métodos atlas y deep learning para segmentación automática. La plataforma soporta personalización de nombres de estructura, permitiendo que los servicios configuren la salida para seguir la convención TG-263 de su template institucional.
MIM Software ofrece flujos de trabajo de contorno con templates de estructura personalizables. La capacidad de definir templates con nombres TG-263 y aplicarlos a nuevos casos facilita la adopción del estándar en servicios que procesan alto volumen de pacientes.
Varian Eclipse incluye, a partir de ARIA 13.x, un Structure Dictionary que asocia nombres TG-263 a FMAIDs y sinónimos reconocidos. Cuando el físico crea una nueva estructura, el sistema sugiere el nombre estándar y permite busqueda por sinónimo. Este recurso reduce la barrera de adopción porque el profesional no necesita memorizar el catálogo completo — el sistema lo orienta durante la delineación.
Elekta Monaco soporta gestión de conjuntos de estructura y templates que pueden ser configurados con nombres TG-263. La herramienta de template permite que el servicio defina anticipadamente las estructuras esperadas para cada sitio de tratamiento, imponiendo la nomenclatura desde la creación del plan.
RaySearch RayStation ofrece capacidades de scripting via IronPython y C# que permiten construir validadores de nomenclatura. Un script puede verificar, al guardar el plan, si todos los nombres de estructura adhieren al estándar TG-263 y alertar al usuario en caso de encontrar desvios. Este enfoque transforma la nomenclatura de recomendación en regla operacional.
Impacto en Big Data e investigación multicéntrica
El valor acumulado de la estandarización aparece con más fuerza a escala. Cuando decenas o cientos de instituciones alimentan un repositorio centralizado con datos dosimétricos y de contorno — como ocurre en Learning Health Systems, registros de desenlaces y proyectos de predicción de toxicidad — la nomenclatura consistente es prerrequisito para que los datos sean utilizables sin curaduría manual intensiva.
Los proyectos que analizan la correlación entre dosis en órganos de riesgo y desenlaces clínicos (modelos NTCP, por ejemplo) necesitan agregar DVHs de miles de pacientes. Si cada institución nombra el esofago de forma diferente, el pipeline de análisis necesita una etapa de resolución de entidades que es laboriosa, propensa a errores y difícil de auditar. El TG-263 elimina esa etapa al definir Esophagus como nombre canónico, universalmente reconocido.
El mismo principio se aplica a competiciones de segmentación como los AAPM Grand Challenges y a repositorios públicos como el TCIA. La adopción del TG-263 como convención de etiquetado en estos ambientes ya esta en marcha y tiende a convertirse en requisito formal en publicaciones futuras. Los servicios que adoptan el estándar ahora posicionan sus datos para participar en estas iniciativas sin retrabajo retroactivo.
Flujo de implementación en 10 pasos
La Sección 13 del informe TG-263 define un flujo de implementación en 10 pasos diseñado para ser aplicable a cualquier servicio de radioterapia, independientemente de su escala o madurez operacional. El flujo no exige detener la operación — es un proceso incremental que puede ejecutarse en paralelo con la rutina clínica.
Paso 1: Identificar sitios de tratamiento comunes y equipo involucrado. El punto de partida es mapear cuales sitios de enfermedad el servicio trata con más frecuencia y cuales profesionales participan de la delineación, planificación y revisión para cada sitio. Este mapeo define el alcance inicial de la adopción y evita el error de intentar estandarizar todo de una vez.
Paso 2: Detallar las convenciones actuales de nomenclatura. Antes de cambiar cualquier nombre, el servicio necesita documentar lo que ya usa. Esta etapa revela la real extensión de la inconsistencia — es común que los equipos descubran variaciones que no sabian que existian. Listar los nombres actualmente en uso para las estructuras más frecuentes crea la base de comparación con el estándar TG-263.
Paso 3: Descargar la lista completa del TG-263. El material suplementario del informe, disponible en el sitio de la AAPM, contiene la planilla con las 717 estructuras y todas las 9 columnas. Esta planilla es el documento de referencia para todo el proceso.
Paso 4: Guardar y crear una copia de trabajo. El servicio debe mantener una copia intacta de la planilla original y trabajar en una versión separada. La copia de trabajo sera personalizada para la realidad del servicio; la original sirve como referencia inmutable para consultas futuras y para nuevos profesionales que necesiten entender el estándar.
Paso 5: Eliminar estructuras que el servicio no utiliza. La planilla completa contiene 717 estructuras, pero ningún servicio usa todas. Un centro especializado en cabeza y cuello puede comenzar eliminando estructuras de pelvis y abdomen que no forman parte de su práctica. Esta poda reduce el catálogo a un tamaño manejable y enfoca la atención del equipo en las estructuras que realmente importan.
Paso 6: Discutir con grupos de sitio de enfermedad y stakeholders. Cada estructura mantenida en la lista debe ser validada por los profesionales que la utilizan. Los médicos necesitan concordar que los nombres estándar son clinicamente adecuados. Los físicos necesitan confirmar que los nombres son compatibles con scripts y herramientas existentes. Los dosimetristas necesitan verificar que los nombres son prácticos en el flujo diario de delineación.
Paso 7: Identificar templates y documentos que necesitan actualización. La nomenclatura no vive solo en el TPS. Protocolos institucionales, checklists de QA, formularios de prescripción, scripts de automatización e informes de dosimetría pueden contener nombres de estructura. Todos necesitan ser revisados para reflejar el estándar adoptado.
Paso 8: Desarrollar un plan de rollout por fases. La implementación más eficaz comienza por un sitio de enfermedad (típicamente el más frecuente), valida el estándar con casos reales y solo entonces se expande a otros sitios. Cada fase incluye entrenamiento, seguimiento y ajuste antes de avanzar. Los intentos de implementar todos los sitios simultáneamente suelen resultar en adhesión parcial y eventual abandono.
Paso 9: Crear templates en el TPS con nombres estándar. Los templates de estructura en el sistema de planificación son el mecanismo de imposición más eficaz. Cuando el físico o dosimetrista abre un nuevo caso y carga el template para «cabeza y cuello», todas las estructuras ya vienen nombradas conforme al TG-263. Esto elimina la digitación manual y reduce dramáticamente la posibilidad de desvio.
Paso 10: Mantener la lista completa accesible para referencia futura. Nuevos profesionales, nuevas modalidades y nuevos sitios de enfermedad surgiran. La planilla completa debe estar disponible en un lugar conocido (red, intranet, sistema de gestión de documentos) para que cualquier persona pueda consultar el estándar cuando necesite agregar una estructura al catálogo local.
Relación con la delineación de volúmenes blanco
La nomenclatura TG-263 no existe aislada del proceso de delineación. Por el contrario: fue diseñada para integrarse directamente al flujo de trabajo de contorno, funcionando como la capa de identidad que conecta lo que el médico delinea con lo que el sistema de planificación calcula y lo que la base de datos almacena.
Cuando un radioterapeuta delinea el GTV de un tumor primario de orofaringe, el TG-263 define que esa estructura debe ser nombrada GTV_p. Si hay compromiso nodal, los ganglios linfáticos delineados como enfermedad macroscópica se convierten en GTV_n. El CTV que cubre la extensión microscópica del primario sera CTV_p, y el del nodal, CTV_n. El PTV generado a partir del CTV primario con la dosis más alta sera PTV_p_High o PTV_7000 (si la dosis es de 70 Gy). Cada nombre lleva información clínica que cualquier profesional entrenado en el estándar logra decodificar sin consultar la historia clínica.
Esta integración es particularmente valiosa en sitios de cabeza y cuello, donde el número de estructuras por plan puede superar las 40 y la distinción entre órganos de riesgo, blancos primarios y blancos nodales necesita ser inequívoca. Un plan de nasofaringe con tres niveles de dosis, múltiples GTVs y una densa red de órganos de riesgo se vuelve significativamente más legible cuando la nomenclatura sigue un estándar predecible. Lo mismo aplica a sitios como hipofaringe, cavidad oral, cavidad nasal y senos paranasales, glandulas salivales y tiroides, donde la cantidad de órganos de riesgo exige nomenclatura inequívoca.
El mismo principio se aplica a todos los sitios anatómicos. En la delineación de orofaringe, la distinción entre GTV mucoso y GTV nodal es inmediatamente visible en los nombres. En laringe, donde estructuras de cartilago como Arytenoid_L, Cricoid y Thyroid_Cart son críticas para la definición de margenes, los nombres TG-263 eliminan dudas sobre cual cartilago esta siendo referenciado.
En tratamientos de mama, la nomenclatura estándar facilita la distinción entre Breast_L (mama completa como órgano) y estructuras de planificación como zBreast_Flash. Para la irradiación nodal de mama, la nomenclatura de los niveles axilares, supraclaviculares e internos mamarios sigue la convención LN_ del TG-263. Los planes de pulmon se benefician de la claridad entre Lung_L, Lung~_L (parcial) y Lungs (bilateral), cada nombre con implicación dosimétrica distinta.
En la pelvis, la delineación de prostata usa Prostate, SeminalVes, Rectum, Bladder y Femur_L/Femur_R como órganos de riesgo estándar. Para cancer rectal, la nomenclatura de los niveles nodales sigue la convención LN_ del TG-263, facilitando la identificación de cuales cadenas ganglionares estan incluidas en el CTV. La delineación de vejiga, vulva, seminoma testicular y ginecologia definitiva y ginecologia posoperatoria sigue la misma lógica.
En escenarios como metastasis cerebrales tratadas con SRS y en la planificación de tumores benignos del SNC o tumores malignos del SNC, la nomenclatura de los volúmenes blanco con identificación por número (GTV_1, GTV_2, PTV_1) se vuelve crítica para la trazabilidad. El TG-263 permite esta numeración dentro del framework de composición de nombres.
La conexión entre nomenclatura y delineación se extiende también a técnicas especiales. En braquiterapia guiada por imagen, estructuras como Applicator, Tandem y órganos de riesgo pélvicos siguen el mismo estándar. Para esofago, linfoma, sarcoma de partes blandas, cancer gástrico, cancer de pancreas, hepatocelular y cancer anal, el TG-263 proporciona nombres estándar para las estructuras anatómicas específicas de cada sitio.
Para una visión integral de como la delineación de volúmenes blanco se integra al flujo de trabajo en radioterapia, consulte nuestra guia completa de delineación de volumen blanco, que cubre principios, técnicas y recomendaciones por sitio anatómico.
El futuro de la estandarización en radioterapia
El TG-263 representa el estado del arte en nomenclatura de estructuras para radioterapia, pero el campo continua evolucionando. Varios desarrollos en curso prometen expandir el alcance y la profundidad de la estandarización.
Integración con DICOM RT Structure Set. El estándar DICOM ya soporta el concepto de Structure Set, pero la adopción de la nomenclatura TG-263 como vocabulario controlado dentro de DICOM esta en discusión. El Supplement 196, propuesto por el DICOM Working Group 7, define un mecanismo para incluir templates de estructura directamente en el estándar DICOM, permitiendo que los sistemas interoperen no solo en el formato de los datos, sino también en la semántica de los nombres. Cuando este suplemento sea ampliamente implementado, el nombre Parotid_L en un archivo DICOM sera no solo una etiqueta, sino un identificador semántico vinculado a una ontología.
HL7 FHIR e interoperabilidad con historias clínicas. El estándar HL7 FHIR, cada vez más adoptado para intercambio de informaciones clínicas, ofrece recursos para codificación de procedimientos y hallazgos anatómicos. El puente entre TG-263 (nomenclatura de radioterapia) y FHIR (interoperabilidad en salud) pasa por el mapeo de FMAIDs y códigos SNOMED CT. Este mapeo permite que los datos de radioterapia sean integrados a la historia clínica electrónica con semántica preservada, viabilizando consultas como «cuales pacientes recibieron dosis > 50 Gy en la parotida izquierda» directamente en el sistema de información hospitalario.
Registros de modelos de IA. A medida que los modelos de auto-segmentación proliferan, surge la necesidad de registros que documenten la nomenclatura de entrenamiento de cada modelo. Si un modelo fue entrenado con etiquetas TG-263, cualquier servicio que use el estándar puede adoptarlo sin mapeo. Si fue entrenado con etiquetas propietarias, el mapeo necesita ser documentado y validado. La tendencia es que los registros de modelos incluyan la tabla de mapeo TG-263 como metadato obligatorio.
Tablas de traducción multilenguaje. El TG-263 fue publicado en ingles, pero los servicios en paises no anglofonos necesitan un mapeo entre los nombres TG-263 y los nombres locales. Tablas de traducción que asocian, por ejemplo, Brainstem a «tronco encefálico» y SpinalCord a «medula espinal» ya estan en desarrollo en varios paises. La expectativa es que la AAPM o un grupo de trabajo internacional publique tablas oficiales de correspondencia que preserven el nombre TG-263 como identificador canónico y ofrezcan traducciones como aliases de interfaz.
Sucesión del grupo de trabajo. El TG-263 original fue publicado en 2018 y cubre las estructuras anatómicas conocidas hasta esa fecha. Nuevas técnicas de tratamiento, nuevas modalidades de imagen y nuevos enfoques de delineación continuaran demandando adiciones al catálogo. El mantenimiento del estándar necesitara un grupo sucesor — ya sea vinculado a la AAPM, a la ASTRO o a una entidad conjunta — que revise periódicamente la planilla, incorpore nuevas estructuras y publique versiones actualizadas. El modelo de gobernanza de este grupo definira si el TG-263 permanece como un estándar vivo o se congela en la versión de 2018.
Conclusión
El TG-263 transformo la nomenclatura de estructuras en radioterapia de una cuestión de preferencia personal a un estándar técnico documentado, probado y adoptable. Las 717 estructuras catalogadas, los 15 principios para órganos de riesgo, los 10 principios para volúmenes blanco y la notación estandarizada de DVH forman un kit completo para cualquier servicio que desee operar con consistencia.
El impacto clínico es directo. Revisión de planes más rápida. Datos históricos utilizables. Automatización de QA confiable. Compatibilidad con modelos de auto-segmentación. Participación en estudios multicéntricos sin retrabajo. Entrenamiento de nuevos profesionales facilitado. Ninguno de estos beneficios depende de tecnologia sofisticada — depende de disciplina en la nomenclatura.
La implementación no necesita ser un proyecto de meses. El flujo de 10 pasos del propio informe muestra que comenzar por un sitio de enfermedad, crear templates en el TPS y entrenar al equipo ya produce resultados tangibles en la primera semana. La expansión a otros sitios ocurre naturalmente a medida que el equipo internaliza la lógica del estándar.
Si su servicio aun no ha adoptado el TG-263, el mejor momento para comenzar es ahora. Descargue la planilla, identifique las estructuras de su sitio de tratamiento más frecuente y cree el primer template estandarizado. RT Medical Systems ofrece herramientas como AutoSeg y RTConnect que integran la nomenclatura TG-263 directamente en el flujo clínico — desde la segmentación automática hasta la entrega del contorno en el TPS, con nombres conformes desde el origen. Si necesita soporte en este camino, nuestro equipo esta disponible para evaluar el escenario de su servicio y proponer un plan de adopción personalizado.